AI 新工具 UNAGI:解码细胞动态,为复杂疾病药物研发开新路
AI 新工具 UNAGI:解码细胞动态,为复杂疾病药物研发开新路
复杂疾病的发生发展藏着无数细胞层面的动态变化,想要精准找到治疗靶点、筛选有效药物,就需要拨开这些复杂变化的迷雾。《Nature Biomedical Engineering》发表的一项研究带来了全新的深度学习模型 UNAGI,它专为分析时间序列单细胞转录组数据而生,能精准捕捉疾病背后的细胞动态,还能实现虚拟药物筛选,为特发性肺纤维化、新冠等复杂疾病的研究和药物研发提供了强大的计算机算法工具。
UNAGI 的核心是融合图卷积层的 VAE-GAN 深度生成神经网络,这一算法架构让它能完美适配单细胞数据的高维、噪声大、分布复杂等特点,从海量数据中提取有价值的疾病信息,整体工作流程分为三个关键阶段。第一阶段,UNAGI 利用零膨胀对数正态分布处理单细胞数据,通过图卷积层挖掘细胞间的结构关系,降低测序 dropout 噪声,再结合变分自编码器(VAE)将高维细胞数据映射到低维潜空间,生成疾病相关的细胞嵌入特征,对抗判别器(GAN)则负责保证这些特征的真实性,让细胞表征更精准。
第二阶段,UNAGI 基于学习到的细胞嵌入,用 Leiden 聚类法识别细胞群,并根据细胞群的内在相似性,构建跨疾病进展阶段的时间动态图,清晰描绘细胞状态随疾病发展的转变轨迹。第三阶段,借助 iDREM 工具,从动态图中挖掘调控疾病进展的关键基因和调控因子,同时通过迭代训练,让模型不断强化对疾病特征基因的关注,让细胞表征更贴合疾病本身的特点。
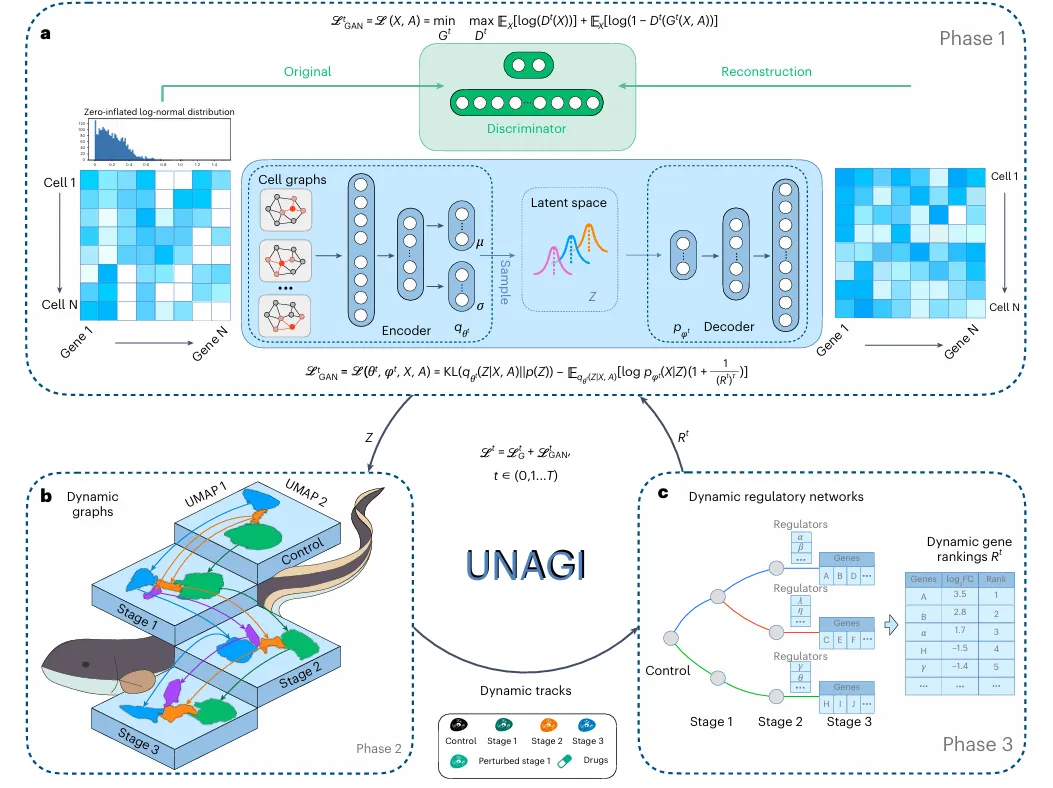
在完成疾病细胞动态解析后,UNAGI 的虚拟扰动模块成为药物研发的关键。它结合 Connectivity Map 药物数据库,通过两种方式模拟药物作用:一是直接调控药物靶基因的表达,二是基于基因互作网络,模拟基因调控的下游效应。随后通过计算扰动分数,评估药物能否让病变细胞的状态向健康细胞靠拢,分数越高,药物的潜在治疗效果越好,这一过程全程无需实验数据监督,大幅降低了药物初筛的成本和时间。
为验证算法的有效性,研究团队将 UNAGI 应用于特发性肺纤维化(IPF)研究。UNAGI 不仅精准识别出 IPF 进展过程中基质细胞群的动态变化 —— 成纤维细胞占比从不足 15% 升至 40% 以上,血管内皮细胞持续减少,还重构了成纤维细胞的基因调控网络,发现了 CTCF、EP300 等关键调控因子,以及 Netrin-1 信号通路等潜在治疗靶点。
更重要的是,UNAGI 筛选出硝苯地平(一种降压药)具有潜在抗肺纤维化作用,后续人体精密肺切片实验证实,硝苯地平能有效逆转纤维化细胞的状态,与算法预测高度一致。此外,UNAGI 还成功应用于新冠研究,解析了新冠患者外周血单核细胞的动态变化,识别出干扰素信号通路等治疗靶点,并筛选出阿洛司他丁、去羟肌苷等潜在抗新冠药物,证明了其跨疾病的通用性。
与传统单细胞分析算法相比,UNAGI 的优势十分显著。传统算法多将时间序列数据视为离散快照,无法捕捉疾病的连续动态,且缺乏疾病特异性优化;而 UNAGI 通过迭代训练策略,实现细胞嵌入学习与基因调控网络推断的信息交互,让模型不断深化对疾病的理解,同时其无监督虚拟扰动能力,无需依赖大量实验扰动数据,适配性更强。基准测试显示,UNAGI 在细胞嵌入质量、疾病标志物识别、药物筛选准确性等方面均显著优于 scVI、scGPT 等主流算法。
UNAGI 的出现,搭建了从单细胞数据到疾病机制解析、再到药物筛选的全流程算法框架,不仅为复杂疾病的细胞动态研究提供了新视角,还能大幅加速药物重定位和新靶点发现的进程。未来,这一算法还可拓展到胚胎发育、器官发生等领域,为更多生命科学研究和临床转化提供 AI 助力。
扫描下方二维码获取原文

(下载论文仅用于学术交流,如果版权保护请联系删除)
 夜雨聆风
夜雨聆风




