 2026年广东广州市普通高中毕业班综合测试(二)生物学
2026年广东广州市普通高中毕业班综合测试(二)生物学
一、单选题
1.广州海珠国家湿地公园被称为“都市果林湿地”。下列叙述错误的是()
A.建设湿地公园有利于当地野生生物的就地保护
B.公园可供观光休闲体现了生物多样性的间接价值
C.“都市果林湿地”体现了生态工程的整体原理
D.建设湿地公园能有效降低周边地区的生态足迹
2.名菜“白切鸡”以其皮爽肉滑的独特口感而闻名,其制作关键在于95℃浸煮20min、冰水冷浸15min的烹饪方式。下列叙述错误的是()
A.95℃浸煮20min具有消毒作用
B.95℃浸煮后的鸡肉易被蛋白酶水解
C.冰水冷浸可导致蛋白质肽键断裂
D.鸡肉消化后可提供多种必需氨基酸
3.“茶泡”是特定真菌侵染油茶树幼嫩组织,引起激素失衡,导致植物细胞异常增生膨大形成的囊状畸形结构。在“茶泡”形成过程中,含量出现下降的植物激素最可能是()
A.脱落酸B.生长素C.赤霉素D.细胞分裂素
4.某校以洋葱紫色鳞片叶外表皮为材料开展“探究植物细胞的吸水和失水”实验。下列叙述正确的是()
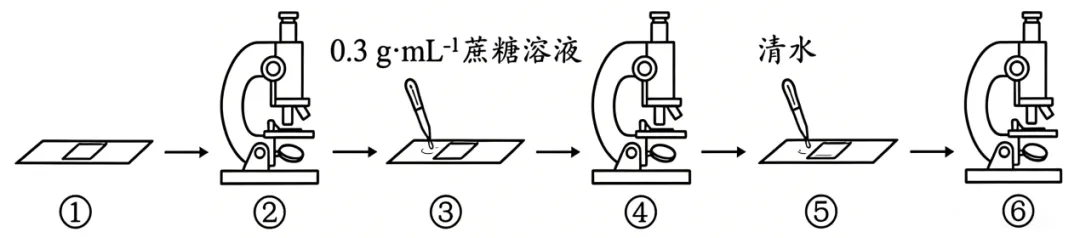
A.实验过程中需要单独设置对照组
B.完成步骤①时用手拿盖玻片放上即可
C.观察到步骤⑥液泡颜色比步骤④更深
D.步骤③—⑥过程中植物细胞吸水能力先上升后下降
5.DRP1蛋白可促进线粒体分裂,心肌细胞中线粒体过度分裂会导致其功能障碍,进而引起心肌细胞凋亡。研究发现,DDX17蛋白可抑制DRPl基因转录。下列叙述错误的是()
A.心肌细胞凋亡是基因选择性表达的结果
B.可通过抑制DRPl基因的表达减少心肌细胞凋亡
C.心肌细胞ATP合成量持续不足可诱发心力衰竭
D.特异性敲除DDX17基因可抑制心力衰竭的发展
6.部分癌细胞中的原癌基因分布在ecDNA上。ecDNA是癌细胞的染色体在细胞质内切酶的作用下,发生断裂和任意拼接后形成的一种染色体外DNA,其结构较松散且缺少着丝粒。下列说法错误的是()
A.细胞质内切酶能够使DNA上的磷酸二酯键断开引发染色体断裂
B.染色体断裂后任意拼接并产生ecDNA的过程可能会发生染色体结构和数目变异
C.ecDNA携带的基因在遗传时遵循孟德尔分离定律并且存在于细胞核中
D.癌细胞能过量表达原癌基因可能与ecDNA结构松散且易与RNA聚合酶结合有关
7.固氮菌在水稻叶片上很难大量定殖,我国科学家利用纳米涂层包裹技术较圆满地解决了此难题,显著提高了固氮菌的定殖率和粮食产量。下列有关叙述错误的是()
A.水稻吸收的氮可促进光能的利用
B.使固氮菌进入水稻叶肉细胞可提高固氮菌定殖率
C.固氮菌将氮气转化为含氮养料过程中需消耗能量
D.此技术的推广可减少化学氮肥的使用
8.科研人员发现,拟南芥可借助细胞膜上的蛋白NRT1.2运输硝酸盐并吸收Na+。在高盐胁迫条件下,SOS2通过磷酸化NRT1.2,降低其Na+转运能力。下列叙述错误的是()
A.NRT1.2可能是一种依赖硝酸盐协同运输的Na+转运蛋白
B.磷酸化修饰可能引起NRT1.2构象改变,抑制其Na+转运活性
C.长期高盐胁迫下,NRT1.2基因表达增强,可以提高植株耐盐性
D.调控SOS2和NRT1.2的相互作用以提高植物耐盐性是一种新研究思路
9.动物信号传递长期被视为“发送者主导”的过程,但越来越多研究表明,接收者能够显著影响信号表达形式,即“观众效应”。我国研究人员揭示了蜜蜂摇摆舞的“观众效应”。下列说法正确的是()
A.蜜蜂摇摆舞属于物理信息
B.蜜蜂跳摇摆舞是固定不变的单向信号
C.观众反馈会影响蜜蜂摇摆舞信息编码精度
D.观众中幼蜂比例不会影响摇摆舞的精度
10.乳酸脱氢酶(LDHA)能催化丙酮酸与NADH反应生成乳酸。科研人员检测了正常与睡眠剥夺条件下,小鼠不同组织中LDHA的mRNA表达量,结果如图所示。下列叙述错误的是()
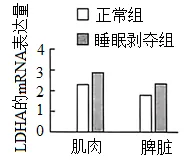
A.缺氧条件下,LDHA催化丙酮酸生成乳酸的过程不产生ATP
B.若氧气充足,丙酮酸主要进入线粒体被氧化分解
C.长期睡眠不足可能导致肌肉中的乳酸含量升高,引起肌肉酸痛
D.睡眠剥夺后脾脏中LDHA表达量上升,说明熬夜直接抑制免疫功能
11.光伏电站建设形成了板前、板下、板后、板间等不同微生境。研究人员对半干旱矿区塌陷区和非塌陷区的板前、板下、板后、板间等微生境植物群落开展调查,发现板前植物群落多样性、稳定性和植株密度均显著高于非塌陷对照区,而板下微生境则呈现相反趋势。下列叙述错误的是()
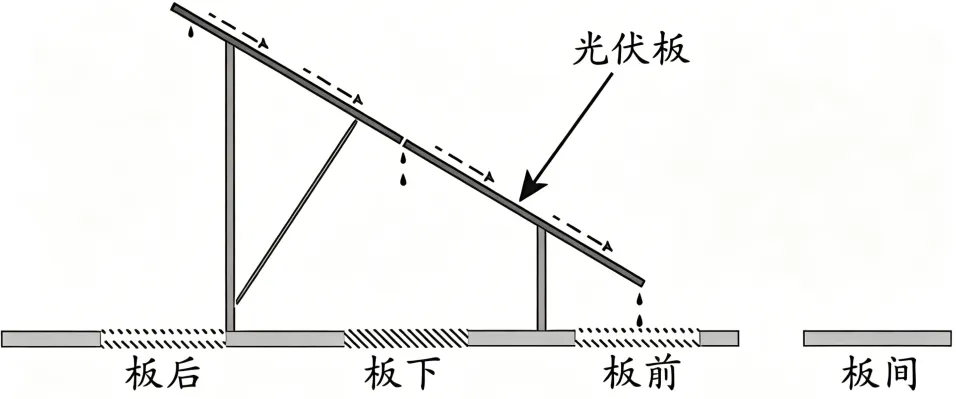
A.光伏电站建设可以影响群落演替的方向和速度
B.建议在板间播撒本地耐阴植物种子加速矿区生态恢复
C.不同微生境群落结构差异体现了群落内物种的生态位分化
D.板前雨水汇集促进植被恢复,提高了该生态系统的稳定性
12.羟基四氢嘧啶可用作生物大分子稳定剂,开发高效生产工程菌株成为研究重点。不同质粒在一个细胞中的数量(拷贝数)有差异。研究人员利用低拷贝质粒p1、中拷贝质粒p2、高拷贝质粒p3构建含ectD基因的重组质粒,在大肠杆菌中表达并进行摇瓶发酵,结果如图所示。下列叙述错误的是()
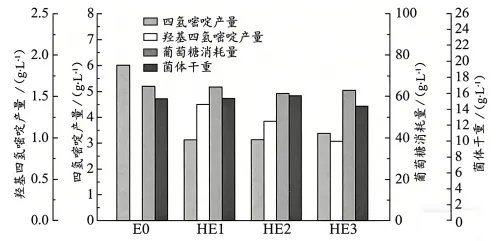
注:HE1、HE2、HE3分别为转入p1、p2、p3重组质粒的菌株,E0为原始菌株。
A.发酵过程中微生物数量和代谢物浓度变化均为重要检测指标
B.据结果推测ectD基因的表达产物可以促进羟基四氢嘧啶的产生
C.HE3可能消耗更多的葡萄糖用于合成羟基四氢嘧啶
D.在该实验基础上,筛选、分离高效菌株可以使用平板划线法
13.CO2与C5反应固定为C3的碳同化途径,被称为C3途径;CAM途径是指在夜晚捕获CO2转变成苹果酸储存在液泡中,白天气孔关闭,苹果酸脱羧释放CO2用于卡尔文循环的碳同化途径。为研究流苏石斛和美花石斛的碳同化途径类型,科研人员测量了不同水分条件下二者的气孔开度和有机酸含量,如下表所示。下列说法错误的是()
种名 | 处理 | 气孔开放率/% | 有机酸含量/mg·g-1 | ||
白天 | 夜间 | 清晨 | 傍晚 | ||
流苏石斛 | 对照 | 92.21 | 17.13 | 0.80 | 0.78 |
干旱 | 69.8 | 17.26 | 0.85 | 0.83 | |
美花石斛 | 对照 | 33.33 | 98.00 | 2.01 | 1.21 |
干旱 | 20.56 | 91.11 | 2.82 | 1.44 |
A.美花石斛为CAM植物
B.美花石斛夜间细胞液的pH较白天低
C.流苏石斛比美花石斛更能适应干旱胁迫的环境
D.干旱导致流苏石斛光合速率下降的原因是气孔开度降低
14.研究发现,肠道中的2型天然淋巴细胞(ILC2)在禁食状态下会迁移到胰腺,经过相关生理反应后,最终维持血糖平衡。下列叙述错误的是()

A.饥饿状态下,小肠交感神经兴奋性增强,肝糖原水解为葡萄糖速度加快
B.当兴奋传至交感神经末梢时,突触前膜内侧由负电位变为正电位
C.ILC2从小肠迁移到胰腺的过程可能依赖于体液运输
D.胰高血糖素的靶细胞有肝脏细胞、脂肪细胞和肌肉细胞等
15.研究人员为研究某一品种矮脚鸡(2n=78)的遗传特性,对该矮脚鸡和正常体型鸡(正常鸡)进行全基因组测序,发现矮脚鸡7号染色体片段缺失导致纯合子致死。同时研究人员进行如下实验:①将矮脚鸡自由交配,仅考虑矮脚性状,子代正常鸡:矮脚鸡=1:2。②芦花对非芦花为显性,由位于性染色体上的一对等位基因控制。由于矮脚芦花鸡产蛋量高但产肉率低,研究人员将与高产肉率相关的一个MSTN基因(基因M)转入鸡的受精卵中,获得高产肉率的两个类型1、2(插入位置不考虑性染色体)。③分别将类型1、类型2中雌雄鸡自由交配,子代表型及比例如下表:
类型 | 子代表型及比例 |
1 | 子代全为高产肉率鸡 |
2 | 高产肉率:低产肉率=3:1 |
下列叙述错误的是()
A.对矮脚鸡进行全基因组测序需要测40条染色体的DNA序列
B.实验①结果推测可知矮脚鸡对正常鸡为显性
C.根据有无芦花可辨别类型1中所产雏鸡为高产肉率的矮脚鸡
D.类型2中M基因插入的是非7号染色体上
16.为探究猪流行性腹泻病毒蛋白Nsp15是否与宿主蛋白SLC25a3结合,研究人员构建两种重组质粒分别表达融合蛋白Flag-Nsp15和Myc-SLC25a3,转化后获得三组细胞(①、②、③)。利用抗Flag抗体分别收集各组中能与之结合的蛋白,再分别用抗Flag、抗Myc的单克隆抗体检测,同时取各组细胞总蛋白进行相同检测,结果如图所示。下列分析正确的是()
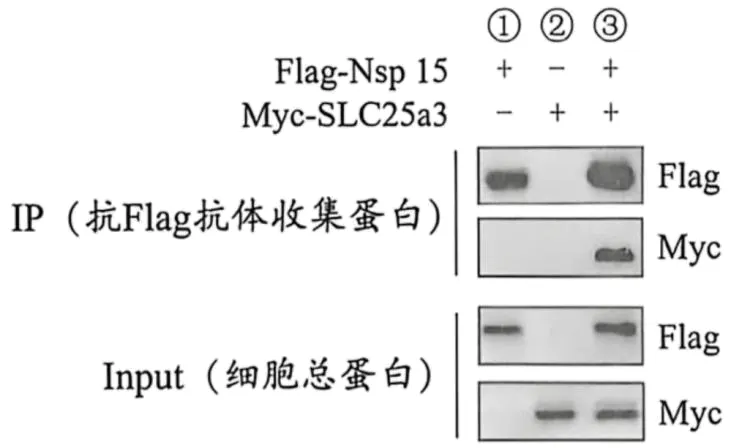
A.制备抗Flag单克隆抗体时需在已免疫动物体内分离得到记忆B细胞作为材料
B.若使用抗Myc抗体收集蛋白,则①组中同样会出现Flag条带
C.②组IP产物中无Myc条带,说明细胞内不表达SLC25a3蛋白
D.③组IP产物中有Myc条带,表明Nsp15能与SLC25a3结合
二、解答题
17.酸性土壤中铝(Al3+)毒害与磷(P)缺乏是限制水稻产量的重要因素。科学家以耐铝菌株红球菌(R)和铜绿假单胞菌(P)构建合成群落(RP)。随后将水稻种植于铝胁迫的酸性土壤(Al)和接种RP的铝胁迫的酸性土壤(Al+RP)中,探究RP对酸性土壤铝胁迫中水稻生长的影响。结果如图。
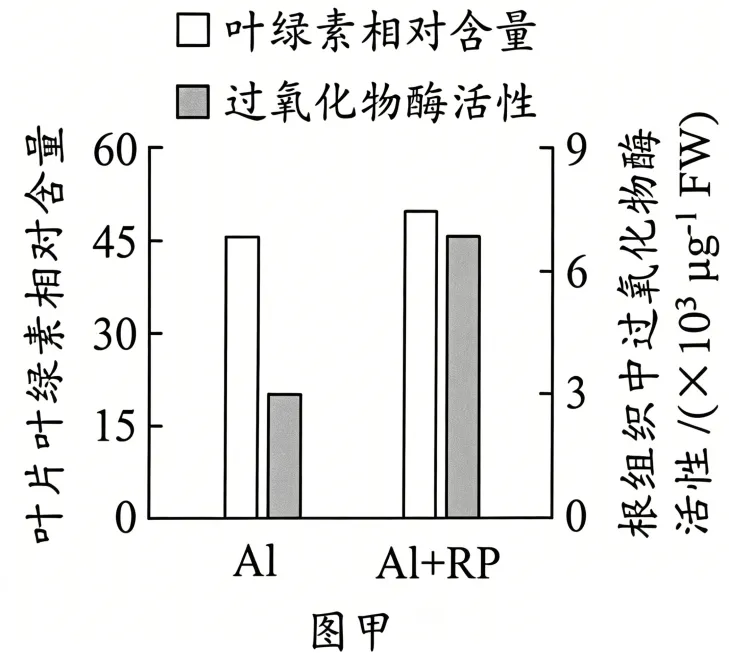
回答下列问题:
(1)可溶性Al3+会引发自由基积累,自由基攻击_______,导致根部细胞吸收的磷较少。
(2)研究发现,接种RP可以提高酸性土壤区水稻的产量。据图甲分析,可能的原因是_______
(3)在铝胁迫的酸性土壤中接种RP后,水稻更多的根向土壤表层(0-4cm)生长。由图乙可知,接种RP可以_______,从而改善水稻根系的生长环境。
(4)进一步研究发现铝胁迫的酸性土壤中接种RP利于招募溶磷菌,将不可利用的有机磷转化成无机磷,缓解铝胁迫的酸性土壤的磷缺乏胁迫。对两组水稻根细胞中相关基因的相对表达量、水稻根系分泌的葡萄糖进行测定,结果如下。
组别 | OsPht1;2基因相对表达量 | 水稻根系分泌的葡萄糖相对值/×105 |
Al | 12.5 | 2.3 |
Al+RP | 33.4 | 26.5 |
注:OsPht1;2基因表达产物可促进磷酸盐的运输。
推测接种RP可缓解铝胁迫的酸性土壤中水稻磷缺乏的原因是_______。从水稻和根际耐铝菌株的种间关系推测,根际耐铝菌株和水稻之间建立了长效的_______调节机制。
18.海洋热浪是指某海域异常增温,并持续5天或以上的现象。海洋热浪不仅影响浮游植物的总量,更会重塑其群落结构,对海洋生态系统产生深远的影响。研究人员探究海洋热浪对海洋生物的影响,结果如图。
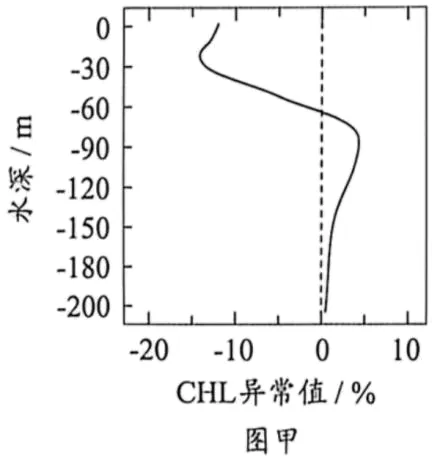
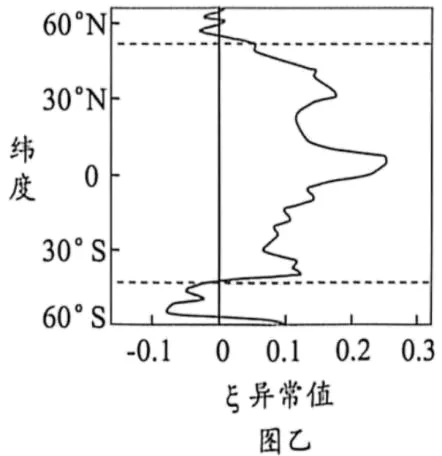
注:CHL异常值指观测到的叶绿素浓度与该海域长期平均叶绿素浓度的偏差,正值表示海水叶绿素浓度高于常年平均,负值反之注:ξ异常值较低表明海洋热浪影响下较大尺寸的浮游植物占比较高,ξ异常值较高反之。
(1)光照、温度和盐分等____因素均会影响海洋浮游生物数量。海洋热浪通过直接影响浮游植物的____等种群数量特征,进而影响其种群密度。
(2)高纬度地区浮游植物生长主要受光照限制,海水的叶绿素浓度(CHL)越高,通常表示水体中浮游植物生长繁殖越旺盛。海洋热浪期间,测得某高纬度海域不同水深的CHL异常值如图甲,推测海洋热浪使该海域60-150m水层的CHL异常值升高的主要原因是____。
(3)浮游植物是海洋初级生产力的主要贡献者,直接影响海洋生态系统的能量流动和碳循环。浮游植物按细胞大小可分为P级(<2μm)、N级(2-20μm)和M级(>20μm)。
①中低纬度地区海域,浮游植物生长主要受营养限制,海洋热浪会加剧中低纬度营养限制。科学家调查了全球不同纬度海域的浮游植物大小,其浮游植物ξ异常值如图乙。结果表明,海洋热浪使中低纬度地区海域群落中浮游植物细胞大小趋向于____(填“较大”或“较小”)尺寸,其意义主要是____(从物质运输效率的角度分析)。
②海洋热浪导致CHL降低,营养限制加剧,浮游植物大小发生变化,进而通过食物网产生级联效应。结合下表,从能量流动的角度分析,海洋热浪造成中低纬度渔业资源总量减少的原因是____。
浮游动物大小 | 主要摄食浮游植物细胞大小范围 | 定位 |
中型浮游动物 | 5-50μm | 小型鱼类和幼鱼的主要食物来源 |
微型浮游动物 | <5μm | 需被其他动物捕食才能传递给小型鱼类和幼鱼 |
三、实验题
19.皮肤黑色素细胞癌变可形成黑色素瘤,恶性程度高,约一半的黑色素瘤患者对免疫治疗无应答。黑色素体是黑色素瘤细胞特有的细胞外囊泡,将黑色素运输至邻近细胞。回答下列问题。
(1)免疫细胞之间可以通过释放信号分子、____等方式进行信息交流,参与免疫过程。
(2)CD8+T细胞是一种细胞毒性T细胞,临床样本分析发现,免疫治疗效果较差的患者中,携带黑色素的CD8+T细胞比例显著更高,推测____。为进一步验证这一推测,研究者从患者组织样本中分离出黑色素体及黑色素瘤,并与CD8+T细胞共同培养,结果如图。
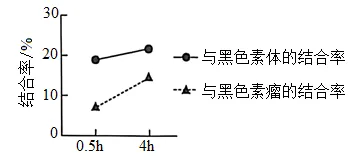
研究人员认为黑色素体-CD8+T细胞相互作用比CD8+T细胞-黑色素瘤相互作用更高效,依据是____。
(3)为探究黑色素体的功能,以小鼠黑色素瘤模型为材料,分组进行下表所示处理。
组别 | 实验处理 | 实验现象 |
A | 小鼠黑色素瘤模型+DMSO | 变化不明显 |
B | 小鼠黑色素瘤模型+曲酸 | 肿瘤生长减缓,瘤内CD8+T细胞增加 |
注:曲酸:酪氨酸酶抑制剂,不直接影响黑色素瘤生长或CD8+T细胞存活;DMSO:溶剂对照;
①据A组和B组实验结果推测,曲酸通过____阻断黑色素瘤生长。
②若想证明曲酸的抗肿瘤效果依赖于CD8+T细胞,应在上述实验基础上增设以下实验组别:小鼠黑色素瘤模型+DMSO+IgG;____(除了上述材料外,还提供以下材料:抗CD8+T细胞抗体;对照试剂IgG)
(4)蛋白质组学等分析发现,与普通胞外囊泡相比,黑色素体携带强效的MHC-肿瘤抗原。同时通过单细胞TCR(受体)测序发现,与黑色素体结合的CD8+T细胞和与黑色素瘤细胞结合的CD8+T细胞有大量相同的TCR。请根据上述研究结果描述黑色素瘤免疫逃逸的机制____。
四、解答题
20.猕猴桃是雌雄异株的二倍体生物。其红心性状由三对位于常染色体上的独立遗传的等位基因共同调控:MYB(用A表示)与HLH(用B表示)两个基因的表达产物需形成异源二聚体后,才能激活ANS基因(用E表示)的转录;ANS编码花青素合成酶,催化花青素合成形成红心。某科研团队用纯合非红心植株甲与纯合非红心植株乙杂交,F1均为红心,随机交配得到的F2植株中红心:非红心=9:7。回答下列问题:
(1)植株甲的基因型是______________。
(2)研究人员发现,植株乙的ANS基因未发生突变。为进一步确定其突变基因,研究人员利用一株MYB基因突变体(A+ABBEE),A+对A为显性,且A+基因编码的蛋白无需与HLH蛋白结合,即可单独激活ANS转录。研究人员将该突变体与植株乙杂交得F1,F1随机交配,统计F2的表型及比例。若F2表型及比例为______________,则为植株乙A基因发生隐性纯合突变;若F2表型及比例为红心:非红心=55:9,则为植株乙B基因发生隐性纯合突变。
(3)红心猕猴桃的边缘果肉呈现绿色,可能与ARF、F-box1蛋白在边缘果肉的含量高有关。为研究其作用机制,科学家设计了荧光素酶互补实验:将目标蛋白分别带上NLuc和CLuc片段(不影响蛋白质空间结构),如果目标蛋白能相互结合,则NLuc和CLuc片段会组装成完整荧光素酶,从而触发荧光。实验结果如下。
组别 | 实验处理 | 荧光强度 |
1 | MYBN+HLHC | +++ |
2 | MYBN+HLHC+ARF | - |
3 | MYBN+HLHC+F-box1 | + |
4 | MYBN+ARFC | ++ |
5 | MYBN+C+F-boxl | - |
注:蛋白质右上角的N表示该蛋白连接了NLuc片段,C表示该蛋白连接了CLuc片段。
根据实验结果,推测ARF在边缘果肉含量高导致边缘果肉呈现绿色的原因是______________。有人根据第5组的实验结果推断,F-box1可以促进MYB蛋白降解,从而抑制果肉转红。请补充一组对照实验,使结论更加严谨______________。
(4)基于以上研究,提出一种能获得全红肉猕猴桃新品种的思路:______________。
五、实验题
21. 插入突变是基于农杆菌Ti质粒的遗传学技术,通过将农杆菌Ti质粒上的T-DNA片段随机插入受体生物,破坏基因结构或影响其表达,是研究植物基因功能的重要手段。土壤镉(Cd)污染严重危害植物的生长发育。研究人员通过构建Cd敏感的T-DNA插入突变体拟南芥(S)进行植物耐Cd分子机制的研究。回答下列问题:
插入突变是基于农杆菌Ti质粒的遗传学技术,通过将农杆菌Ti质粒上的T-DNA片段随机插入受体生物,破坏基因结构或影响其表达,是研究植物基因功能的重要手段。土壤镉(Cd)污染严重危害植物的生长发育。研究人员通过构建Cd敏感的T-DNA插入突变体拟南芥(S)进行植物耐Cd分子机制的研究。回答下列问题:
(1)构建拟南芥突变体S过程中,Ti质粒的T-DNA可随机整合至拟南芥的______________中,筛选后的细胞需经植物组织培养成为突变体植株。
(2)提取突变体S的DNA,测序可确定发生突变的基因为SCL14基因。研究人员欲构建突变体S的回补株系进一步验证:
①利用Ti质粒和SCL14基因(如图)构建基因表达载体时,需用PCR技术对SCL14基因进行扩增,为保证该基因能以正确方向连入T-DNA,根据图中信息写出SCL14基因上游引物的碱基序列______________(从5′端到3′端,只写出前8个碱基即可)。

②将重组质粒成功导入农杆菌后配成细菌悬液,突变体S的花序直接浸入细菌悬液一段时间,继续培养植株获得T0种子。将T0种子平铺至含______________(填抗生素)固体培养基上培养,筛选后移栽至营养土生长,自交得T1种子。
③将若干单株收获的T1种子平铺至含相同抗生素的培养基中,选择分离比为3(有抗性):1(无抗性)的植株继续种植、自交以最后获得纯合株系。优先选择分离比为3:1而非15:1或其他比例的植株的目的是______________。
(3)实验证明,SCL14基因的缺失是突变体S对Cd胁迫敏感的原因。另有研究表明TGA3基因缺失导致突变体T对Cd胁迫敏感。若正常和Cd胁迫条件下,突变体S中TGA3表达量无明显差异,且______________,则表明SCL14蛋白与TGA3蛋白可能独立调控拟南芥对Cd的耐受性。
(4)为进一步探究SCL14调控拟南芥耐Cd的分子机制,研究人员对Cd胁迫下WT和突变体S特定细胞的总mRNA进行提取和测序分析,目的是______________。
《2026年广东广州市普通高中毕业班综合测试(二)生物学》参考答案
题号 | 1 | 2 | 3 | 4 | 5 | 6 | 7 | 8 | 9 | 10 |
答案 | B | C | A | D | D | C | B | C | C | D |
题号 | 11 | 12 | 13 | 14 | 15 | 16 | ||||
答案 | B | C | C | D | C | D |
1.B
【详解】A、就地保护是指在原地对被保护的生态系统或物种建立保护区域,建设湿地公园属于在原生环境中保护野生生物,属于就地保护措施,A正确;
B、生物多样性的间接价值是指调节生态系统功能的生态价值,观光休闲属于旅游观赏类的直接价值,B错误;
C、生态工程的整体原理要求生态建设兼顾自然、经济、社会三方面效益,“都市果林湿地”既发挥生态保护功能,又适配城市发展、居民生活需求,体现了整体原理,C正确;
D、生态足迹是维持人口生存所需的生产资源、吸纳废物的生态用地面积,湿地公园可自主净化污染物、提供生态服务,能降低周边地区的生态足迹,D正确。
2.C
【详解】A、95℃属于高温条件,高温可使微生物的蛋白质发生变性失活,起到消毒作用,A正确;
B、95℃浸煮会使鸡肉中的蛋白质空间结构被破坏,结构变得伸展松散,更易被蛋白酶结合水解,B正确;
C、冰水冷浸属于低温处理,低温仅会抑制蛋白质的活性,不会破坏蛋白质的空间结构,更不会使肽键断裂,肽键断裂需要蛋白酶催化或强酸强碱等剧烈条件,C错误;
D、鸡肉的蛋白质含有人体无法自主合成、需要从食物中获取的多种必需氨基酸,消化分解后可被人体吸收利用,D正确。
3.A
【详解】A、脱落酸的核心生理作用是抑制细胞分裂,促进器官衰老和脱落,茶泡形成需要细胞持续分裂、伸长生长,因此抑制细胞分裂的脱落酸含量最可能下降,A正确;
B、生长素可促进细胞伸长,是茶泡细胞膨大所需的激素,其含量大概率升高,B错误;
C、赤霉素可促进细胞伸长和细胞分裂,利于茶泡的增生膨大,其含量大概率升高,C错误;
D、细胞分裂素可促进细胞分裂,是茶泡细胞异常增生所需的激素,其含量大概率升高,D错误。
4.D
【详解】A、在“探究植物细胞的吸水和失水”实验中,实验过程中自身前后形成对照,不需要单独设置对照组,A错误;
B、完成步骤①(制作临时装片)时,应用镊子夹起盖玻片,让它的一侧先接触载玻片上的液滴,然后缓缓放平,而不能用手拿盖玻片放上,B错误;
C、步骤④是细胞发生质壁分离后的状态,步骤⑥是细胞发生质壁分离复原后的状态。由于质壁分离复原时细胞吸水,液泡内细胞液浓度降低,所以观察到步骤⑥液泡颜色比步骤④更浅,C错误;
D、步骤③ - ⑥过程中,细胞先发生质壁分离(细胞失水,细胞液浓度增大,吸水能力上升),后发生质壁分离复原(细胞吸水,细胞液浓度减小,吸水能力下降),即植物细胞吸水能力先上升后下降,D正确。
5.D
【详解】A、细胞凋亡是由基因决定的细胞程序性死亡过程,本质是基因的选择性表达,A正确;
B、DRP1蛋白会促进线粒体过度分裂进而引发心肌细胞凋亡,抑制DRP1基因的表达可减少DRP1蛋白合成,减少线粒体过度分裂,从而减少心肌细胞凋亡,B正确;
C、线粒体是有氧呼吸的主要场所,是细胞合成ATP的主要结构,心肌细胞收缩需要消耗大量ATP,若ATP合成量持续不足会导致心肌功能障碍,诱发心力衰竭,C正确;
D、DDX17蛋白可抑制DRP1基因转录,特异性敲除DDX17基因后,DRP1基因的表达不受抑制,DRP1蛋白含量升高,会促进线粒体过度分裂,加剧心肌细胞凋亡,会促进心力衰竭的发展,D错误。
6.C
【详解】A、DNA的脱氧核苷酸链的基本骨架通过磷酸二酯键连接形成,细胞质内切酶切割DNA会断裂磷酸二酯键,进而引发染色体断裂,A正确;
B、染色体断裂后任意拼接可引发染色体片段的缺失、重复、易位、倒位等结构变异,若断裂片段未接回原染色体形成ecDNA,也存在引发染色体数目变异的可能性,B正确;
C、孟德尔分离定律只适用于进行有性生殖的真核生物、位于细胞核内染色体上的等位基因的遗传。ecDNA是染色体外DNA,缺少着丝粒,无法在细胞分裂时随同源染色体均等分离,因此其上携带的基因遗传时不遵循孟德尔分离定律,C错误;
D、ecDNA结构松散,更易解旋暴露转录模板链,便于RNA聚合酶结合启动转录过程,因此其携带的原癌基因表达量更高,可能导致癌细胞中原癌基因过量表达,D正确。
7.B
【详解】A、氮是叶绿素、光合酶、ATP、NADPH等光合作用相关物质的组成元素,水稻吸收的氮可用于合成上述物质,进而促进光能的吸收、转化与利用,A正确;
B、题干明确固氮菌是在水稻叶片表面定殖,并非进入叶肉细胞;且固氮菌进入叶肉细胞后会受到植物细胞防御机制的抑制,无法正常生存繁殖,不能提高定殖率,B错误;
C、固氮菌将氮气转化为含氮养料的生物固氮过程需要固氮酶催化,消耗ATP提供的能量,C正确;
D、该技术提高了固氮菌的定殖率,固氮菌固定的氮素可直接供给水稻生长利用,因此可减少化学氮肥的使用,D正确。
8.C
【详解】A、题干明确说明NRT1.2可同时运输硝酸盐和吸收Na+,说明其可能是依赖硝酸盐协同运输的Na+转运蛋白,A正确;
B、蛋白质的磷酸化修饰会改变蛋白质的空间构象,题干提到磷酸化后NRT1.2的Na+转运能力降低,说明该修饰抑制了其Na+转运活性,B正确;
C、NRT1.2的作用是吸收Na+,若长期高盐胁迫下NRT1.2基因表达增强,会导致植株吸收更多Na+,加重细胞盐胁迫损伤,降低植株耐盐性,C错误;
D、SOS2磷酸化NRT1.2可降低Na+转运能力,减少Na+进入细胞,因此调控二者的相互作用可以作为提高植物耐盐性的研究思路,D正确。
9.C
【详解】A、蜜蜂摇摆舞是通过特殊的行为动作传递信息,属于行为信息,并非物理信息,A错误;
B、根据题干“观众效应”可知,接收者能够影响信号表达形式,因此蜜蜂摇摆舞不是固定不变的单向信号,B错误;
C、题干明确接收者可显著影响信号表达形式,观众属于信号接收者,因此观众的反馈会影响蜜蜂摇摆舞的信息编码精度,C正确;
D、幼蜂属于观众(接收者)的组成部分,其比例变化会改变接收者的整体反馈,因此会影响摇摆舞的精度,D错误。
10.D
【详解】A、缺氧条件下,细胞进行无氧呼吸,LDHA催化丙酮酸生成乳酸的过程属于无氧呼吸的第二阶段,不产生ATP,A正确;
B、若氧气充足,细胞进行有氧呼吸,丙酮酸主要进入线粒体被氧化分解为CO2和H2O,B正确;
C、由图可知,睡眠剥夺组小鼠肌肉中 LDHA 的 mRNA 表达量升高,LDHA 可催化丙酮酸生成乳酸,因此长期睡眠不足,会影响肌肉细胞的有氧呼吸,导致肌肉细胞进行无氧呼吸增强,LDHA催化丙酮酸生成乳酸的过程增强,可能导致肌肉中的乳酸含量升高,引起肌肉酸痛,C正确;
D、睡眠剥夺后脾脏中LDHA表达量上升,只能说明脾脏细胞无氧呼吸可能增强,但不能说明熬夜直接抑制免疫功能,D错误。
11.B
【详解】A、光伏电站建设形成了板前、板下、板后、板间等不同微生境,改变了群落的环境条件,从而影响了群落演替的方向和速度,A正确;
B、由图可知板间光照条件相对较好,应播撒本地耐阳植物种子加速矿区生态恢复,而不是耐阴植物种子,B错误;
C、不同微生境的群落结构差异,是不同物种利用资源、适应环境的结果,体现了群落内物种的生态位分化,C正确;
D、板前是雨水汇集区,水分条件更优越,促进了植被恢复,植物群落多样性、稳定性均显著提高,因此生态系统的稳定性增强,D正确。
12.C
【详解】A、发酵过程中,微生物的生长状态(如菌体数量 / 干重)和代谢产物浓度(如目标产物、底物消耗)都是衡量发酵效果的重要指标,A正确;
B、对比E0(原始菌株)和HE1/HE2/HE3(转入ectD基因的菌株)的羟基四氢嘧啶产量: E0几乎不产羟基四氢嘧啶转入ectD基因的菌株均有羟基四氢嘧啶生成,且产量随质粒拷贝数变化 说明ectD基因的表达产物可以促进羟基四氢嘧啶的产生,B正确;
C、从图中数据看: HE1/HE2/HE3的葡萄糖消耗量相近,其中HE3的羟基四氢嘧啶产量低于HE1/HE2,说明它消耗葡萄糖合成羟基四氢嘧啶的效率低,并非消耗更多葡萄糖用于合成该产物,C错误;
D、平板划线法是微生物分离纯化的常用方法,可用于从混合菌群中筛选、分离高效菌株,D正确。
13.C
【详解】A、美花石斛夜间气孔开放率远高于白天,且清晨有机酸含量显著高于傍晚,符合CAM植物夜间吸收CO₂合成苹果酸储存、白天苹果酸分解释放CO₂用于光合作用的特征,属于CAM植物,A正确;
B、美花石斛夜间合成苹果酸储存于液泡中,细胞液酸性较强,pH较低;白天苹果酸脱羧分解,酸性减弱,pH升高,因此夜间细胞液的pH较白天低,B正确;
C、美花石斛为CAM植物,干旱条件下白天气孔开放率低,可减少水分散失,同时可利用夜间储存的CO₂进行光合作用;流苏石斛为C3植物,干旱时白天仍保持较高的气孔开放率,水分散失更多,因此美花石斛比流苏石斛更能适应干旱胁迫环境,C错误;
D、流苏石斛为C3植物,依赖白天开放气孔吸收CO₂进行光合作用,干旱条件下气孔开度降低,CO₂供应不足,导致光合速率下降,D正确。
14.D
【详解】A、饥饿状态下血糖浓度偏低,小肠交感神经兴奋性增强,最终促进胰高血糖素分泌,胰高血糖素可促进肝糖原水解为葡萄糖,因此肝糖原水解为葡萄糖的速度加快,A正确;
B、静息状态下神经纤维膜电位为外正内负,当兴奋传至交感神经末梢时,会产生动作电位,膜电位变为外负内正,因此突触前膜内侧由负电位变为正电位,B正确;
C、细胞在体内不同组织器官间的迁移需要借助血液、组织液等体液运输,因此ILC2从小肠迁移到胰腺的过程可能依赖于体液运输,C正确;
D、胰高血糖素的作用是促进肝糖原分解、脂肪等非糖物质转化为葡萄糖以升高血糖,肌糖原不能水解为葡萄糖补充血糖,因此肌肉细胞不是胰高血糖素的靶细胞,D错误。
15.C
【详解】A、鸡为ZW型性别决定,体细胞含38对常染色体和1对异型性染色体(Z、W),全基因组测序需测38条常染色体+Z染色体+W染色体,共40条染色体的DNA序列,A正确;
B、矮脚鸡自由交配,子代出现性状分离,产生正常鸡新性状,说明矮脚对正常鸡为显性,且子代正常:矮脚=1:2,符合显性纯合致死的分离比例,B正确;
C、芦花/非芦花基因位于性染色体上,高产肉率基因、矮脚基因均位于常染色体,且与芦花基因不存在连锁关系,性状遗传互不关联,无法通过有无芦花辨别雏鸡是否为高产肉率矮脚鸡,C错误;
D、若M基因插入7号染色体,会与7号染色体上控制矮脚的基因连锁,受7号片段纯合致死效应影响,类型2自由交配子代高产:低产不会出现3:1的典型杂合子自交分离比,因此M基因插入非7号染色体,D正确。
16.D
【详解】A、制备单克隆抗体时,需要从已免疫动物体内分离得到能产生抗体的浆细胞(效应B细胞),不是记忆B细胞,A错误;
B、①组仅表达Flag-Nsp15,不表达Myc-SLC25a3,若用抗Myc抗体收集蛋白,无法捕获到Flag-Nsp15,不会出现Flag条带,B错误;
C、从Input(总蛋白)结果可以看出,②组总蛋白有Myc条带,说明细胞内正常表达SLC25a3蛋白;IP产物无Myc条带是因为②组本身不表达Flag-Nsp15,无法被抗Flag抗体捕获,C错误;
D、③组用抗Flag抗体收集蛋白时,沉淀中检测到Myc条带,说明Flag-Nsp15被捕获时,Myc-SLC25a3也一同被拉下来,证明Nsp15能与SLC25a3结合,D正确。
17.(1)细胞膜/磷脂/载体蛋白
(2)可以提高叶绿素相对含量,促进水稻光合作用)提高过氧化物酶活性,减少自由基积累/减少铝毒害/减缓细胞损伤/促进 对磷元素的吸收
(3)提高土壤pH升高/减弱土壤酸性, 降低近表层土壤铝离子含量
(4)
促进水稻分泌葡萄糖,招募更多的溶磷菌,将更多有机磷转化为无机磷促进OsPht1;2基因的表达,促进 磷酸盐运输和吸收正反馈
【详解】(1)磷元素主要是以磷酸盐的形式被植物根系吸收,而吸收过程需要细胞膜上的载体蛋白协助,同时细胞膜的基本支架是磷脂。当自由基攻击细胞膜的磷脂和载体蛋白后,细胞膜结构被破坏、运输磷的载体蛋白受损,就会导致根部细胞吸收磷的能力下降。
(2)从图甲可以看到,和单独Al组相比,Al+RP组的叶片叶绿素相对含量更高,叶绿素是光合作用的关键色素,含量高可以提升水稻的光合作用强度,制造更多有机物;同时Al+RP组的过氧化物酶活性更高,过氧化物酶可以清除自由基,减少自由基对细胞的损伤,缓解铝毒害,还能促进水稻对磷元素的吸收,保障细胞正常代谢,最终提升产量。
(3)观察图乙,接种RP后土壤的pH值更高(酸性更弱),同时表层土壤的Al³⁺浓度更低。较高的pH能降低土壤酸性,减少Al³⁺的毒害,为根系提供更适宜的环境。
(4)Al+RP组水稻根系分泌的葡萄糖远多于Al组,葡萄糖可以为溶磷菌提供营养,招募更多溶磷菌,将土壤中有机磷转化为无机磷,增加可吸收的磷源; 同时Al+RP组OsPht1;2基因表达量更高,该基因产物能促进磷酸盐的运输,提升水稻对无机磷的吸收效率,双重作用缓解磷缺乏。水稻分泌葡萄糖给根际菌株提供营养,根际菌株帮助水稻改善生存环境、提升磷吸收,两者相互促进,这种相互受益的关系属于正反馈调节,一方的变化会促进另一方的正向变化,形成长效的互利机制。
18.(1)非生物/非密度制约出生率和死亡率
(2)0-60m浮游植物生物量(数量)下降,60-150m光照增加
(3)较小浮游植物细胞尺寸越小,表面积与体积 之比(相对表面积越大),在低营养环境下吸收营养盐分的效率更高CHL下降,浮游植物总量(初级生产力),/能量输入总量减少中低纬度浮游植物尺寸变小导致营养级数增加(食物链延长),能量在沿食物链传递过程中散失损耗增加
【详解】(1)光照、温度、盐分属于非生物因素(也叫非密度制约因素),这类因素的影响强度不随种群密度变化而改变,对种群数量起限制作用。种群密度的直接影响因素是出生率和死亡率(迁入率 / 迁出率,浮游植物无明显的迁入迁出,因此核心是出生率和死亡率)。温度(海洋热浪)会影响浮游植物的酶活性、代谢速率,直接影响繁殖(出生率)和死亡速率,进而改变种群密度。
(2)图甲中,0-60m 水层的 CHL 异常值为负值(低于常年平均,说明浮游植物数量下降),60-150m 水层的 CHL 异常值为正值(高于常年平均,说明浮游植物数量上升)。 高纬度浮游植物生长主要受光照限制:海洋热浪会导致表层(0-60m)水温升高,浮游植物代谢加快、繁殖或死亡速率变化,导致表层浮游植物生物量下降; 表层浮游植物减少后,对光的遮挡减弱,60-150m 水层的光照强度增加,原本光照不足的深水层环境变得更适宜浮游植物生长,因此该水层浮游植物繁殖旺盛,CHL 异常值升高。
(3)由背景可知,中低纬度 ξ 异常值高,对应较小尺寸的浮游植物占比升高,因此尺寸趋向于 “较小”。细胞尺寸与物质运输效率的核心规律:细胞体积越小,表面积与体积之比(相对表面积)越大,物质运输效率越高。中低纬度受营养限制,小尺寸浮游植物相对表面积大,吸收营养盐分的效率更高,更能适应低营养的环境。初级生产力下降:CHL 降低,说明浮游植物总量减少,生态系统的能量输入(生产者固定的太阳能)总量减少,可流向更高营养级的能量基础变少; 食物链延长,能量损耗增加:浮游植物趋向于小尺寸(多为 <5μm),只能被微型浮游动物摄食;而微型浮游动物不能直接被小型鱼类利用,需要经过 “微型浮游动物→其他动物→小型鱼类 / 幼鱼” 的额外营养级,食物链延长,能量在传递过程中的损耗大幅增加,最终能到达渔业资源(鱼类)的能量总量减少。
19.(1)细胞直接接触
(2)黑色素体可以与CD8⁺T细胞相互作用并损害其功能黑色素体与CD8⁺T细胞的结合率明显高于黑色素瘤细胞与CD8⁺T细胞,结合速率更快
(3)抑制黑色素(体)形成,诱导CD8⁺T细胞浸润小鼠黑色素瘤模型+曲酸+IgG和小鼠黑色素瘤模型+曲酸+抗CD8⁺T细胞抗体
(4)黑色素瘤细胞分泌携带强效MHC-肿瘤抗原分子的黑色素体,且这些黑色素体更容易与肿瘤特异性CD8⁺T细胞结合,导致CD8⁺T细胞功能障碍和凋亡
【详解】(1)免疫细胞之间可以通过释放信号分子(细胞因子)、 细胞直接接触(如细胞毒性T细胞与靶细胞直接接触)等方式进行信息交流,参与免疫过程。。
(2)免疫治疗效果差,说明 CD8⁺T 细胞(细胞毒性 T 细胞)无法有效杀伤肿瘤细胞,功能被抑制了。 患者体内 “携带黑色素体的 CD8⁺T 细胞比例显著更高”,说明黑色素体和 CD8⁺T 细胞发生了相互作用,并且这种作用会抑制 / 损害 CD8⁺T 细胞的功能,导致其无法发挥抗肿瘤作用,最终免疫治疗失效。纵坐标是 “结合率 /%”,横坐标是培养时间(0.5h、4h)。 代表 “黑色素体 - CD8⁺T 细胞结合率” 的黑色圆点线,在 0.5h 和 4h 的结合率都显著高于代表 “黑色素瘤 - CD8⁺T 细胞结合率” 的三角虚线。 0.5h 时两者差距就很大,4h 时差距进一步扩大,说明黑色素体和 CD8⁺T 细胞结合更快、结合率更高,因此相互作用更高效。
(3)①A 组:DMSO(溶剂对照)处理,肿瘤变化不明显,说明溶剂本身无作用。 B 组:曲酸处理,肿瘤生长减缓,且瘤内 CD8⁺T 细胞增加。 曲酸是 “酪氨酸酶抑制剂”,酪氨酸酶是黑色素合成的关键酶,因此曲酸可以抑制黑色素 / 黑色素体的形成;同时,B 组瘤内 CD8⁺T 细胞增多,说明曲酸能诱导 CD8⁺T 细胞浸润到肿瘤组织中,增强免疫杀伤作用,从而阻断肿瘤生长。
②实验设计要遵循 “单一变量原则”,验证 “效果依赖 CD8⁺T 细胞”,核心思路是: 对照组 1:小鼠 + DMSO+IgG(空白对照,和 A 组逻辑一致,IgG 是抗体对照,排除抗体本身的影响) 对照组 2:小鼠 + 曲酸 + IgG(曲酸 + 无关抗体,和 B 组逻辑一致,证明曲酸本身有效) 实验组:小鼠 + 曲酸 + 抗 CD8⁺T 细胞抗体(清除 CD8⁺T 细胞,观察曲酸是否还能抑制肿瘤生长) 如果实验组肿瘤生长恢复,说明曲酸的抗肿瘤效果依赖 CD8⁺T 细胞。
(4)黑色素体是黑色素瘤细胞分泌的细胞外囊泡,携带强效 MHC - 肿瘤抗原。 黑色素体与 CD8⁺T 细胞的结合比肿瘤细胞本身更高效,且结合的 CD8⁺T 细胞和结合肿瘤细胞的 CD8⁺T 细胞有大量相同的 TCR(受体),说明这些 CD8⁺T 细胞是肿瘤特异性 T 细胞。 黑色素体和这些 T 细胞结合后,会损害 T 细胞的功能(题目 2 的结论),导致 T 细胞无法识别和杀伤肿瘤细胞,甚至凋亡。 因此,黑色素瘤的免疫逃逸机制可以总结为: 黑色素瘤细胞通过分泌携带肿瘤抗原的黑色素体,“抢先” 与肿瘤特异性 CD8⁺T 细胞结合,诱导 T 细胞功能障碍或凋亡,从而逃避免疫系统的杀伤。
20.(1)aaBBEE、AAbbEE、AABBee
(2)红心:非红心=3:1
(3)边缘果肉ARF蛋白含量高,ARF与MYB结合,干扰MYB与HLH结合形成二聚体,抑制ANS的转录合成,ANS减少,花青素合成减少,进而呈现绿色增加一组MYBN+C作为对照组
(4)抑制果肉边缘ARF基因和F-box1基因的表达/敲除ARF基因和F-box1使A基因突变为A+,使其不需与HLH结合即可直接诱导ANS基因转录
【详解】(1)根据题干,红心猕猴桃的基因型为A_B_E_,只有同时含三个显性基因才能表现红心。纯合非红心亲本杂交,F1全为红心,F2红心 :非红心=9:7,说明F1只有两对基因杂合,一对为显性纯合,因此亲本为一个单隐性纯合的非红心,另一个为另一对单隐性纯合的非红心,故甲的基因型可能为aaBBEE、AAbbEE、AABBee中的一种。
:非红心=9:7,说明F1只有两对基因杂合,一对为显性纯合,因此亲本为一个单隐性纯合的非红心,另一个为另一对单隐性纯合的非红心,故甲的基因型可能为aaBBEE、AAbbEE、AABBee中的一种。
(2)若植株乙为A基因隐性纯合突变,则乙基因型为aaBBEE,与突变体A+ABBEE杂交,F1为1/2A+aBBEE、1/2AaBBEE;F1随机交配,配子中a为1/2,非红心只有aa(无功能性A/A+,无法激活ANS),aa概率为(1/2)2=1/4,因此红心 :非红心=3:1。
:非红心=3:1。
(3)对比实验结果:组1MYB与HLH可结合产生强荧光,加入ARF后荧光消失,且组4证明MYB可与ARF结合,因此推测ARF竞争性结合MYB,由于边缘果肉ARF蛋白含量高,ARF与MYB结合,干扰MYB与HLH结合形成二聚体,抑制ANS的转录合成,ANS减少,花青素合成减少,进而呈现绿色。 第5组只做了加F−box1、MYBN+C的处理,要证明F−box1促进MYB降解,需要增加一组MYBN+C作为对照组,排除其他因素对荧光的影响,使结论严谨。
(4) 已知边缘果肉绿色是ARF和F−box1含量高导致,因此获得全红肉猕猴桃新品种的思路:抑制果肉边缘ARF基因和F-box1基因的表达/敲除ARF基因和F-box1/使A基因突变为A+,使其不需与HLH结合即可直接诱导ANS基因转录。
21.(1)染色体的DNA
(2)5'-AAGCTTTC-3'潮霉素确保只有1个SCLI4基因整合至细胞染色体DNA
(3)突变体T中SCL14基因表达量无明显差异
(4)比较两种转录组的差异性/寻找Cd胁迫下受到SCL14蛋白特异性调控的基因
【详解】(1)农杆菌转化法中,Ti 质粒的 T-DNA 片段可以随机整合到植物细胞的染色体DNA(核基因) 中,从而稳定遗传给后代。
(2)①为保证基因定向连接,Ti质粒启动子后酶切位点顺序为BamH Ⅰ→Hind Ⅲ,选择BamH Ⅰ和Hind Ⅲ双酶切载体,而SCL14的下游(转录终止端)本身自带BamH Ⅰ位点,仅需在上游引物5'端加入Hind Ⅲ的识别序列(5′−AAGCTT−3′,共6个碱基),SCL14基因开头序列为TCGCAACGTG,后续两个碱基为TC,因此上游引物5'端前8个碱基为5'-AAGCTTTC-3'。
②潮霉素抗性基因位于T-DNA区域,随T-DNA整合到植物基因组中,卡那霉素抗性基因位于T-DNA外,因此用含潮霉素的培养基筛选成功转入重组T-DNA的植株。
③3:1是一对等位基因的性状分离比,说明目的基因仅插入一个染色体位点,为单拷贝,后续自交筛选纯合株系更简便;若为15:1说明目的基因插入两个非同源染色体,后续筛选纯合难度大,故优先选择分离比为3:1而非15:1或其他比例的植株的目的是确保只有1个SCLI4基因整合至细胞染色体DNA。
(3)若SCL14与 TGA3 蛋白独立调控拟南芥对 Cd 的耐受性,则突变体 S(SCL14 缺失)中 TGA3 表达量无明显差异;同时,突变体 T(TGA3 缺失)中 SCL14的表达量也无明显差异,说明两者的表达互不影响,功能上独立调控。
(4)提取总mRNA测序属于转录组分析,目的是比较两种转录组的差异性,寻找Cd胁迫下受到SCL14蛋白特异性调控的基因,明确其调控耐镉性的机制。
 夜雨聆风
夜雨聆风