近日,诺贝尔化学奖得主、蛋白质设计先驱 David Baker 教授作为通讯作者(杨为、王顺智等为共同第一作者),在国际顶尖学术期刊 Nature 上发表了题为:The past, present and future of de novo protein design的综述论文。杨为博士已全职加入深圳医学科学院,任特聘研究员,成立蛋白质药物设计课题组。
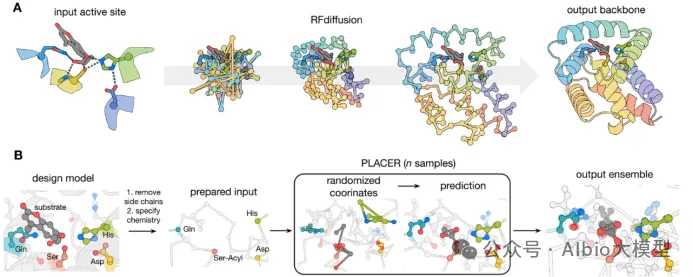
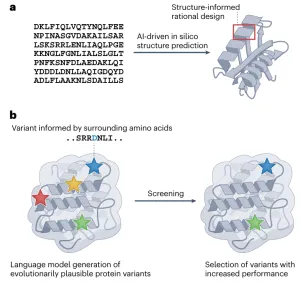
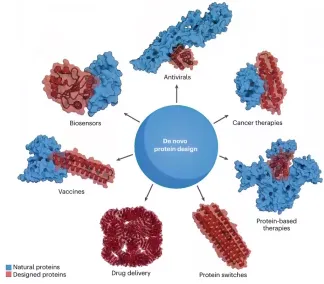
该综述论文描述了从头蛋白质设计(de novo protein design)的当前状态。尽管在成功率和活动方面仍有改进的空间,但设计新型蛋白质结构、组装体和蛋白质结合剂这一长期存在的难题已接近解决。这些领域当前的关键问题不是如何设计,而是设计什么,开源设计方法如 RFdiffusion 和 ProteinMPNN 以及蛋白质结构预测工具使生物化学家和分子生物学家能够广泛探索可能的应用。在从头设计小分子靶点结合剂、酶和多态蛋白质系统方面也取得了相当大的进展。方法开发目前面临的挑战包括设计用于克服高能垒反应的催化剂,以及更广泛地说,设计将结合、构象变化和催化整合在一起的开关和纳米机器。在接下来的 5-10 年里,预计会设计出复杂的蛋白质纳米机器和材料,其功能远远超出自然进化所产生的功能,应用于医学、技术和可持续性等广泛领域。

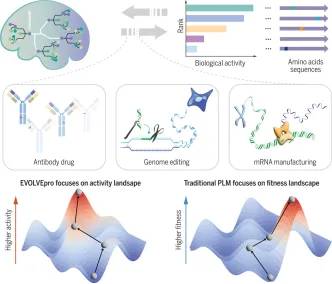
在这篇综述论文中,David Baker 团队为我们展望了一个激动人心的新时代——未来十年内,蛋白质从头设计将解决人类面临的重大难题,并在医学、可持续发展和生物技术领域发展成为一项基础性工具。我们可以利用这些工具设计出可能成为攻克癌症、阿尔茨海默病的利器,制造出高效环保的工业催化剂,甚至能组装成微小的“纳米机器”,执行特定的任务。
作为2026年最值得期待的技术!
AI蛋白质设计资料与学习途径少之又少,特培训学习迫在眉睫!联合清华大学、北京大学、西湖大学、浙江大学、中国科技技术大学、天津大学、协和药物研究所、中科院微生物所、上海药物研究所等高校和研究单位已经举办培训把八十余期,参会学员达9000余人!学员好评极高!其中不乏有发表Nature、Cell、Science等国际顶刊!
01 AI蛋白质设计线上直播课
02 AI抗体设计线上直播课
03 合成生物学与基因线路设计
04 AI基因编辑线上直播课
05 AI构建虚拟细胞线上直播课
06 深度学习在多组学融合中的应用
AI蛋白质设计主讲老师在学术界和工业界都有丰富算法开发和应用经验,博士毕业于国内顶尖课题组,从事蛋白质结构预测和蛋白质设计的研究工作,相关工作成果已在Cell Systems、Angew. Chem. Int. Ed.、JCIM等国际知名期刊发表论文。目前在知名药企担任高级研究员,主导AI驱动的大分子药物设计平台开发与团队管理。

学员评价


01
AI蛋白质设计课表

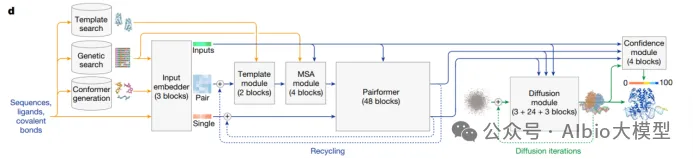
02
通过课程学习您将得到

多种蛋白质设计方法、深度学习酶设计、深度学习抗体设计等流程!让学员快速学会David baker核心方法!培训理论结合实操!提供服务器使用!通过详细讲解实操AlphaFold2、AlphaFold3以及pymol和Foldseek等软件让学员学会蛋白质结构预测!通过详细讲解实操ESM系列(ESM-1b、ESM-1v、ESM2、ESMC、ESM3)、GPT的生成模型ProGen让学员学会蛋白质大语言模型!通过详细讲解实操ProteinMPNN、LigandMPNN、ThermoMPNN、Rfdiffusion等软件让学员学会多种蛋白质设计方法!最后通过深度学习酶设计与深度学习抗体设计让学员通过不同方向不同方法更全面的了解蛋白质设计当下的全面性!六天培训流程循序渐进!知识点全覆盖!更是讲解十篇顶刊文献,让学员更好的知道当下蛋白质设计的核心热点以及优势
AI抗体设计
主讲老师在学术界和工业界都有丰富算法开发和应用经验,博士毕业于国内顶尖课题组,从事蛋白质结构预测和蛋白质设计的研究工作,相关工作成果已在Cell Systems、Angew. Chem. Int. Ed.、JCIM等国际知名期刊发表论文。目前在知名药企担任高级研究员,主导AI驱动的大分子药物设计平台开发与团队管理。
02
AI抗体设计课表

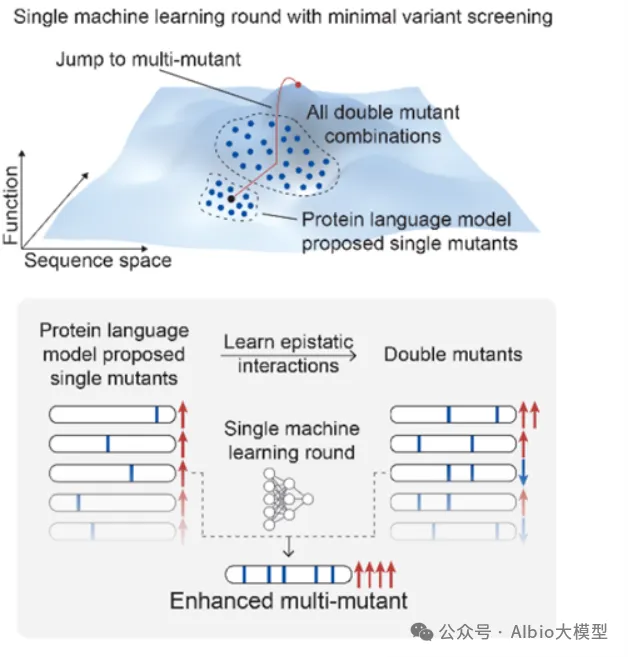
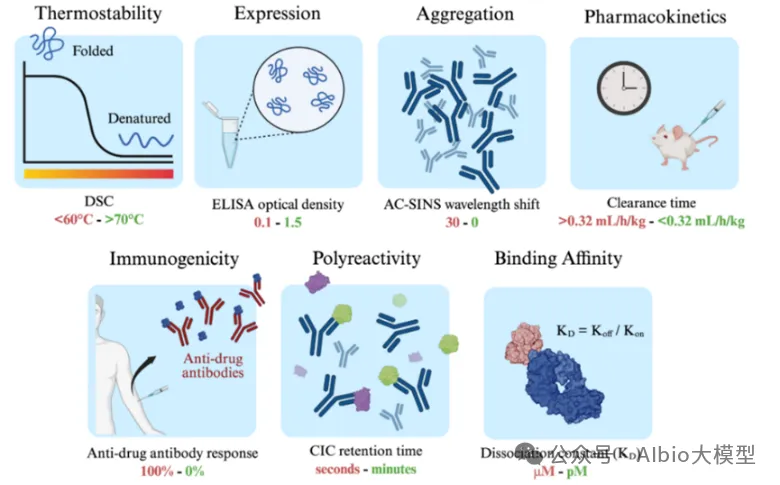
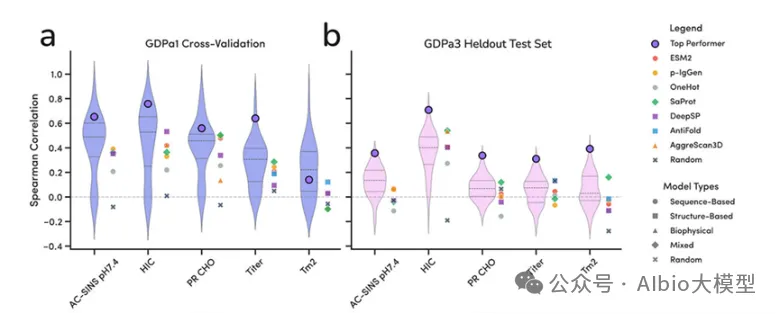
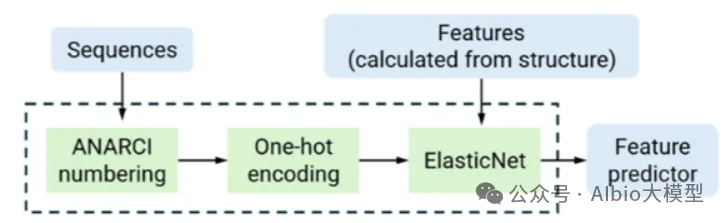

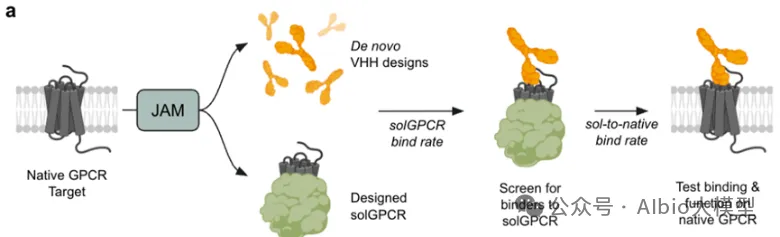
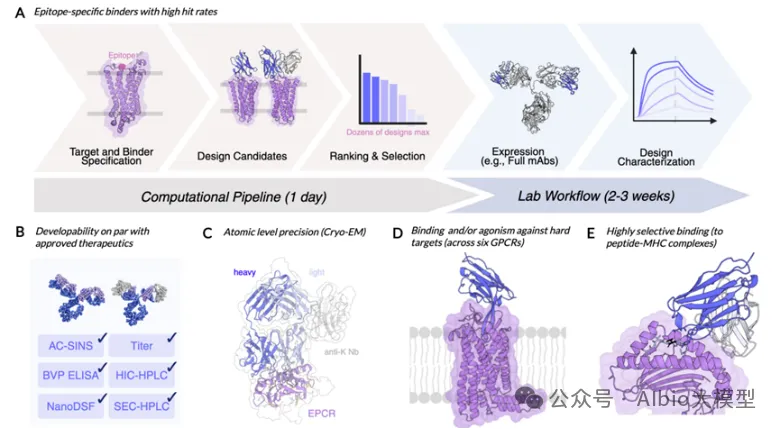
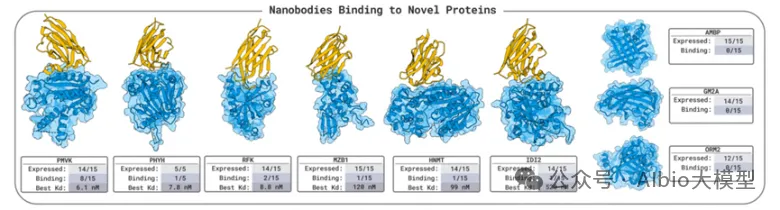

02
通过课程学习您将得到

培训聚焦深度学习驱动的抗体设计为核心方向,以David Baker实验室核心设计方法、主流抗体大语言模型、AI抗体结构预测模型为教学核心,秉持理论夯实、实操落地、科研进阶、工程应用的培训原则。依托高性能服务器实操环境,循序渐进讲解行业主流软件、开源模型、代码实操、数据处理与模型调优,搭配十篇顶刊经典文献深度解析,全方位覆盖当下抗体设计领域前沿技术、研究热点与工业落地方案。助力零基础及进阶学员快速打通理论原理、代码实操、模型应用、科研创新全流程,熟练掌握AI抗体设计全套技术栈,可独立完成抗体结构预测、抗体亲和力优化、可开发性改造、抗体从头设计等科研实操任务,适配药物研发、生物工程、合成生物学等科研与工业应用场景。
AI+基因编辑
主讲老师在学术界具有多年的研究经历和应用经验,来自于国内顶尖课题组,从事基因组编辑技术与人工智能交叉融合的研究工作,相关工作成果已在Nature Biotechnology、Nature Plants、Trends in Biotechnology等国际知名期刊发表
03
AI+基因编辑课表

第一天
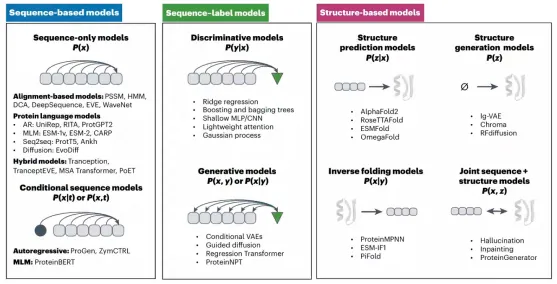
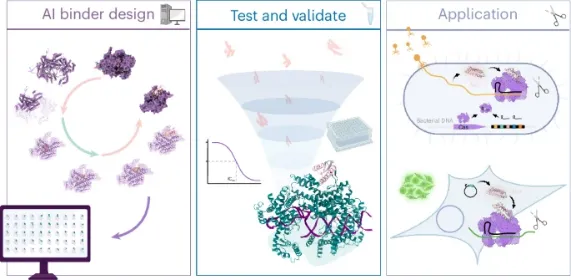
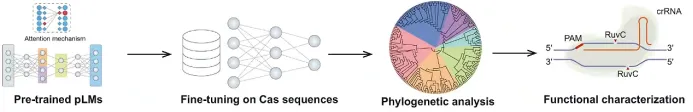
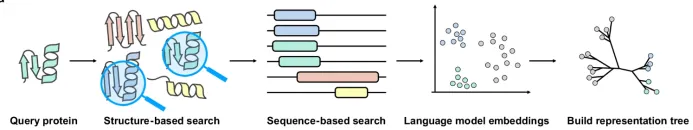
02
通过课程学习您将得到

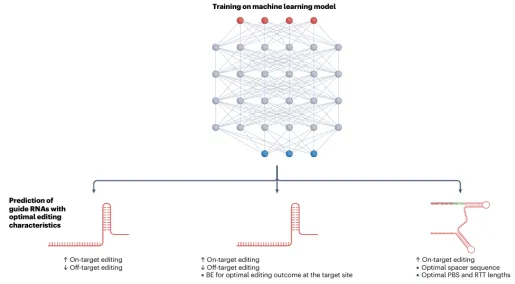
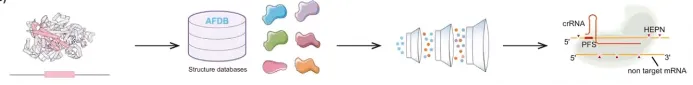
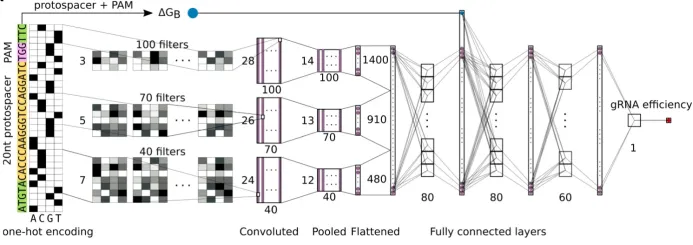
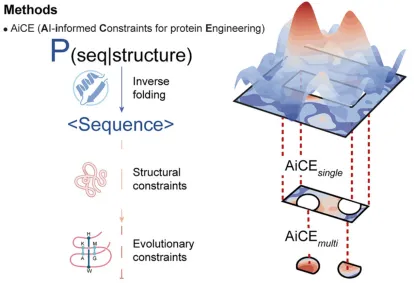
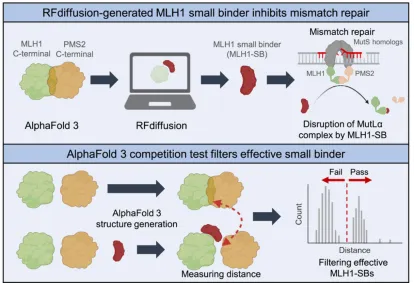
本次培训聚焦基因组编辑技术体系与人工智能辅助基因编辑设计前沿方向,系统讲解CRISPR基因编辑全套技术原理、编辑工具、脱靶检测、实验流程、主流设计分析软件;深入剖析深度学习在gRNA优化、编辑活性预测、编辑酶改造、新型编辑系统挖掘中的核心应用。培训秉持理论扎实、通俗易懂、实操落地、案例复刻、科研进阶的教学理念,依托高性能GPU服务器,手把手完成Linux环境配置、深度学习模型搭建、AI蛋白进化、从头设计、结构比对、新型CRISPR挖掘等高阶实操。结合当下主流AI生成模型、大语言模型、结构比对工具,复刻多篇顶刊经典研究案例,使学员能够完整掌握传统基因编辑+人工智能基因编辑全流程技术栈,具备独立开展基因编辑载体构建、gRNA智能优化、编辑酶定向进化、新型编辑元件挖掘、人工设计结合蛋白等科研能力,适配植物育种、基因治疗、生物医药、分子诊断等科研及工业研发场景。
AI构建虚拟细胞
主讲老师在学术界具有多年的研究经历和应用经验,来自于国内顶尖课题组,从事基因组编辑技术与人工智能交叉融合的研究工作,相关工作成果已在Nature Biotechnology、Nature Plants、Trends in Biotechnology等国际知名期刊发表
04
AI构建虚拟细胞课表

第一天| 细胞数据数字化与基础表征





02
通过课程学习您将得到

• 技术栈回顾:从数据→状态→调控→动态→药物→疾病→孪生→临床• 前沿趋势:大模型、多模态、空间组学、虚拟敲除• 职业发展:计算生物学人才需求与能力路径配套资源


授课时间安排

01
AI蛋白质设计授课时间

2026.6.06-2026.6.07白天(09:00-11:30--13:30-17:00)
共计6天的课 通过腾讯会议直播 线上实操 提供全部录播
02

AI抗体设计授课时间
2026.6.23-2026.6.26晚上(19:00-22:00)
共计5天的课 通过腾讯会议直播 线上实操 提供全部录播
03
AI+基因编辑授课时间

共计5天的课 通过腾讯会议直播 线上实操 提供全部录播
04
AI构建虚拟细胞授课时间

共计5天的课 通过腾讯会议直播 线上实操 提供全部录播
培训费用及福利
课程报名费用:
AI蛋白质设计、AI构建虚拟细胞、AI基因编辑、AI抗体设计直播课:
公费价:每人每班¥6880元 (含报名费、培训费、资料费、提供课后全程回放资料)
自费价:每人每班¥6580元 (含报名费、培训费、资料费、提供课后全程回放资料)
重磅优惠:
报二送一(同时报名两个班免费赠送一个学习名额赠送班任选)
优惠1:
两班同报:10880元 (原价18640)
三班同报:14880元 (原价23620)
特惠一:24880元 (可免费学习一整年本单位举办的任意课程)
特惠二:28880元(可免费学习两整年本单位举办的任意课程)
优惠2:提前报名缴费可享受300元优惠(仅限十五名)
报名学习课程可赠送往期课程回放(报多少赠多少)
(可点击跳转详情链接):


1、课程特色--全面的课程技术应用、原理流程、实例联系全贯穿
2、学习模式--理论知识与上机操作相结合,让零基础学员快速熟练掌握
3、课程服务答疑--主讲老师将为您实际工作中遇到的问题提供专业解答
授课方式:通过腾讯会议线上直播,理论+实操的授课模式,老师手把手带着操作,从零基础开始讲解,电子PPT和教程开课前一周提前发送给学员,所有培训使用软件都会发送给学员,有什么疑问采取开麦共享屏幕和微信群解疑,学员和老师交流、学员与学员交流,培训完毕后老师长期解疑,培训群不解散,往期培训学员对于培训质量和授课方式一致评价极高!

腾讯会议实时直播解答|手把手带着操作

 夜雨聆风
夜雨聆风