R包神器 | 系统发育和进化分析 – ape (二) Face to Face 树
介绍ape包绘制的面对面树
cophyloplot
绘制两个系统发育树的面对面(Face to face)图,并在顶端(Tips,即序列名)之间连线。用于比较、展示2个有所关联的系统发育树。
如果指定了链接(Links,即2列Tips名称)方式,此函数将绘制两棵面对面的树。通过鼠标单击可围绕节点 (Nodes)旋转每棵树的分支 (Branches)。
在文献中的展示例子:
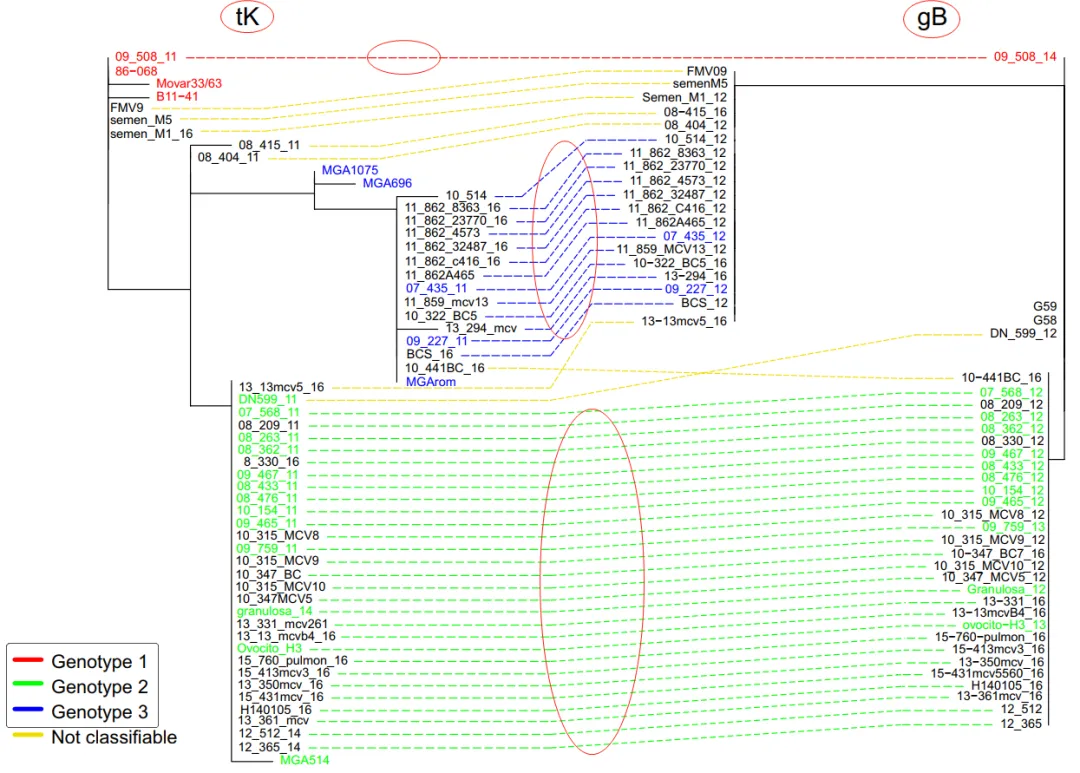
相关方法:

https://doi.org/10.1007/s11033-020-05449-9
扫码、联系客服老师报名,领取资料、上手分析

参考描述:
The comparison of tree topology was performed using “cophyloplot” function available in the R package APE.
另1个面对面树图 (粉丝后台共享)
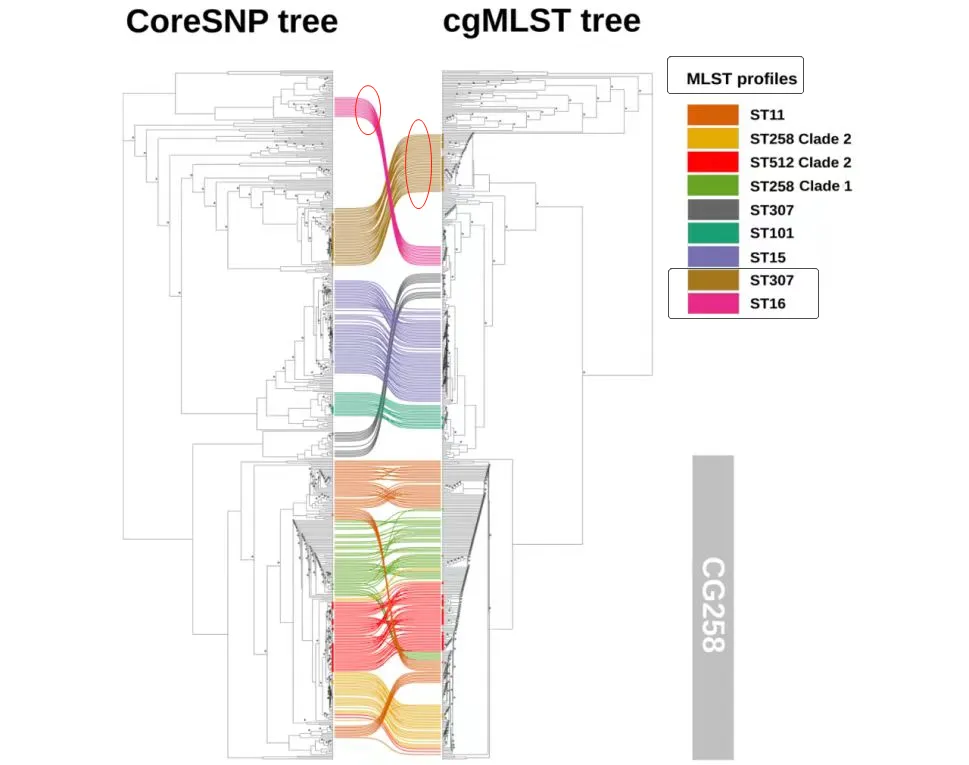
ST注释来自MLST分析
示例数据
# 面对面树library(ape)# cophyloplot函数:绘制两个系统发育树的面对面(Face to face)图,并在顶端(Tips,即序列名)之间连线。用于比较、展示2个有所关联的系统发育树。# 如果指定了链接(Links,即2列Tips名称)方式,此函数将绘制两棵面对面的树。通过鼠标单击可围绕节点 (Nodes)旋转每棵树的分支 (Branches)。#two random treestree1 <- rtree(40)tree2 <- rtree(20)tree1# Phylogenetic tree with 40 tips and 39 internal nodes.# Tip labels:# t14, t13, t18, t20, t3, t9, ...# Rooted; includes branch lengths.tree2# Phylogenetic tree with 20 tips and 19 internal nodes.# Tip labels:# t15, t7, t6, t20, t8, t10, ...# Rooted; includes branch lengths.# 生成1个关联矩阵,来引导2棵树之间的连线:association <- cbind(tree2$tip.label, tree2$tip.label)association

cophyloplot(tree1, tree2, assoc = association, type="phylogram", use.edge.length=F, space = 50, length.line = 7, gap = 6, rotate=F, col="green", show.tip.label=T, font=4, lwd=1, lty=1)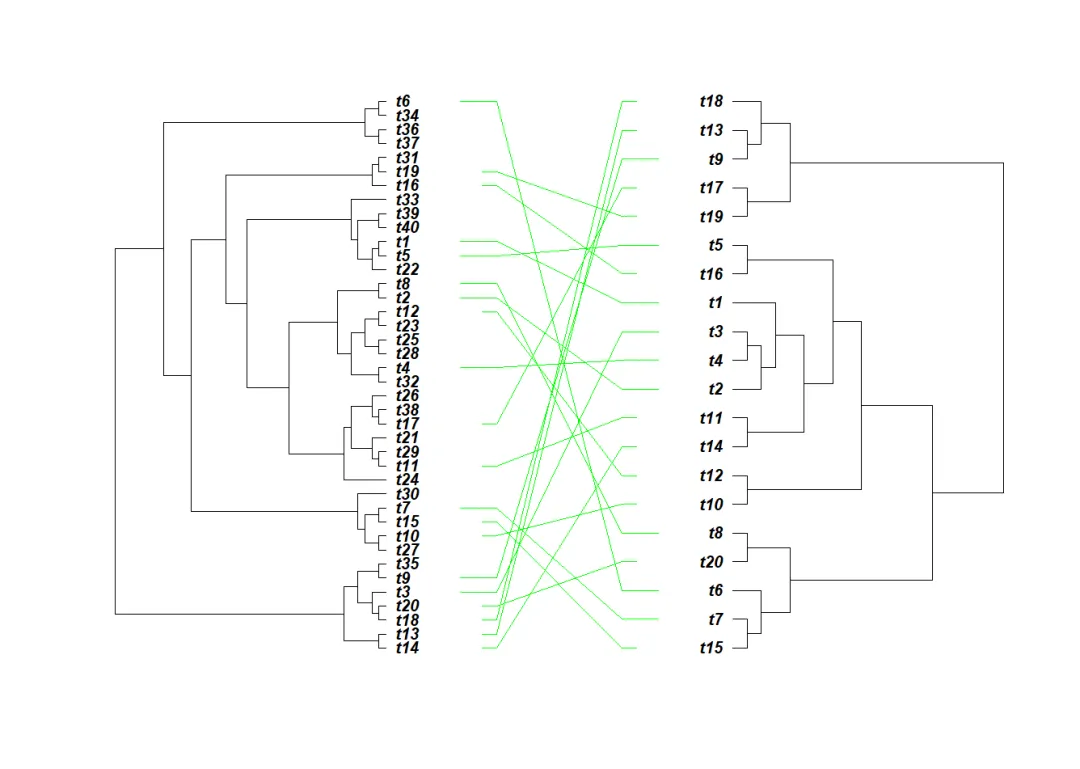
变量tree1、tree2是2个ape包的”phylo“类对象 (即ape对树的存储变量)
其它选项:
cophyloplot(tree1, tree2, assoc = association, type="cladogram", use.edge.length=T, space = 6, length.line = 1, gap = 2, rotate=F, col="orange", show.tip.label=F, font=4, lwd=2, lty=2)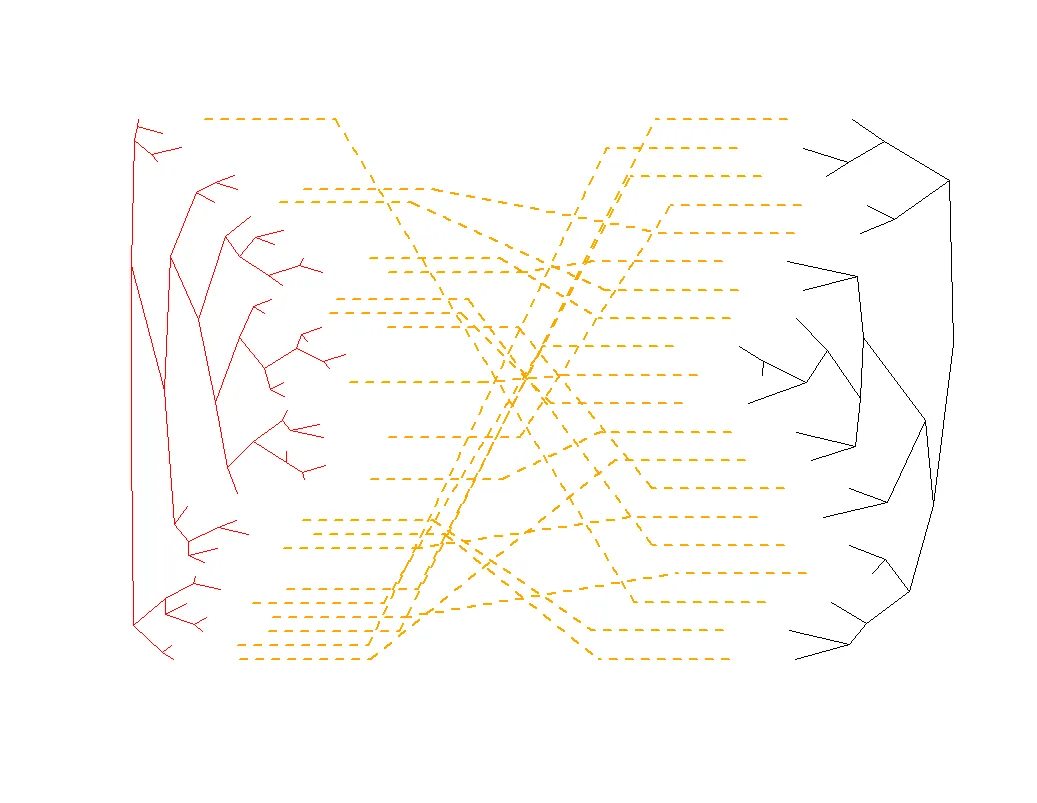
(交互式) plot with rotations
## Not run:# cophyloplot(tree1, tree2, assoc=association, length.line=4, space=28, gap=3, rotate=TRUE)
ape包的cophyloplot函数的目的是同时绘制2个具有相关分类群(Associated taxa)的系统发育树。这2棵树的尖端/Tips(即序列名)数量不一定相同,一个系统发育中的1个以上的尖端/Tips可与另一个尖端相关联。
用于绘制链接的关联矩阵必须是包含尖端/Tips名称的两列矩阵。矩阵中的1行表示绘图上的1个连接线。矩阵的第1列必须包含第1棵树(phy1)的顶端/Tip标签,矩阵的第2列必须包含第2棵树(phy2)的顶端/Tip标签。矩阵中的行数没有限制。一个有2列、1行的矩阵,将给出只有1个连接线的图。
必须改变gap、length.line和space参数,才能得到这2个系统发育的好看的图。该函数会考虑与尖端/Tips处的名称相对应的字符串的长度,尽量使连接线就不会覆盖这些名称。
rotate参数可用于转换2个系统发育树,以获得更可读的图(一般通过减少交叉线的数量)。这可以通过单击节点来完成。按下退出按钮(ESC)或右键返回R的控制台。
扫码、联系客服老师报名,领取资料、上手分析

 夜雨聆风
夜雨聆风




