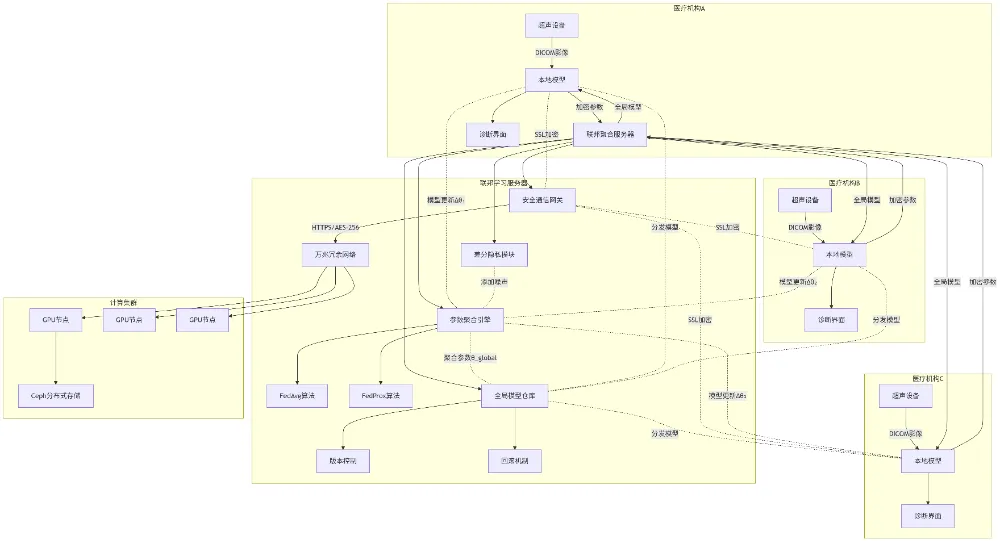
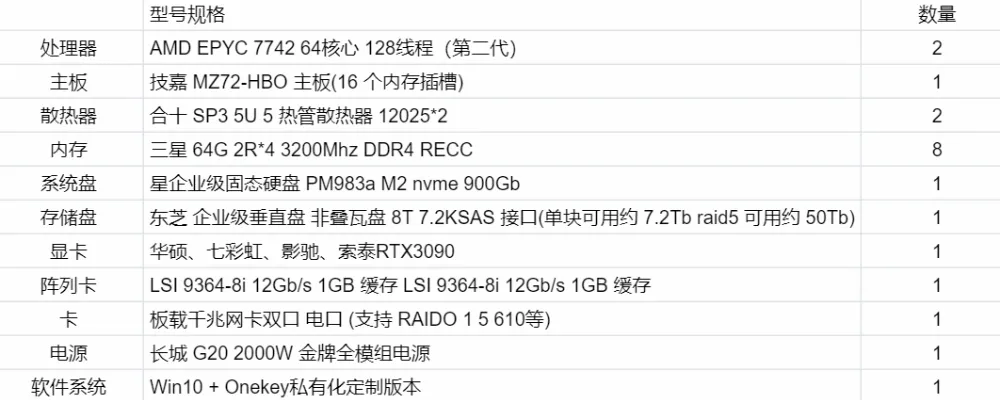
| | |
| 适用于病理,超声,CT,MRI,临床等可用作科研的数据类型。 | | |
| | 2.1.1、CT:3d的CT的样例数据。包括images和masks | | |
| 2.1.2、skin4clf:【What】组件使用到的数据:此数据可以使用labelme进行标注;skin4clf_out:转化出来的数据 | | |
| 2.1.3、list模式:包括1个文件夹和2个文件:images和train.txt和val.txt:分别表示原始数据:训练集和测试集。 | | |
| 2.1.4、folder模式:包括2个文件夹和1个文件:train、val分别表示训练集和测试集:labels.txt为模型标签。 | | |
| 2.1.5、skin4seg:【Which2d】组件使用功能的数据:此数据依然是label标注结果;skin4seg_out:转化出来的数据。 | | |
| | |
| 2.1.7、tumor_stroma:病理切片数据:此数据为qupath标注之后按照8倍降采样保存的images和masks(geojson格式)。 | | |
| | |
| 2.1.9、phy_bio.csv:生理生化数据。 | | |
| 2.1.10、survival.csv:生存数据。 | | |
| 2.1.11、Metabonomics.csv:蛋白质组学数据。 | | |
| 注:这些数据大部分开源数据集:或者其他脱敏混淆之后的数据:不代表任何临床问题:仅供模型训练使用。 | | |
| | 3.1.1、OKT-update:Onekey软件更新程序。(如果更新失败请在论坛下载最新)。 | | |
| 3.1.2、OKT-crop2path:将病理切片切分成小patch。 | | |
| 3.1.3、OKT-crop_max_roi:功能十分强大的crop ROI工具。 | | |
| 3.1.4、OKT-convert2nii:将指定目录所有可以转化成nii的数据都转化成nii的数据格式。 | | |
| 3.1.5、OKR-convert2jpg:将指定目录下所有可以转化为jpg的数据全部转化成jpg数据。 | | |
| 3.1.6、OKT-convertjpg2nii:将指定目录下所有的jpg转化成nii数据。 | | |
| 3.1.7、OKT-convert_geojson2mask:应用与qupath标注好的数据:进行image-mask数据转化。 | | |
| 3.1.8、OKT-convert_rtstruct2nii:讲RTstruct数据转化成标注数据。 | | |
| 3.1.9、OKT-crop_WSI2patch:讲WSI病理数据转化成patch。数据格式包括ndpi和svs。 | | |
| 3.1.10、OKT-resample:3d数据采样:将所有的数据进行体素归一。 | | |
| 3.1.11、OKT-standardize:数据标准化:裁剪掉制定范围之外的数据。 | | |
| 3.1.12、OKT-fix_spacing:接近 Image/Mask miss matching的问题。 | | |
| 3.1.13、OKT-gen_probably_map:生成病理数据的概率图和预测结果图。 | | |
| 3.1.14、OKT-crop_video_frame:将视频数据进行抽取关键帧。 | | |
| | 4.1.1、临床指标统计分析,单因素、多因素回归筛选。 | | |
| 4.1.2、Pyradiomics提取特征,Shape、First Order、Texture特征;LoG、Wavelet小波变换等 | | |
| 1.ICC,随机挑选30,多人标注,选择特征鲁棒性高的。 2.统计检验筛选,utest、ttest、、ANOVA检验,筛选p_value<0.05 3.mRmR,相关系数筛选,spearman、pearson、kendall系数等,相关系数大于0.9的两者保留其一。 4.Lasso,10折交叉验证,权重曲线、rad_score公式、权重图 | | |
| 4.1.4、问题建模,筛选出来的特征,输入到机器学习算法,COX、LR、SVM、RF、XGBoost、LightGBM等模型,构建Signature。 | | |
| 1.统计对比表格,准确率、AUC、Sensitivity,Specificity,F1。 2.挑最好的模型,ROC曲线,DCA曲线、校准曲线。 4.Signature融合,Nomogram,增加临床可解释性。 | | |
| 4.2.1、临床指标统计分析,单因素、步进多因素回归筛选。 | | |
| 1.Pyradiomics提取特征,Shape、First Order、Texture特征;LoG、Wavelet小波变换等 b.裁剪最大的ROI界面,或者使用整体ROI区域。 | | |
| 1.ICC,随机挑选30,多人标注,选择特征鲁棒性高的。 2.PCA,针对深度学习特征使用,也可以选择进行端到端降维。 3.统计检验筛选,utest、ttest、、ANOVA检验,筛选p_value<0.05 4.mRmR,相关系数筛选,spearman、pearson、kendall系数等,相关系数大于0.9的两者保留其一。 5.Lasso,10折交叉验证,权重曲线、rad_score公式、权重图 | | |
| 4.2.4、问题建模,筛选出来的特征,分数据输入到机器学习算法,构建Rad Signature,DTL Signature、DLR Signature。 | | |
| 1.统计对比表格,准确率、AUC、Sensitivity,Specificity,F1。 4.Grad-CAM激活图,寻找深度学习模型可解释性。 5.Nomogram,Signature融合,对比Clinical、Rad、DTL、DLR不同数据的结果差异。 | | |
| 4.3.1、临床指标统计分析,单因素、步进多因素回归筛选。 | | |
| a.训练分类任务,例如:VGG、ResNet、Inception、DenseNet等 b.训练分割任务,例如:FCN、Deeplab、Unet等 a.所有的patch融合成类别histogram直方图或者做成TF-IDF特征。 c.使用深度学习中间层特征,然后使用深度模型进行融合。 | | |
| 4.3.3、问题建模,筛选出来特征,分数据输入到机器学习算法,构建Signature。 | | |
| b.Grad-CAM激活图,结合病理组织解释模型。 2.统计对比表格,准确率、AUC、Sensitivity,Specificity,F1。 | | |
| 4.3.5、Nomogram,Signature融合,对比Clinical、Pathology不同数据的结果差异。 | | |
| 1.临床特征,指标统计分析,单因素、步进多因素回归筛选 a.基于传统机器学习算法,PCA、Lasso降维。 b.基于自监督深度学习算法,Auto encoder decoder,VAE。 a.Pyradiomics提取特征,Shape、First Order、Texture特征;LoG、Wavelet小波变换等 c.融合深度学习特征,Histogram、TF-IDF、概率直方图,或者深度模型特征融合。 | | |
| 4.4.2、问题建模,筛选出来的特征,分数据输入到机器学习算法,构建Signature。 | | |
| b.Grad-CAM激活图,结合病理组织解释模型。 2.统计对比表格,准确率、AUC、Sensitivity,Specificity,F1。 5.Nomogram,Signature融合,对比Clinical、Pathology不同数据的结果差异。 | | |