

医疗智能体 | 官网

https://github.com/FreedomIntelligence/OpenClaw-Medical-SkillsSKILL.md 的形式存在。这些模块既能教 agent 某个专业领域的知识和工作流,也能连接真实数据库、API 和计算工具,并输出更符合临床或科研场景的结构化结果。覆盖范围
它并不只是医学文献检索工具,而是覆盖了临床、基因组学、药物发现、生物信息学、医疗器械等完整生态。README 还专门强调,有了这套 skills 之后,agent 可以执行 PubMed、ClinicalTrials.gov、FDA 查询,也能支持 RNA-seq、scRNA-seq、GWAS、变异注释、药物情报、临床文书和合规分析等任务
pubmed-searchmedical-research-toolkit、medical-specialty-briefs | ||
medical-entity-extractor、clinical-nlp-extractor | ||
clinpgx-databasepharmacogenomics-agent、trialgpt-matching、precision-oncology-agent | ||
scanpyanndata、single-cell-rna-qc、single-preprocessing | ||
bio-single-cell-batch-integrationbio-single-cell-cell-communication | ||
single-to-spatial-mapping | ||
clinvar-databasecosmic-database、vcf-annotator | ||
bio-orchestratorscrna-orchestrator、seq-wrangler、repro-enforcer | ||
scientific-writingscientific-critical-thinking | ||
opentrons-integrationpylabrobot、benchling-integration |
安装流程
curl -fsSL https://openclaw.ai/install.sh | bash
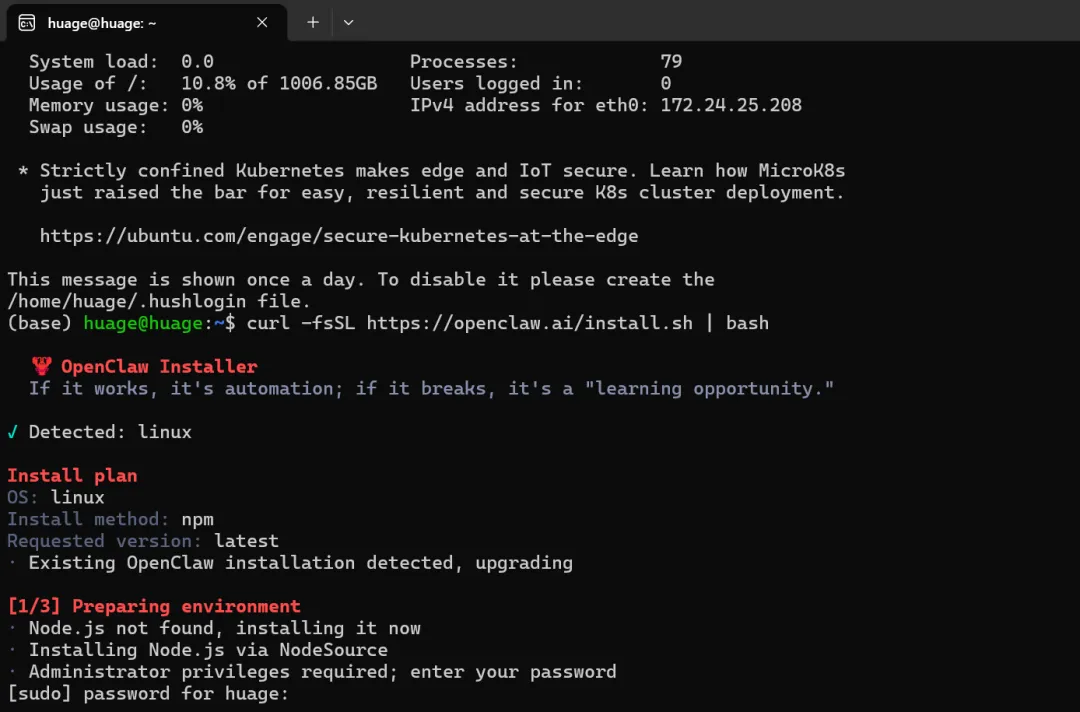
[1/3] Preparing environment
[2/3] Installing OpenClaw
[3/3] Finalizing setup
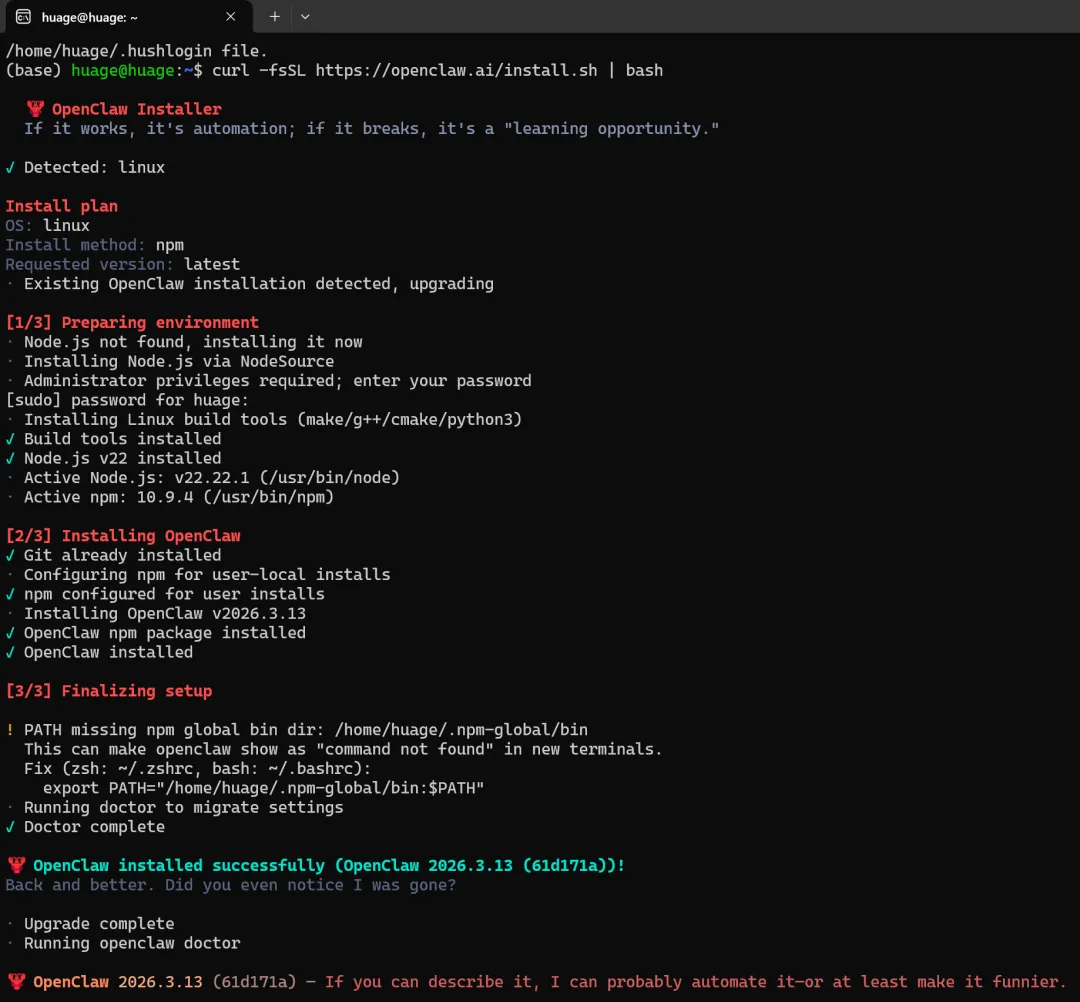
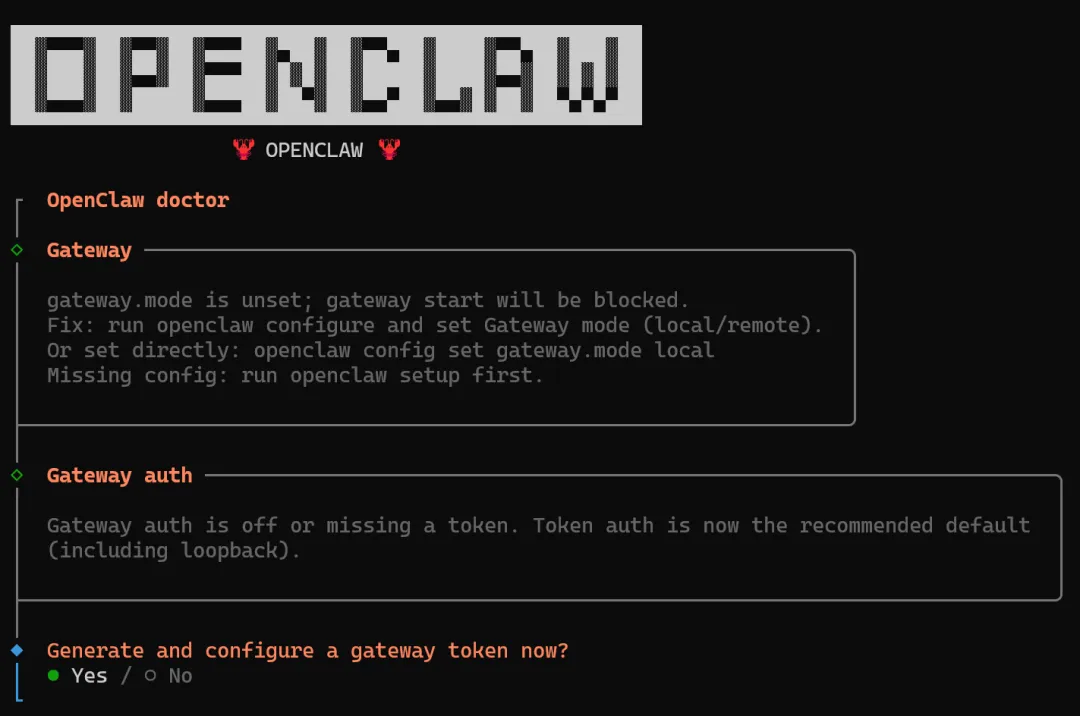
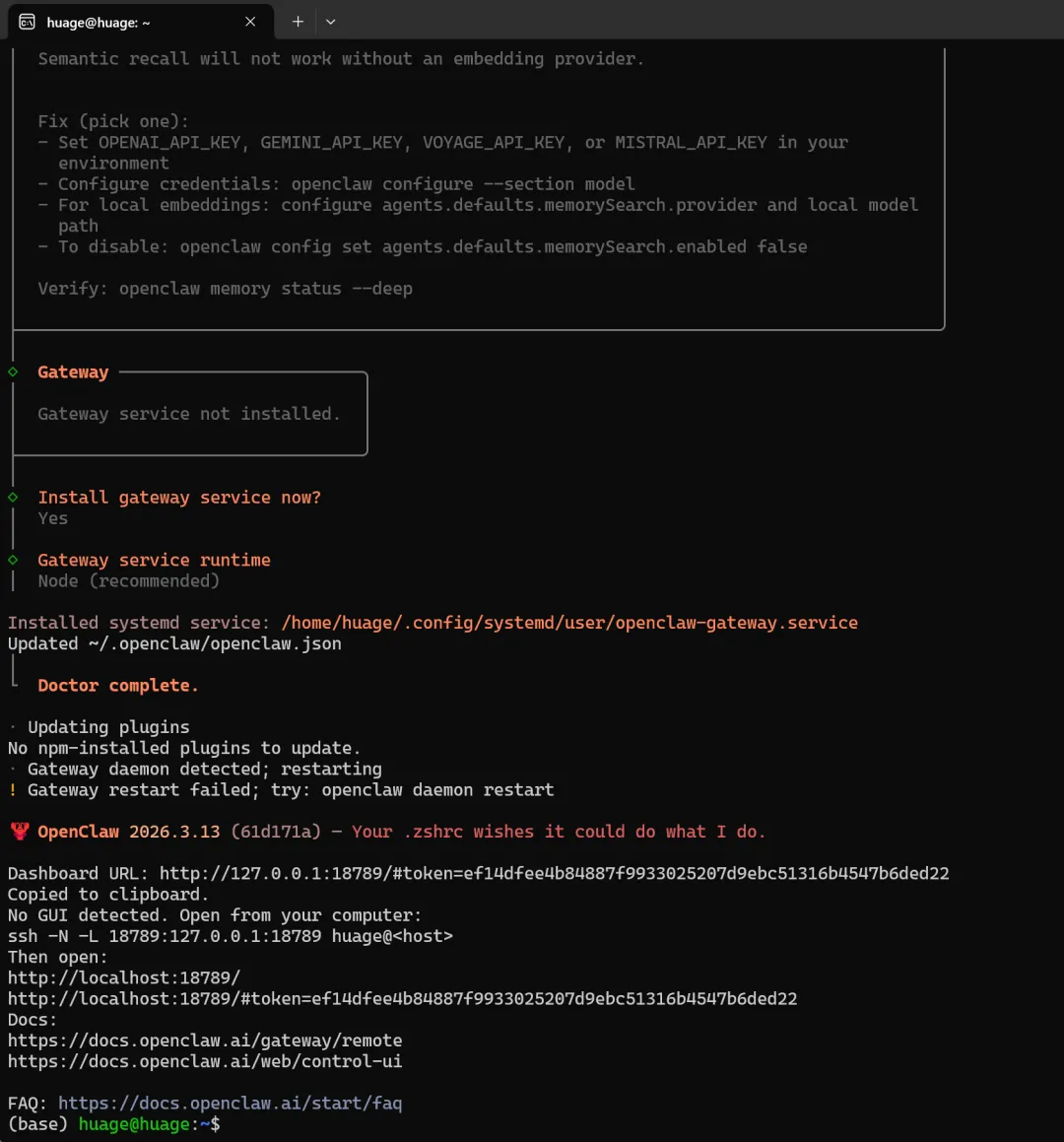
openclaw onboard --install-daemon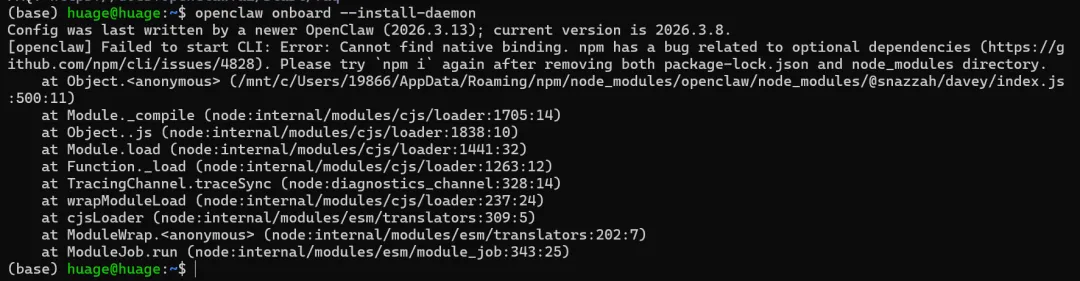
openclaw dashboardgit clone --depth=1 --no-checkout https://github.com/FreedomIntelligence/OpenClaw-Medical-Skills.git--depth=1 这是浅克隆:只下载最近一次提交附近的最新历史,不下载完整提交历史
cd OpenClaw-Medical-Skillsgit sparse-checkout init --coneskills 目录git sparse-checkout set skillsmain 分支,并把该分支内容检出到工作区git checkout main虽然仓库里有 869 个 skills,第一次没必要一股脑全装,先装一个最小可用组合。只安装部分 skills”的示例,比如临床 + 药物发现组合:clinical-reports、tooluniverse-drug-research、tooluniverse-pharmacovigilance、clinicaltrials-database、biomedical-search、tooluniverse-drug-drug-interaction
mkdir -p ~/.openclaw/skillsSKILLS=("clinical-reports""tooluniverse-drug-research""tooluniverse-pharmacovigilance""clinicaltrials-database""biomedical-search""tooluniverse-drug-drug-interaction")for skill in "${SKILLS[@]}"; docp -r OpenClaw-Medical-Skills/skills/$skill ~/.openclaw/skills/done
openclaw skills list实操
biomedical-search、clinicaltrials-database 这类 skill,在龙虾的对话框中可以直接给出如下指令:请帮我检索最近 3 年胃癌免疫治疗相关的高质量文献,优先 PubMed 和临床试验数据库,并给我一个中文总结。
或者:
请查询 HER2 阳性胃癌相关的正在招募中的临床试验,整理出 NCT 编号、研究阶段、干预药物和主要纳入条件。
场景 2:单细胞分析流程指导
如果你安装了 scanpy 或 bio-single-cell-preprocessing,可以直接给 agent 下这样的任务:
我有一个 10x 的 filtered_feature_bc_matrix 目录,请给我一个完整的 Scanpy 预处理流程,包括 QC、过滤、归一化、HVG、PCA、UMAP、Leiden 聚类,并解释每一步为什么这样做。
因为 scanpy 这个 skill 里面本来就写了从 10x / h5ad 数据读入,到 QC、normalize、HVG、PCA、neighbors、UMAP、Leiden、marker gene 和 cell type annotation 的完整流程;而 bio-single-cell-preprocessing 则更偏向预处理和版本兼容提醒。
场景 3:多步骤组合任务
真正体现 skill 价值的,往往不是单一步骤,而是串联多个技能。比如你可以这样问:
我现在有 4 个 scRNA-seq 样本,想先做双细胞去除,再做批次整合,然后聚类注释,最后对 T 细胞做伪时序分析。请先给我一套完整分析方案,再分别给出 Scanpy 和 Seurat 的代码模板。
因为仓库本身就把双细胞去除、批次整合、注释、轨迹分析拆成了不同 skill,这种组合式提问通常比泛泛问一句怎么做单细胞分析更容易得到成体系的回答。

零基础想学生信,看👇这个文章:
想学机器学习,看👇这个文章:
想系统学单细胞,看👇这个文章:
想系统学空间转录组,看👇这个文章:
欢迎关注 | 华哥科研平台

亲,写的这么辛苦,记得关注、点赞、转发哟!

 夜雨聆风
夜雨聆风