
OpenClaw Medical Skills 仓库中可用的单细胞与空间组学技能的完整生态系统。这些技能横跨三个贡献集合的 60 多项专业技能 —— gptomics bio-* 套件、组学与计算生物学层级以及 ClawBio 编排层 —— 赋能 AI Agent 执行单细胞分析生命周期的每个阶段:从原始计数矩阵导入、质量控制、聚类、轨迹推断和细胞间通讯,到空间转录组预处理、结构域检测、反卷积和多模态整合。
1
技术全景
单细胞与空间组学技能被组织为分层架构,这反映了从业者实际构建分析的方式。在底层,数据 I/O 与预处理技能负责格式转换与质量过滤。其上方的核心分析技能执行降维、聚类与注释。高级分析层增加了轨迹推断、通讯网络和扰动分析。最后,空间组学技能通过组织上下文处理扩展了单细胞方法,而编排技能则将所有内容串联为可复现的流水线。
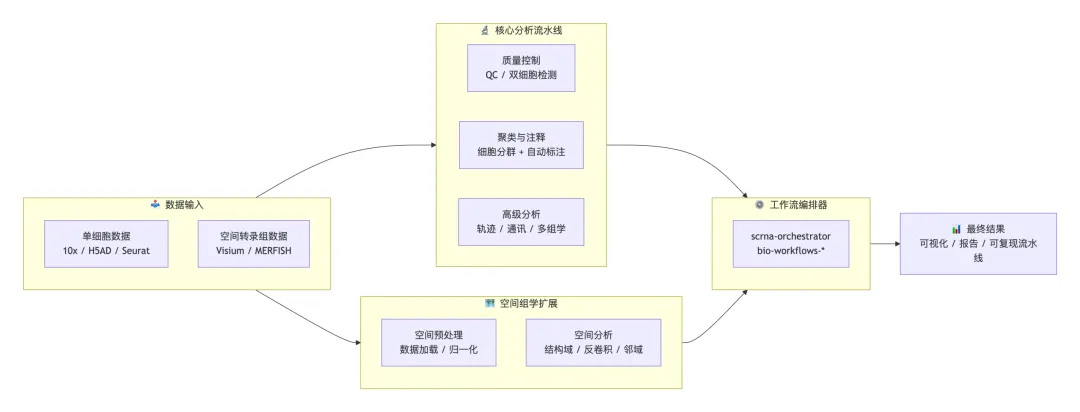
单细胞与空间组学技能来源于 OpenClaw 生态系统中三个不同的贡献仓库,每个仓库具有不同的设计理念和颗粒度层级。了解这些集合对于针对给定任务选择合适的技能至关重要。
2
数据基础:I/O、预处理与质量控制
每一个单细胞分析都始于加载数据并确保其符合质量标准。基础层提供了读取所有主要文件格式(.h5ad、.h5、10x Genomics 格式、Seurat 对象)的技能,执行基于 MAD 的质量过滤,检测并移除双细胞,并通过高变基因选择进行计数归一化。这些技能实现了 scverse 的最佳实践,并与 Scanpy 和 AnnData 生态紧密集成。

scanpy 技能作为大多数单细胞工作流的主要入口点,而 scvi-tools 则为批次校正(scVI)、细胞类型注释(scANVI)和多模态整合(MultiVI)提供了基于深度学习的替代方案。若要使用公共参考图谱,cellxgene-census 提供了对 6100 万+ 经策展细胞的直接查询访问,而无需下载单个数据集。
3
核心分析:聚类、注释与 scATAC-seq
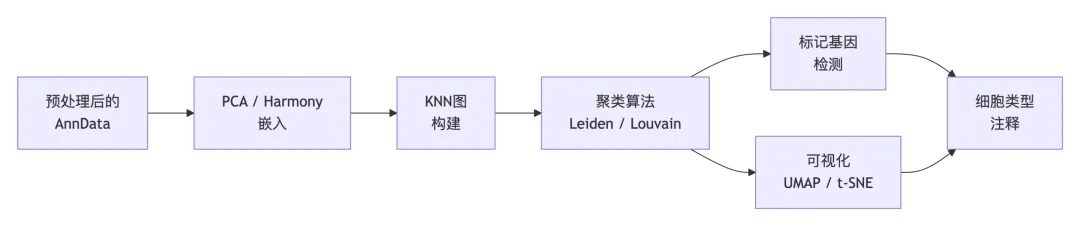
一旦数据经过预处理和批次校正,核心分析层便会处理细胞分组和身份分配的基本任务。聚类技能实现了带有分辨率优化的 Leiden/Louvain 算法,而注释技能则利用标记基因数据库和参考图谱进行自动化的细胞类型标记。scATAC-seq 技能通过峰调用和 TF 基序富集将这些能力扩展到了染色质可及性数据。
3.1 聚类
4
高级分析:轨迹、通讯与扰动
超越静态聚类,现代单细胞分析需要对细胞过程进行动态建模。高级分析层提供了用于伪时间轨迹推断(Monocle3、PAGA、Slingshot、scVelo)、配体-受体细胞间通讯(CellChat、NicheNet、CellPhoneDB)、基因扰动筛选分析(Perturb-seq/CROP-seq)以及多模态数据整合(WNN、MultiVI、GLUE)的技能。这些技能代表了单细胞计算生物学的前沿。

对于轨迹分析,gptomics 的 bio-single-cell-trajectory-inference 技能提供了经典方法(Monocle3、PAGA、Slingshot),而 Omics 的 single-trajectory 技能则增加了包含 velocity 耦合和命运评分等 OmicVerse 特有的工作流。在分析 RNA velocity 时,建议将 Omics 的 scvelo 与 gptomics 的 bio-single-cell-splicing 配对使用,以同时支持动态模型和稳态模型。
5
空间组学
空间转录组学代表了单细胞生物学的前沿,为基因表达数据增加了组织架构上下文。空间组学技能覆盖了包括 10x Visium、Visium HD、Slide-seq、Stereo-seq、MERFISH、seqFISH 和 STARmap 在内的多个平台的完整工作流。从数据加载和预处理,到空间结构域检测、细胞类型反卷积、空间统计和多组学整合,这些技能使 AI Agent 能够在原生组织上下文中分析基因表达。
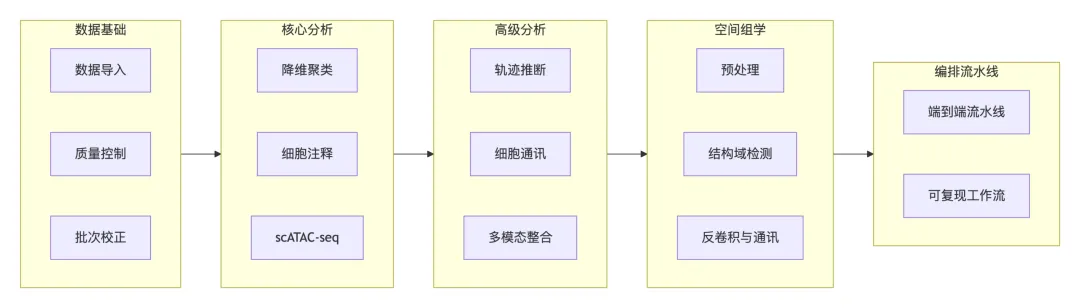
6
Bulk 到单细胞及相关工作流
本技能集合的独特优势在于包含了一套连接 Bulk 和单细胞分析范式的桥接技能。这些技能使 Agent 能够将 Bulk RNA-seq 反卷积为合成的单细胞数据,使用 Bulk 表达谱扩展 scRNA-seq 轨迹,并在两种模态之间迁移知识。当某条件缺失单细胞数据但存在 Bulk 转录组数据时,它们尤其具有价值。
7
端到端的可复现分析
为了实现端到端的可复现分析,ClawBio 编排层提供了元 Agent 技能,能够自动将请求路由至适当的专业子技能。这些流水线技能负责工作流规划、文件类型检测和可复现性导出,非常适合生产级分析。
8
完整技能总结
下表按分析阶段列出了所有单细胞与空间组学技能的完整清单。标有 ◆ 的技能来自 gptomics bio-* 集合,标有 ◇ 的技能来自组学与计算生物学集合,标有 ★ 的技能来自 ClawBio 编排层或 ToolUniverse。
8.1 单细胞核心
| 数据 I/O ◆ | bio-single-cell-data-io | |
| 数据 I/O ◇ | anndata | |
| 数据 I/O ◇ | cellxgene-census | |
| QC 与预处理 ◆ | bio-single-cell-preprocessing | |
| QC 与预处理 ◇ | single-preprocessing | |
| QC 与预处理 ◇ | single-cell-rna-qc | |
| 双细胞检测 ◆ | bio-single-cell-doublet-detection | |
| 批次整合 ◆ | bio-single-cell-batch-integration | |
| 框架 ◇ | scanpy | |
| 深度学习 ◇ | scvi-tools | |
| 聚类 ◆ | bio-single-cell-clustering | |
| 聚类 ◇ | single-clustering | |
| 注释 ◆ | bio-single-cell-cell-annotation | |
| 注释 ◇ | single-annotation | |
| 标记基因 ◆ | bio-single-cell-markers-annotation | |
| scATAC-seq ◆ | bio-single-cell-scatac-analysis | |
| 下游分析 ◇ | single-downstream-analysis |
8.2 轨迹与通讯
| 轨迹 ◇ | ||
8.3 空间组学
8.4 编排与 Bulk 桥接
9
选择技能指南
在不同集合的重叠技能之间做出选择可能具有挑战性。本决策指南将常见的分析需求映射到了最合适的技能。

安装与集成
要使用这些技能,请将它们安装到你的 OpenClaw 或 NanoClaw 工作区中。
#!/bin/bash# 单细胞核心SINGLE_CELL_CORE_SKILLS=("bio-single-cell-data-io""anndata""cellxgene-census""bio-single-cell-preprocessing""single-preprocessing""single-cell-rna-qc""bio-single-cell-doublet-detection""bio-single-cell-batch-integration""scanpy""scvi-tools""bio-single-cell-clustering""single-clustering""bio-single-cell-cell-annotation""single-annotation""bio-single-cell-markers-annotation""bio-single-cell-scatac-analysis""single-downstream-analysis")# 轨迹与通讯TRAJECTORY_COMM_SKILLS=("bio-single-cell-trajectory-inference""single-trajectory""scvelo""bio-single-cell-splicing""bio-single-cell-cell-communication""single-cellphone-db""bio-single-cell-metabolite-communication""bio-single-cell-perturb-seq""bio-single-cell-multimodal-integration""single-multiomics""bio-single-cell-lineage-tracing")# 空间组学SPATIAL_SKILLS=("bio-spatial-transcriptomics-spatial-data-io""bio-spatial-transcriptomics-spatial-preprocessing""bio-spatial-transcriptomics-spatial-neighbors""bio-spatial-transcriptomics-spatial-domains""bio-spatial-transcriptomics-spatial-deconvolution""bio-spatial-transcriptomics-spatial-communication""bio-spatial-transcriptomics-spatial-statistics""bio-spatial-transcriptomics-image-analysis""bio-spatial-transcriptomics-spatial-visualization""bio-spatial-transcriptomics-spatial-proteomics""bio-spatial-transcriptomics-spatial-multiomics""spatial-tutorials""single-to-spatial-mapping""tooluniverse-spatial-transcriptomics""tooluniverse-spatial-omics-analysis")# 编排与 Bulk 桥接ORCHESTRA_BULK_SKILLS=("scrna-orchestrator""bio-workflows-scrnaseq-pipeline""bio-workflows-spatial-pipeline""bio-workflows-multiome-pipeline""bio-workflows-multi-omics-pipeline""bio-orchestrator""bulk-to-single-deconvolution""bulk-trajblend-interpolation""bulk-deg-analysis""bulk-deseq2-analysis""bulk-combat-correction""bulk-stringdb-ppi""bulk-wgcna-analysis""tcga-preprocessing""gsea-enrichment")# 合并所有技能ALL_SKILLS=("${SINGLE_CELL_CORE_SKILLS[@]}""${TRAJECTORY_COMM_SKILLS[@]}""${SPATIAL_SKILLS[@]}""${ORCHESTRA_BULK_SKILLS[@]}")# 复制所有技能到 ~/.openclaw/skills/for skill in "${ALL_SKILLS[@]}"; docp -r OpenClaw-Medical-Skills/skills/"$skill" ~/.openclaw/skills/done
📌 往期回顾
第1期:开源医疗AI的“武器库”OpenClaw Medical Skills:869个技能,拿走不谢
第二期:OpenClaw Medical Skills 生信技能详解|质控与读长处理
第三期:OpenClaw Medical Skills 生信技能详解|变异检测与注释
第四期:OpenClaw Medical Skills 生信技能详解|差异表达与转录组学
📢 下期预告:《OpenClaw Medical Skills 生信技能详解|多组学整合》,敬请期待
 夜雨聆风
夜雨聆风