基因编辑有望解决农业、生物技术和人类健康领域的根本性挑战。源自微生物的基于 CRISPR 的基因编辑器虽功能强大,但移植到人类细胞等非原生环境时,往往存在显著的功能权衡。人工智能辅助设计为突破进化限制、生成具有最优特性的编辑器提供了强有力的替代方案。本研究中,我们利用基于大规模生物多样性训练的大型语言模型,成功实现了对人类基因组的精准编辑,开发出一款由人工智能设计的可编程基因编辑器。为达成这一目标,我们通过系统挖掘 26 兆碱基对的组装基因组和宏基因组,精心构建了包含超过 100 万个 CRISPR 操纵子的数据集。研究证实,我们的模型能够生成涵盖 CRISPR-Cas 家族的蛋白质簇,数量是自然界中发现的 4.8 倍,且能为类 Cas9 效应蛋白定制单向导 RNA(sgRNA)序列。多个生成的基因编辑器相较于原型编辑效应蛋白 SpCas9,表现出相当或更优的活性和特异性,而它们在序列上相差 400 个突变位点。最后,我们证实一款名为 OpenCRISPR-1 的人工智能生成基因编辑器具备碱基编辑兼容性。我们公开 OpenCRISPR-1,以促进其在研究和商业应用中的广泛、符合伦理的使用。









主讲老师在学术界具有多年的研究经历和应用经验,来自于国内顶尖课题组,从事基因组编辑技术与人工智能交叉融合的研究工作,相关工作成果已在Nature Biotechnology、Nature Plants、Trends in Biotechnology等国际知名期刊发表



第一天
1. 基因组编辑技术简述
1.1 基因组测序、编辑和读写时代及基因组编辑技术现状简述
2. 基因组编辑四代技术原理
2.1 四代基因组编辑技术发展历程
2.2 ZFN、TALEN和CRISPR/Cas系统的组成和工作原理
3. CRISPR/Cas系统的来源及分类
3.1 CRISPR/Cas系统的发现过程
3.2 CRISPR/Cas系统的适应性免疫原理
3.3 CRISPR/Cas系统的分类依据和类型
4. CRISPR/Cas系统介导的DNA编辑工具
4.1 CRISPR/Cas9基因编辑工具
4.2 CRISPR/Cas12a基因编辑工具
5. CRISPR/Cas系统衍生工具的发展
5.1 碱基编辑工具的组成、作用原理及其应用
5.2 引导编辑的作用机理、应用及其发展动态
6. CRISPR/Cas介导的基因调控、细胞成像和核酸检测技术
6.1 CRISPR/Cas介导基因调控技术的原理和工具组成
6.2 CRISPR/Cas介导细胞成像技术的原理和工具组成
6.3 CRISPR/Cas介导核酸检测技术的原理和工具组成
第二天
1. 脱靶效应及其检测
1.1 脱靶效应的检测方法:扩增子测序、全基因组测序、GUIDE-seq等
1.2 脱靶效应的规避方法
2. 基因编辑流程-以植物为例
2.1 靶位点sgRNA或crRNA的设计原则
2.2 表达盒设计和构建的方法
2.3 植物原生质体瞬时表达系统
2.4 基因编辑载体的遗传转化
2.5 基因编辑突变体的检测
3. 基因组编辑常用软件实操
3.1 靶位点设计软件Cas-Designer、BE-Designer、PE-Designer等
3.2 突变分析软件Cas- Analyzer、BE-Analyzer、PE- Analyzer
4. 基因组编辑技术在各领域的应用现状及前景
4.1 基因组编辑技术在基因治疗、免疫学、病毒诊断等方面的应用
第三天理论部分(人工智能+基因编辑背景)
1.深度学习概述
1.1. 深度学习的基础
1.2. 深度神经元网络的工作原理
1.3. 深度学习技术的发展趋势:自监督学习、迁移学习和少样本学习的进展
2.深度学习在基因编辑中的应用
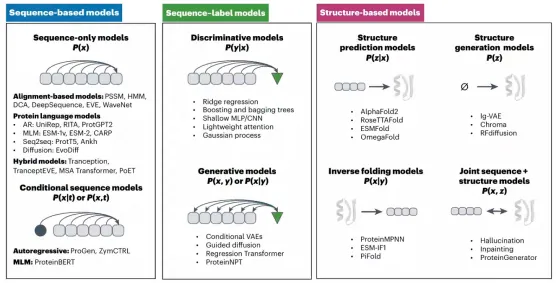
2.1. 基于监督学习的应用:序列标签模型
2.2. 零样本预测模型的应用:结构模型、大语言模型、多模态模型、
2.3. 少样本预测框架的应用(Design-Build-Test-Learn和Lab-in-the-loop范式)
3.深度学习在gRNA优化与设计中的应用
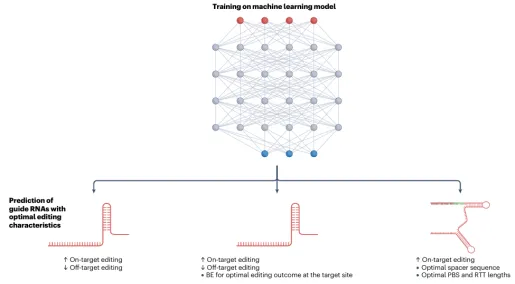
3.1. gRNA活性预测
3.2. 脱靶效应预测
3.3. gRNA预测模型介绍
4. AI辅助的蛋白定向进化在基因编辑中的应用
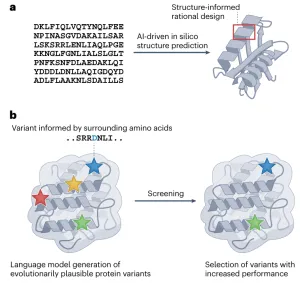
4.1. 蛋白定向进化的基本概念与实验方法
4.2 AI辅助的蛋白进化工具
4.3. AI与实验反馈的结合
5. AI蛋白质设计在基因编辑中的应用
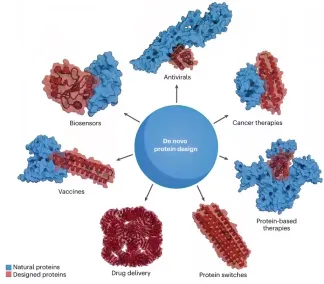
5.1. 蛋白质设计工具
5.2. 酶设计
5.3. binder设计
6.AI酶挖掘在基因编辑中的应用
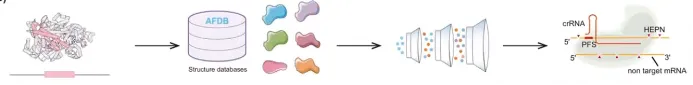
6.1. 基于大语言模型挖掘基因编辑酶
6.2. 基于结构比对挖掘基因编辑酶
第四天深度学习在基因编辑中的应用实操教学
1. 基础知识和环境搭建
1.1. GPU服务器登录
1.2. Linux基础知识
1.3. Python基础知识
1.4. 常用深度学习工具包介绍及安装
2.利用深度学习预测gRNA活性
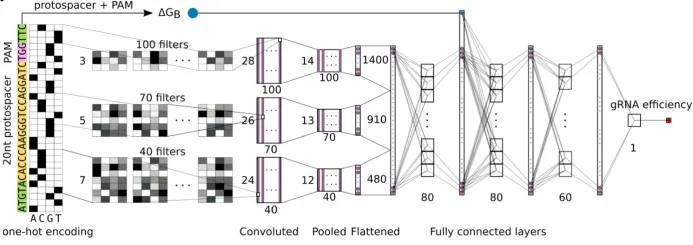
2.1. 配置深度学习环境,安装gRNA活性预测所需的工具
2.2. 高通量数据获取:公开数据集的介绍与使用
2.3. 数据集划分:训练集、验证集、测试集
2.4. 模型搭建与调试:深度学习模型架构设计(如CNN, RNN)
2.5. 模型性能评估:精度、召回率、F1分数等评估指标
2.6. gRNA活性预测:实际应用案例演示和预测结果的解读与应用
3.利用深度学习预测编辑活性
3.1. 环境配置:安装所需工具与库
3.2. 数据获取:编辑活性相关数据集清洗
3.3. 数据集划分
3.4. 模型搭建与调试
3.5. 模型性能评估
3.6. 编辑活性预测:预测结果的展示与解读
4.零样本蛋白进化工具AiCE实操
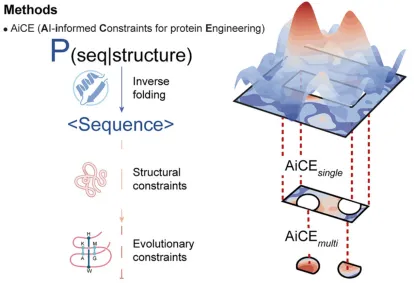
4.1. AiCE的原理与应用场景
4.2. 环境搭建
4.3. 逆折叠模型的使用:如何利用AiCE进行高活性突变预测;案例演示与实际操作
4.4. 应用实例:碱基编辑器的高效进化
5.少样本蛋白质定向进化工具EVOLVEpro实操
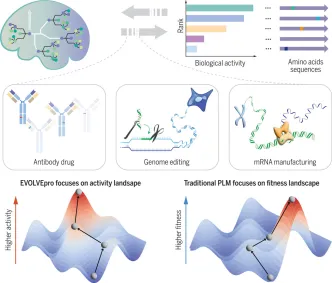
5.1. EVOLVEpro的背景与应用
5.2. 环境搭建与配置
5.3. 基于DMS数据的少样本微调
5.4. 基于实验数据反馈的少样本微调
5.5. 应用实例:Cas12f的高效进化
第五天基因编辑工具设计与挖掘案例复现
1. 设计MLH1 binder提高引导编辑编辑(PE)效率
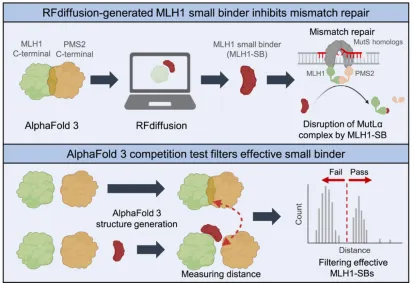
1.1. 背景知识:基于RFdiffusion + ProteinMPNN + AlphaFold的binder设计流程
1.2. 环境搭建与配置
1.3. 输入结构准备(AlphaFold预测)
1.4. 结构骨架生成:利用RFdiffusion进行结构采样与优化,生成蛋白质结构骨架
1.5. 序列设计:基于RFdiffusion生成的结构骨架,进行序列的优化设计
1.6.复合体结构预测验证:使用AlphaFold进行binder与目标蛋白复合体的结构预测,验证设计的复合体结构是否符合预期
1.7. 结果可视化:使用PyMOL进行结构和设计结果的可视化
2. Cas13抑制剂设计
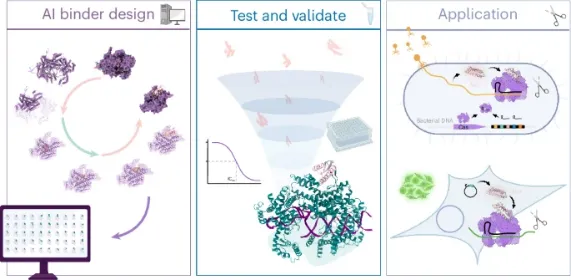
2.1. 背景知识:Cas13的结构与功能介绍
2.2. 输入结构准备
2.3. 蛋白质设计流程:结合RFdiffusion、ProteinMPNN与AlphaFold设计Cas13抑制剂
2.4. 设计结果分析和可视化
3.基于蛋白质语言模型挖掘新型CRISPR系统
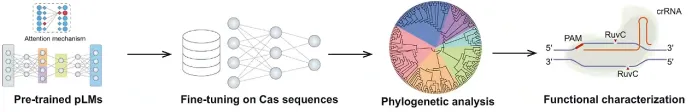
3.1. 蛋白质语言模型在酶挖掘中的介绍与流程
3.2. 序列数据库介绍与下载
3.3. 搜索(query)序列准备
3.4. 基于ESM语言模型挖掘Cas12家族基因编辑酶
4.基于三维结构挖掘新型CRISPR系统
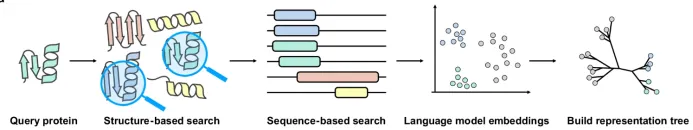
4.1. 结构比对的背景知识:结构比对的重要性与应用;比较不同结构比对工具的优缺点
4.2. Foldseek系列工具介绍:介绍Foldseek、Foldseek multimer、Folddisco、FoldMason等工具的基本原理和使用
4.3. 结构数据库介绍与下载:PDB,AFDB,ESM Atlas
4.4. 输入结构准备:准备用于比对的目标蛋白质结构文件
4.5. Foldseek网页版使用:演示如何使用Foldseek网页版进行结构比对;讲解如何理解输出结果并进行后续分析
4.6. Foldseek本地版使用:本地部署Foldseek并使用命令行工具进行比对
4.7. DALI和TM-align工具本地版使用:介绍DALI与TM-align工具本地版的安装与使用
4.8. 结构进化树构建:使用FoldMason构建蛋白质结构的进化树




培训费用
课程报名费用:
AI+基因编辑
公费价:每人每班¥6380元 (含报名费、培训费、资料费、提供课后全程回放资料)
自费价:每人每班¥6080元 (含报名费、培训费、资料费、提供课后全程回放资料)
报名费用可开具正规报销发票及提供相关缴费证明、邀请函,可提前开具报销发票、文件用于报销 。报名缴费后即可获得全套预习资料供大家提前预习


1、课程特色--全面的课程技术应用、原理流程、实例联系全贯穿
2、学习模式--理论知识与上机操作相结合,让零基础学员快速熟练掌握 3、课程服务答疑--主讲老师将为您实际工作中遇到的问题提供专业解答
授课方式:通过腾讯会议线上直播,理论+实操的授课模式,老师手把手带着操作,从零基础开始讲解,电子PPT和教程开课前一周提前发送给学员,所有培训使用软件都会发送给学员,有什么疑问采取开麦共享屏幕和微信群解疑,学员和老师交流、学员与学员交流,培训完毕后老师长期解疑,培训群不解散,往期培训学员对于培训质量和授课方式一致评价极高!

学员对于培训给予高度评价


引用本次参会学员的一句话:
 夜雨聆风
夜雨聆风