MacOS系统在安装过程中会遇到各种技术障碍。首先Autodock搭配使用的MGLTools为32位x86架构程序,M4为ARM64架构,需要进行Rosetta 2 转译;另外AutoDock Vina的Python绑定需要特定的编译环境和依赖库,而MacOS的系统环境配置比Linux更加复杂,安装难度比较大。对于没有编译基础的MacOS用户来说,使用Conda安装是最可靠的方法。它提供了预编译的二进制版本,完全避免了从源代码编译的复杂性。
安装步骤
一、安装Anaconda/Miniconda
1. 安装 Miniconda(轻量版,适配 M4 ARM64)
M4 为 ARM64 架构,需下载对应版本的Miniconda,避免x86版本兼容问题:
1)打开终端,执行以下命令下载Miniconda3(ARM64原生版):
curl -O https://repo.anaconda.com/miniconda/Miniconda3-latest-MacOSX-arm64.sh
2)运行安装脚本(全程按提示操作,建议默认选项):
bash Miniconda3-latest-MacOSX-arm64.sh
3)安装完成后,关闭当前终端并重新打开(使环境变量生效)。
4)在重新打开的终端中验证conda是否安装成功
conda --version
若输出conda版本号,说明安装成功;若仍报错,手动配置环境变量。
2. 手动配置conda环境变量(若自动配置失败)
1)编辑zsh的配置文件(.zshrc):
nano ~/.zshrc
2)在文件末尾添加以下内容(替换为你的Miniconda安装路径,默认路径如下):
# Miniconda3环境变量
export PATH="/Users/你的用户名/miniconda3/bin:$PATH"
3)查看Miniconda安装路径:find /Users -name "conda" | grep bin。
保存并退出:按Ctrl+O→回车→Ctrl+X。
使配置生效:
source ~/.zshrc
再次验证conda --version,确认生效。
conda --version
二、创建vina_env环境(适配AutoDock Vina)
conda create -n vina_env python=3.8
按提示输入a或y确认安装依赖
#激活环境
conda activate vina_env
三、安装AutoDock Vina
#一键安装AutoDock Vina
conda install -c conda-forge vina
这种方法会自动处理所有依赖关系,包括Boost库等必要组件。
四、验证是否安装成功
#在终端运行python
python
import vina
print(f"AutoDock Vina版本:{vina.__version__}")
如果输出Autodock Vina版本号,说明安装成功!
完成以上步骤后,即可在vina_env环境中运行AutoDock Vina,无需依赖32位的MGLTools。
1. RCSB PDB 数据库下载靶点蛋白结构文件
首先,从RCSB PDB 数据库(https://www.rcsb.org/)搜索靶点蛋白,找到适合自己目的的靶点蛋白结构,下载PDB文件(.pdb )。
进入数据库,主页上搜索框直接输入自己的靶点蛋白名称,如果输入后提示好几个相关结果,不用管,直接按enter键。
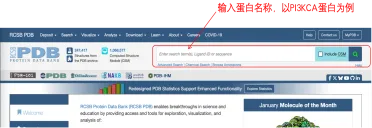
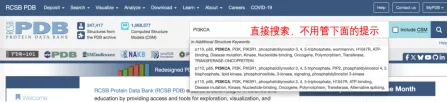
这一步蛋白名称一定要对,如果输入的名称搜索不到符合自己要求的结构,可以试试蛋白的其他名字。比如输入PI3KCA,搜索结果只有4个。
如果预期目的是说明药物通过激活PI3K-AKT信号通路发挥作用,那么需要的是PI3KCA的激活态结构,如果没有激活态结构,就选择apo态(无配体)结构。这四个结果都不能满足我的需求。
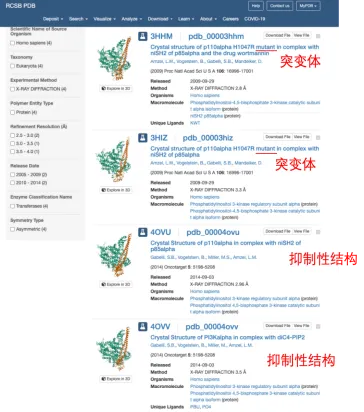
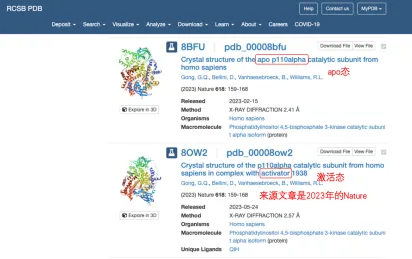
根据上面的搜索结果可以看出PI3KCA编码的蛋白是PI3K的alpha催化亚基(也叫p110alpha),所以重新搜索p110alpha,match到了117个蛋白结构,可以通过旁边的参数栏进一步缩小范围。然后寻找符合自己要求的蛋白结构。
大部分从简介就可以判断是否符合需求,如果简介看不出来就要点进去查看详细信息,会给出结构的来源,有实验验证的就会给出参考文献。
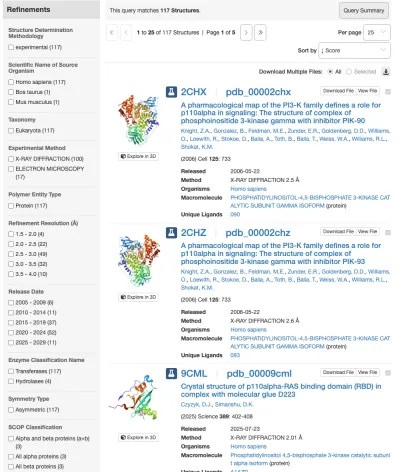
在这里面找到的8OW2是符合要求的激活态构象,简介就能看到结构来源是2023年的Nature上发表的,说明可信度比较高,虽然分辨率为2.57Å,稍微超出2.5Å的范围,但是差别不大,所以我还是选择这个结构。
确定好了选择的蛋白PDB ID后直接下载该结构的PDB文件(.pdb格式),命名protein.pdb。

 夜雨聆风
夜雨聆风