软件介绍 | BABAPPAlign 新型多序列比对程序

1. 软件基本信息
软件名称:BABAPPAlign
开发团队:Krishnendu Sinha
发表期刊:《Bioinformatics》
发表时间:2026 年 4 月
开源仓库:https://github.com/sinhakrishnendu/BABAPPAlign
软件 DOI:10.1093/bioinformatics/btag189
开发语言:Python

2. 研究背景
多序列比对是生物信息学研究的核心基础工具,广泛应用于蛋白保守结构域分析、物种进化分析、同源序列研究等领域。目前主流 MAFFT、Clustal 等传统比对软件,均依赖 BLOSUM62 等固定静态氨基酸替换矩阵打分,无法根据不同蛋白序列的局部特征、上下文信息动态调整打分规则,在远缘同源序列和复杂蛋白序列比对中,结果精准度存在明显短板。
3. 核心原理与技术特色
-
创新 AI 打分机制摒弃传统固定替换矩阵,搭载残基级机器学习打分模型,结合蛋白质语言模型提取的序列嵌入特征,实现上下文自适应动态打分,贴合真实氨基酸进化规律。经典算法结合优化采用渐进式多序列比对策略,保留精准的仿射空位动态规划算法,兼顾运算稳定性与空位比对准确性。特色比对模式内置密码子感知比对功能,可同时适配蛋白序列与编码基因序列联合比对,满足多组学联合分析需求。轻量化开源设计基于Python 编写,代码开源透明,部署简单,支持本地运行与个性化二次开发,可轻松嵌入生信分析流程。 -
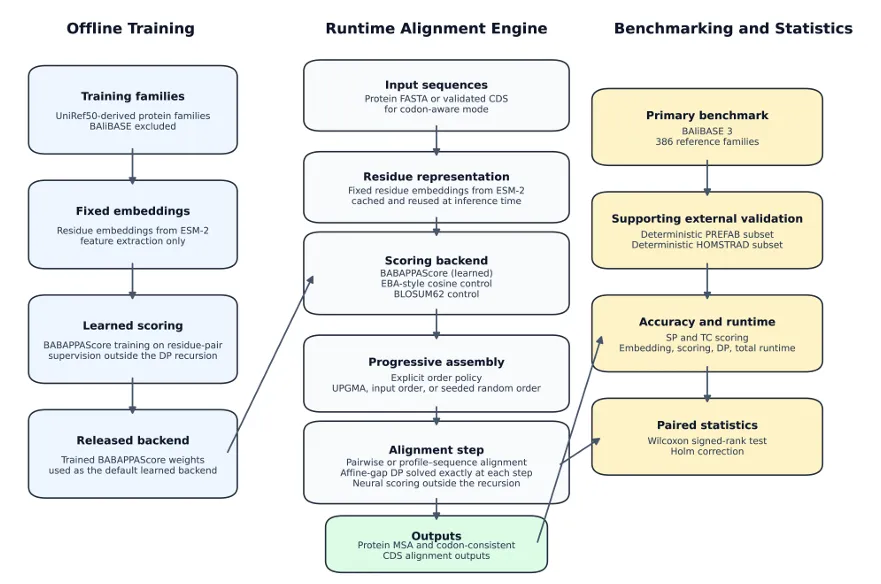
4. 性能优势
以 BAliBASE、PREFAB、HOMSTRAD 等国际通用比对标准数据集开展测试验证:比对效果显著优于 BLOSUM62 传统矩阵打分模型;相较于同类型余弦比对算法,序列匹配度、保守区识别能力大幅提升;整体综合比对精度超越主流经典软件 MAFFT,尤其适用于低同源、远距离蛋白序列分析。
5. 安装与使用
# 简单的安装与使用pip install babappalignbabappalign --helpbabappalign input.fasta# 参数--i interactive mode--mode {protein,codon}--gap-open FLOAT--gap-extend FLOAT--device {cpu,cuda}
6. 主要应用场景
-
蛋白质家族多序列比对、保守功能位点挖掘; -
动植物、微生物物种系统发育分析与进化树构建; -
编码基因与对应蛋白序列联合比对研究; -
远缘同源蛋白鉴定、突变位点关联性分析; -
生信算法研究、多序列比对方法 benchmark 测试。
7. 总结
BABAPPAlign 是一款深度学习赋能的新型多序列比对引擎,打破传统比对软件的打分局限,依托蛋白大模型与机器学习提升比对灵敏度与准确度,同时兼容常规蛋白比对与密码子联合比对需求。软件完全开源、部署便捷,综合性能优于主流传统工具,为复杂蛋白序列、低同源序列的精准比对提供全新高效的分析选择。



 夜雨聆风
夜雨聆风




