实打实的公益课来了,空间组学五大AI插件矩阵首发布+每周常规公开课
-
工具门槛高:原生 QuPath 操作复杂,上手难度大
-
信号干扰强:多通道下自荧光与背景噪声混杂,真实信号难以辨别
-
分析精度低:单一平均荧光强度阈值,无法应对复杂细胞形态的阴阳性区分
-
空间信息难量化:海量细胞拓扑坐标数据,缺乏有效的空间量化分析方法

Part.01
-
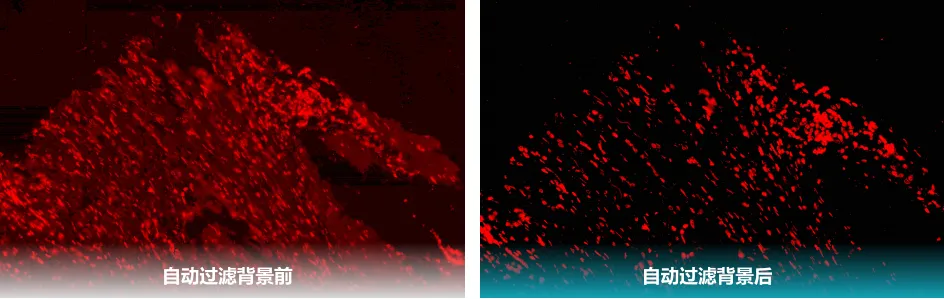
【核心价值】:针对多轮染色产生的自荧光背景及漂移,实现一键智能降噪。自动修复元信息,将各类复杂 TIF 标准化为 QuPath 深度兼容格式。
-
【应用】:告别手动调参的痛苦,降低内存占用,为下游分析提供“零污染”信号。
-
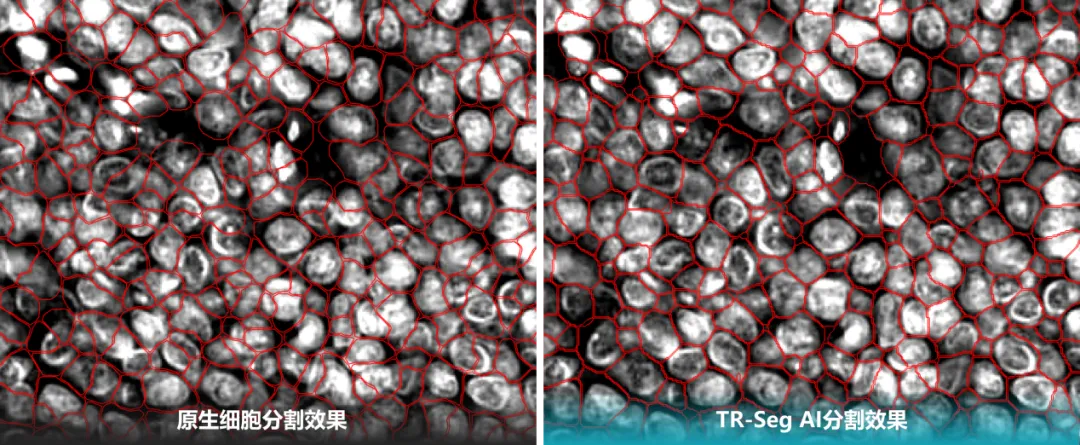
【核心价值】:StainSync支持 H&E、IHC 与 mIF 的自动几何配准;TR-Seg采用深度学习模型,精准拆解致密组织中重叠、挤压的细胞边缘。
-
【应用】:彻底解决“细胞分不开、图像叠不上”的硬伤,实现细胞级精度的对齐分析。
-
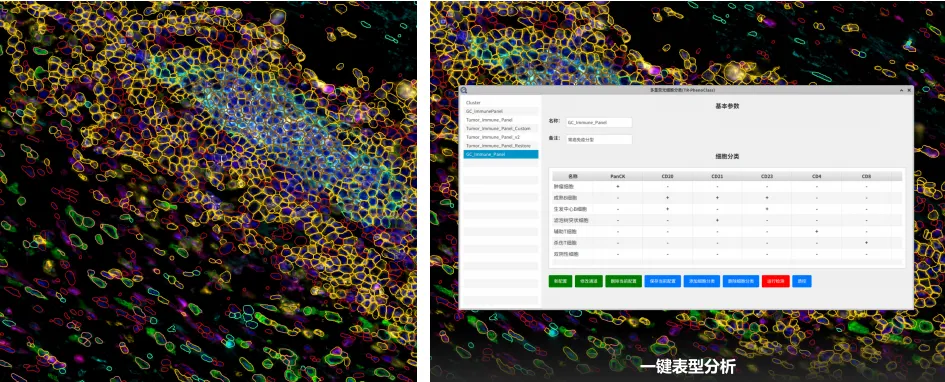
【核心价值】:模拟病理专家肉眼逻辑,结合“膜染色形态特征+荧光强度”进行双重判定,而非死板的数值阈值。
-
【应用】:即使在背景复杂的微环境中,也能清晰区分细胞阴阳性,准确度较传统方法提升数倍。
-
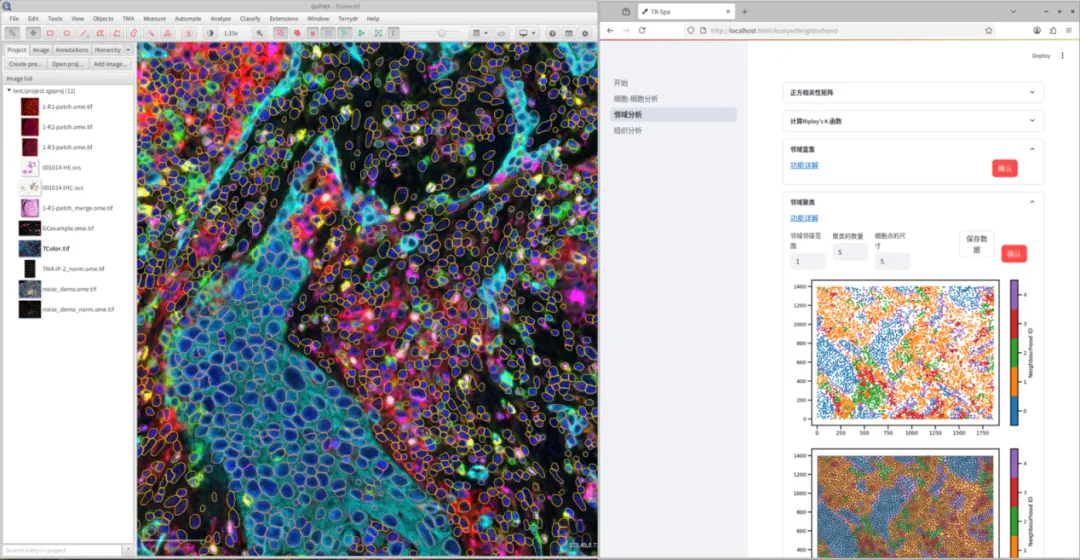
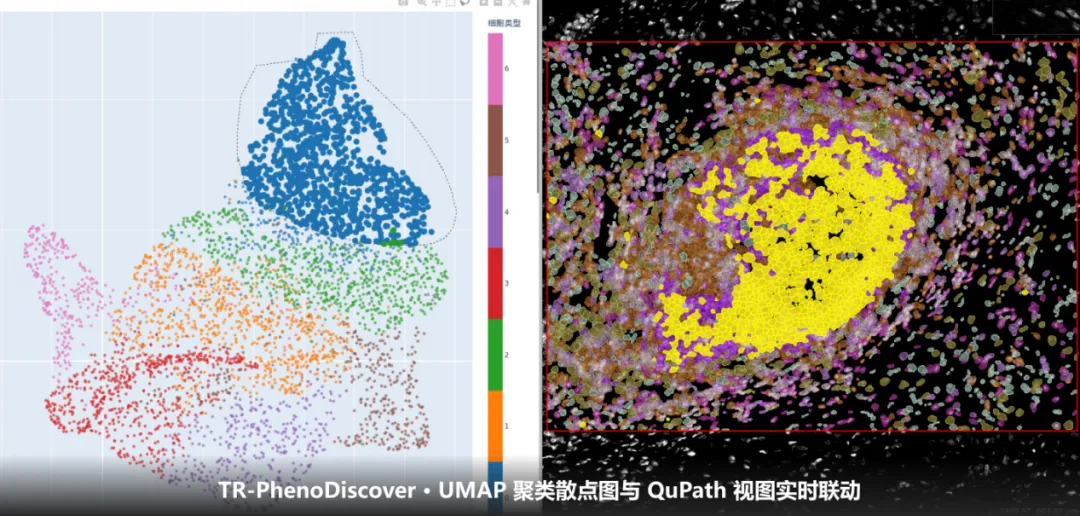
【核心价值】:TR-PhenoDiscover实现 Leiden 自动聚类与 UMAP 互动映射;Spa 插件一键计算免疫细胞浸润深度、排斥/聚集指数及邻域(Niche)组成。
-
【应用】:快速生成符合顶级期刊要求的空间统计图表,揭示肿瘤微环境中的“位置决定论”。
-
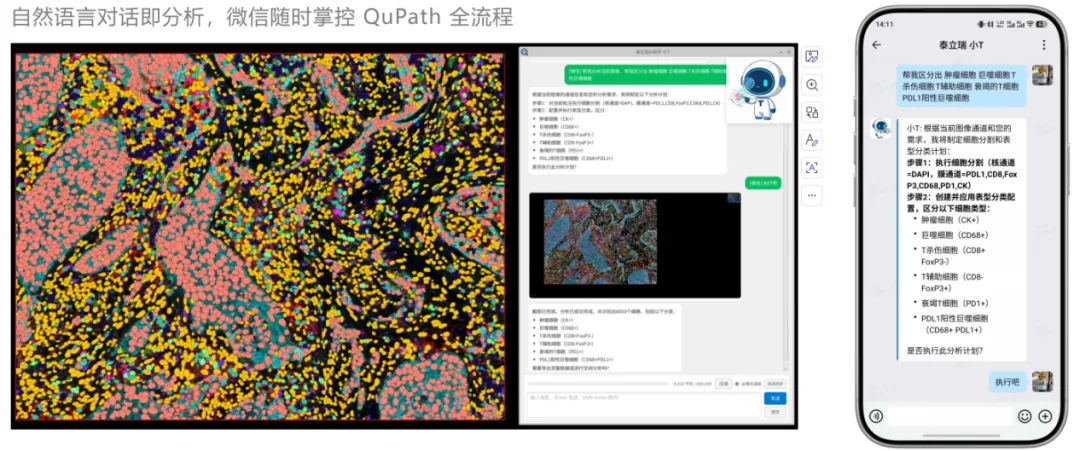
【核心价值】:基于大模型,自然语言驱动的自动化分析流程。
-
【应用】:消除编程门槛,让每一位病理医生和生物学家都能随心所欲地自动化批处理。

Part.02
-
0-30min:极致预处理。TR-NoiseX 解决数据“脏、乱、偏”问题,AI 助手快速搭建管线。
-
30-60min:AI 驱动识别。重点演示PhenoClass 深度学习细胞分类能力,展示如何“秒杀”传统阈值法。
-
60-100min:洞悉空间。利用Spa 插件提取空间异质性指标,完成从图像到统计图的转化。
-
100-120min:互动答疑。
Part.03

Part.04
-
一周免费试用(云端):获得全套 QuPath 插件的一周免费全功能试用权限
-
科学家一对一:泰立瑞资深科学家团队将针对您提交的项目提供一对一的技术支持与分析指导
-
实战案例展示:优秀项目将作为后续每周实战课的案例进行复盘演示(保护数据隐私前提下)
如下是往期内容:
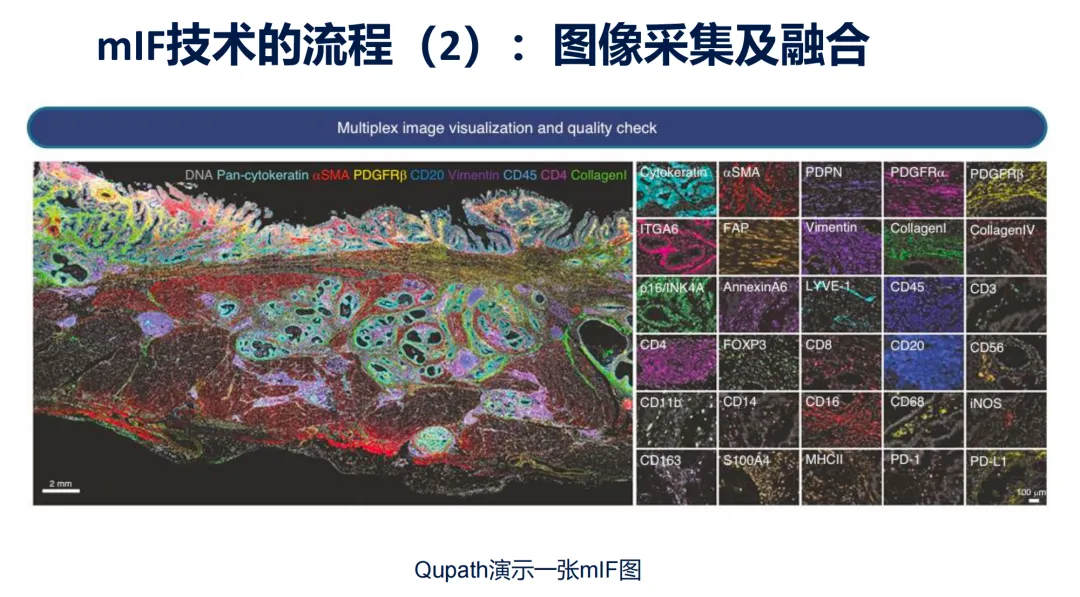
考虑到很多小伙伴对病理、多色免疫荧光(mIF)和空间生物学的分析存在困难,我们上次做的QuPath病理分析公益课程,已在B站同步了部分回放,后续全部课程内容这周会更新完(共5节课,每次时长约2h);
包含课程数据分析过程中的难点、重点和细节分享、以及课后的提问和讨论,都是大家经常遇到的问题;
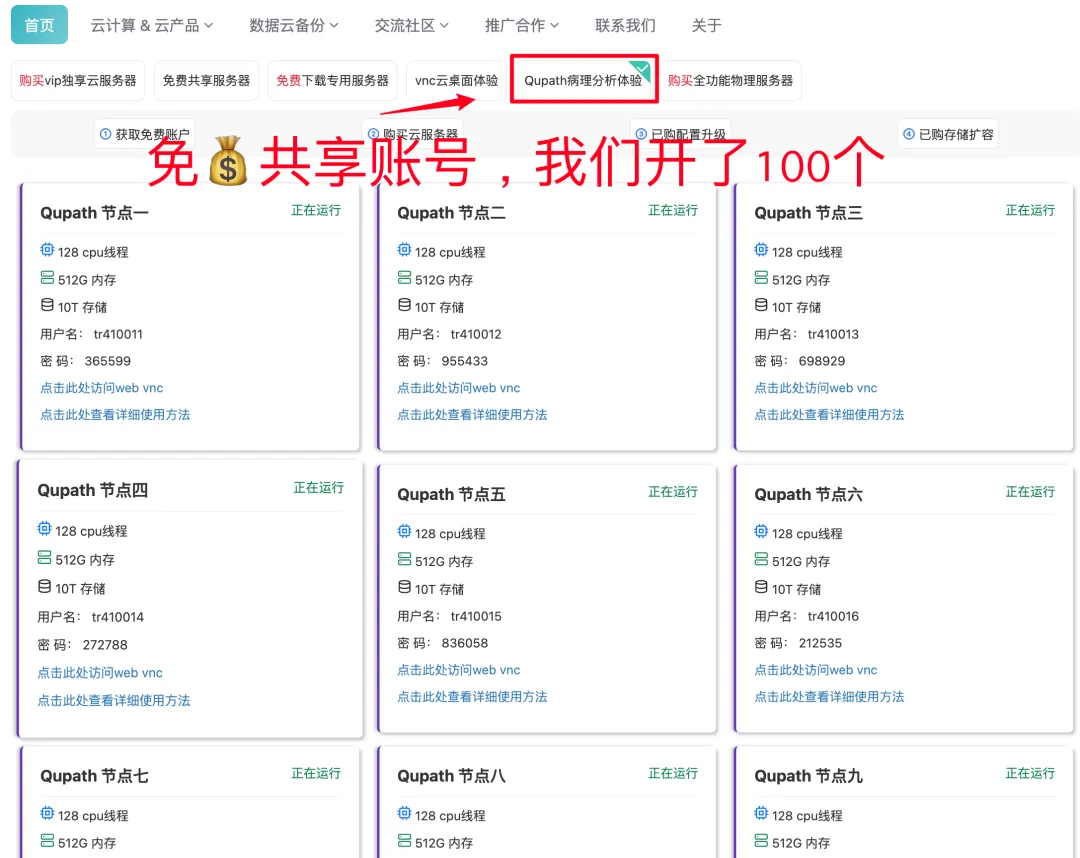
体验服务器下周会再次开放使用,如需高难度病理分析科研服务和Qupath软件插件使用或近Qupath病理分析交流群可以联系下方助手:

https://vip.r-py.com/?type=10
使用说明(云笔记):https://notes.r-py.com/004-qupath/qupath001-%E5%BC%80%E5%A7%8B_%E6%9C%8D%E5%8A%A1%E5%99%A8%E5%9F%BA%E7%A1%80_.html
 夜雨聆风
夜雨聆风




