一文读懂AI编程助手的“系统提示词”
写在前面
现在的生信领域没AI已经完全无法干活了。西柚云结合大家对AI编程以及日常运行任务时的实际需求,推出了AI无缝接入Rstudio≈言出法随帮助大家做到在Rstudio中直接调用AI进行对话、代码修改、代码注释,结合分析环境(足够支持你完成硕博生涯的共享服务器)。几乎能做到数据分析的言出法随,反馈的代码直接就能在Rstudio里跑。
还通过Codex插件实现AI辅助编程,实现覆盖本地与远程两种使用场景,提升科研工作效率。此外,我们还推出openClaw+服务器+微信接入=拥有私人生信助理,可实现在服务器上部署专属OpenClaw。
今天为大家分享:如何设置全局系统提示词——让AI记住你的偏好,无需每次重复交代。使用过程中有任何问题欢迎联系:

 可免费接入小龙虾和其它AI的服务器,可参考:
可免费接入小龙虾和其它AI的服务器,可参考:
系统提示词:AI的入职手册
系统提示词是给AI的“入职手册”——把编码风格、工作规范、个人偏好写成文件,让AI永久记住,无需每次重复交代。Claude用CLAUDE.md和Memory,Codex用AGENTS.md,本质都是这个作用。
这两个文件都是系统提示词配置文件,作用是给AI设定固定的“行为规则”和“工作偏好”。

Claude Code记忆体系
Claude实际上有两套“记忆”机制,分工不同:

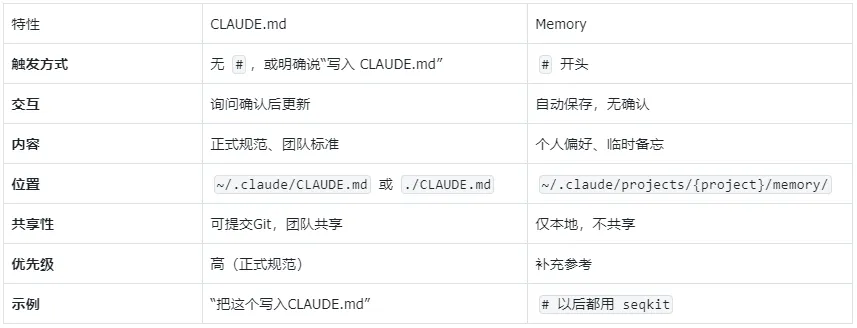
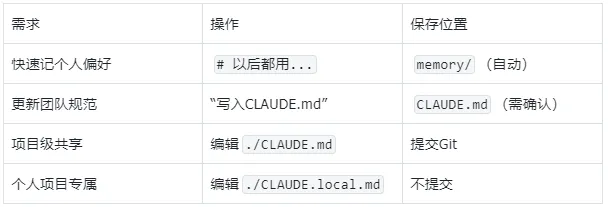
关键区别:# 是Memory系统的触发符。加 # 快速记个人偏好,不加 # 更新正式规范。
CLAUDE.md
|
|
|
|
|
|
~/.claude/CLAUDE.md |
|
|
|
./CLAUDE.md |
|
|
|
./CLAUDE.local.md |
|
|
|
./src/CLAUDE.md |
|
加载优先级:越具体的层级越优先
生效顺序(从基础到优先):用户级 ~/.claude/CLAUDE.md↓项目级 ./CLAUDE.md → ./CLAUDE.local.md↓子目录级 ./src/CLAUDE.md → ./src/CLAUDE.local.md
1️⃣ CLAUDE.md示例
# 生信分析规范## 代码风格- Python脚本使用4空格缩进- 变量名用小写下划线(如'gene_count')- 函数必须添加docstring说明参数和返回值## 数据处理- 原始数据务必保留备份- 中间结果输出到'tmp/'目录- 最终结果输出到'results/'目录并记录版本## 常用工具- 序列处理:seqtk, seqkit- 比对:STAR, minimap2- 定量:featureCounts, Salmon## 交互规范- 分析前确认基因组版本(hg38/hg19/mm10)- 重要操作前告知可能的风险
2️⃣ 验证CLAUDE.md生效
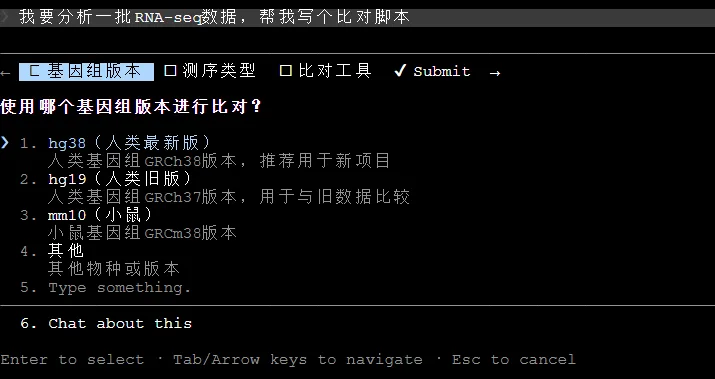
“我要分析一批RNA-seq数据,帮我写个比对脚本”
Claude没有直接写代码,而是先弹出交互式选项询问基因组版本,这正是我们在规范里要求的。界面上还能看到“测序类型”和“比对工具”的待确认项,说明它确实在按“重要操作前告知风险”的规矩来。等这些都选完,它会输出符合我们代码风格的脚本,比如4空格缩进、变量用小写下划线、函数带上docstring等细节。
3️⃣ 更新CLAUDE.md
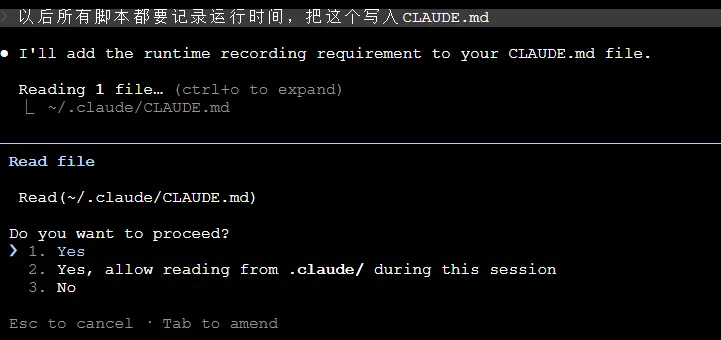
“以后所有脚本都要记录运行时间,把这个写入CLAUDE.md”
Claude会读取现有文件并询问是否确定添加和更新,执行Yes确认后会自动追加新规范
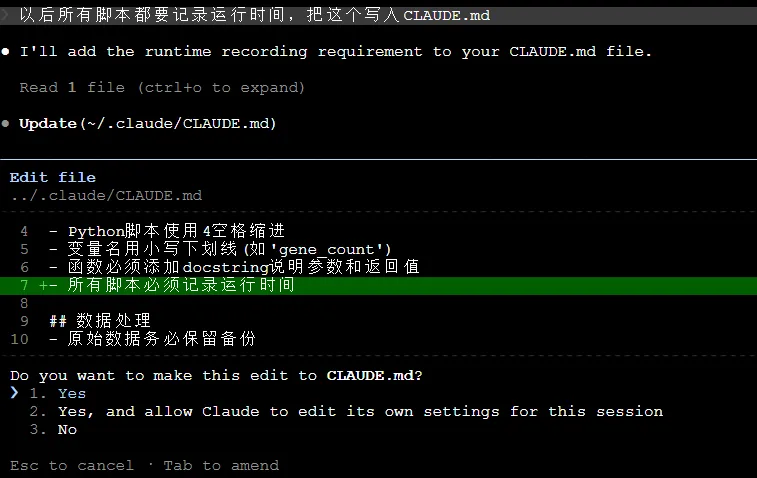
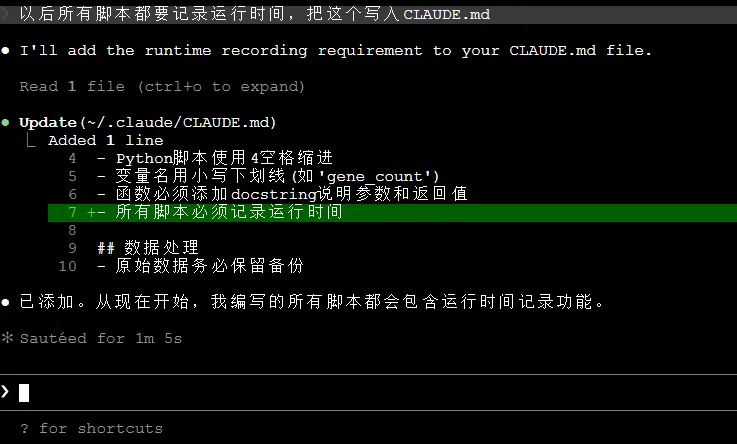
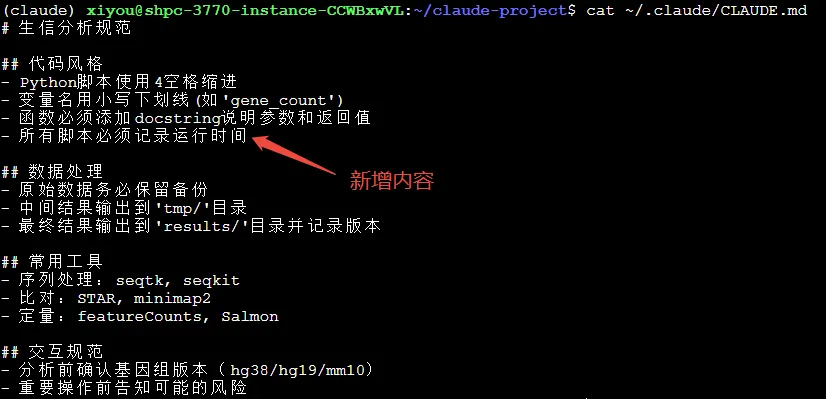
确认后可以看到CLAUDE.md文件已有新添加内容
Memory
1️⃣ 什么是Memory
Memory保存在项目专属的目录中,每个项目独立:
~/.claude/projects/{project-name}/memory/├── MEMORY.md # 记忆索引,列出所有记忆├── fasta_preference.md # 具体记忆文件 1├── scrna_preference.md # 具体记忆文件 2└── ...
每个记忆文件采用YAML前置元数据+Markdown主体内容的标准格式:
---name: fasta-preferencedescription: FASTA文件处理的工具偏好type: feedback---# FASTA 处理偏好## 工具选择- 优先使用 `seqkit` 处理 FASTA 文件- 不再使用 `seqtk`## 常用命令- 统计序列数:`seqkit stats input.fa`- 提取长序列:`seqkit seq -m 1000 input.fa > output.fa`- 格式转换:`seqkit fq2fa input.fq.gz -o output.fa`
# Memory Index- [FASTA Preference](fasta-preference.md) - FASTA文件处理的工具偏好- [Plotting Style](plotting-style.md) - 绘图风格和配色方案
cat ~/.claude/projects/{project}/memory/MEMORY.md
-
由于Memory设计为轻量级备忘,没有精细的管理界面,需要手动删除:
# 删除特定记忆文件rm ~/.claude/projects/{project}/memory/fasta-preference.md# 或清空整个记忆目录rm -rf ~/.claude/projects/{project}/memory/*
2️⃣ 什么时候用Memory
-
突然想到一个顺手的工具组合
-
发现某个参数设置特别适合你的数据
-
临时记住一个常用的分析流程
-
任何不想写进正式文档的小习惯
3️⃣ 如何使用Memory
只需在对话中以#开头:
# 以后处理fasta文件都用seqkit而不是seqtk
Claude会立即记录,没有确认对话框,不打断你的思路
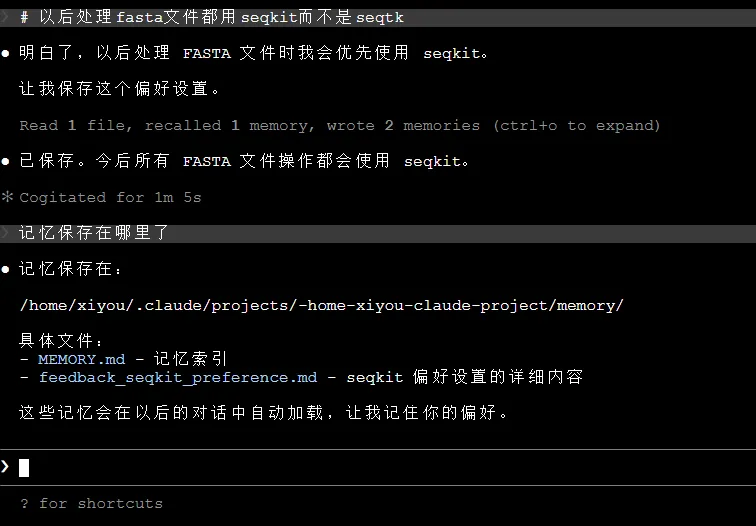
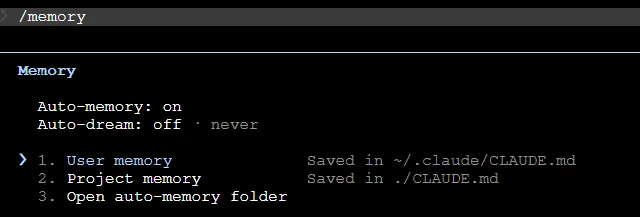
输入/memory可以查看和管理记忆系统:
-
查看Auto-memory状态(on/off)
-
查看User memory和Project memory的保存位置
-
打开auto-memory文件夹快速浏览(终端无图形化界面时不支持打开)
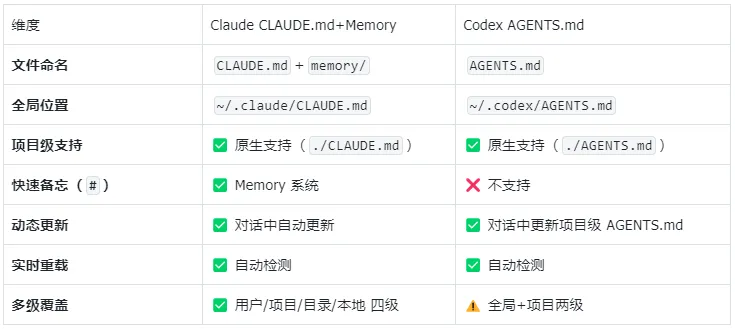
双机制对比

Codex记忆体系
什么是AGENTS.md?
Codex使用AGENTS.md作为系统提示词文件,作用与Claude的CLAUDE.md类似。Codex在开始任何工作前都会读取AGENTS.md,通过分层配置确保每个任务都按统一规范执行。它采用的分层设计可以简单理解为:越靠近你当前位置的配置,优先级越高
Codex启动时会构建一条“指令链”,从两个层面收集规则:
项目层面:从项目根目录一路向下找到你当前的工作目录,每层都可能有配置。Codex会把沿途找到的文件拼在一起,后出现的内容覆盖前面的。
所以实际优先级是:
当前目录 > 父目录 > 项目根目录 > 全局配置 > Codex默认文件结构:
~/.codex/├── AGENTS.md # 全局个人指导├── config.toml # 模型、提供商等配置└── skills/ # 项目级Skill(可选)你的项目/├── AGENTS.md # 项目级规范(最优先)└── .codex/└── AGENTS.md # 替代位置
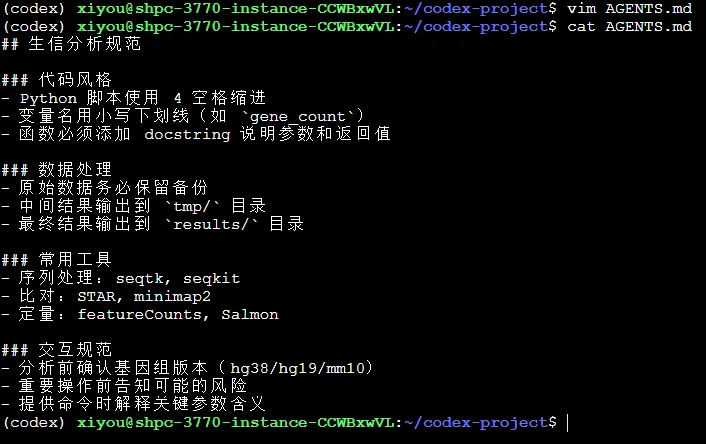
AGENTS.md示例:
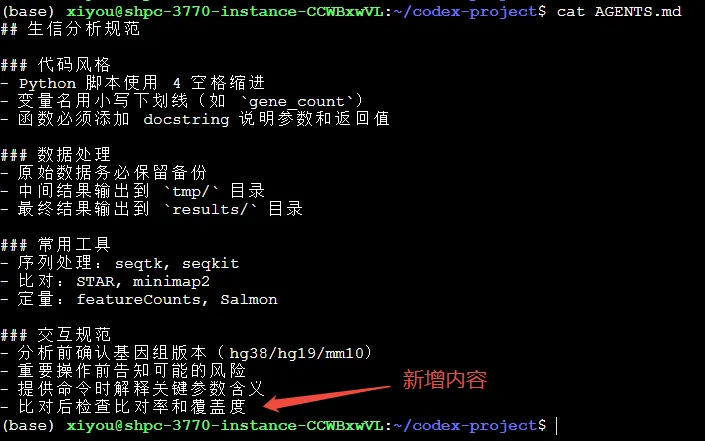
## 生信分析规范### 代码风格- Python 脚本使用 4 空格缩进- 变量名用小写下划线(如 `gene_count`)- 函数必须添加 docstring 说明参数和返回值### 数据处理- 原始数据务必保留备份- 中间结果输出到 `tmp/` 目录- 最终结果输出到 `results/` 目录### 常用工具- 序列处理:seqtk, seqkit- 比对:STAR, minimap2- 定量:featureCounts, Salmon### 交互规范- 分析前确认基因组版本(hg38/hg19/mm10)- 重要操作前告知可能的风险- 提供命令时解释关键参数含义
如何使用AGENTS.md
# 在项目目录创建(推荐)vim ~/codex-project/AGENTS.md# 或者全局配置vim ~/.codex/AGENTS.md
启动Codex,输入:
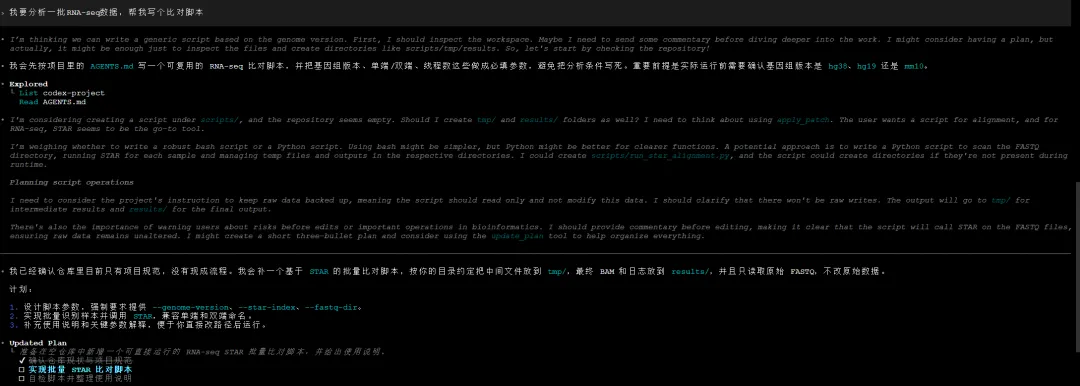
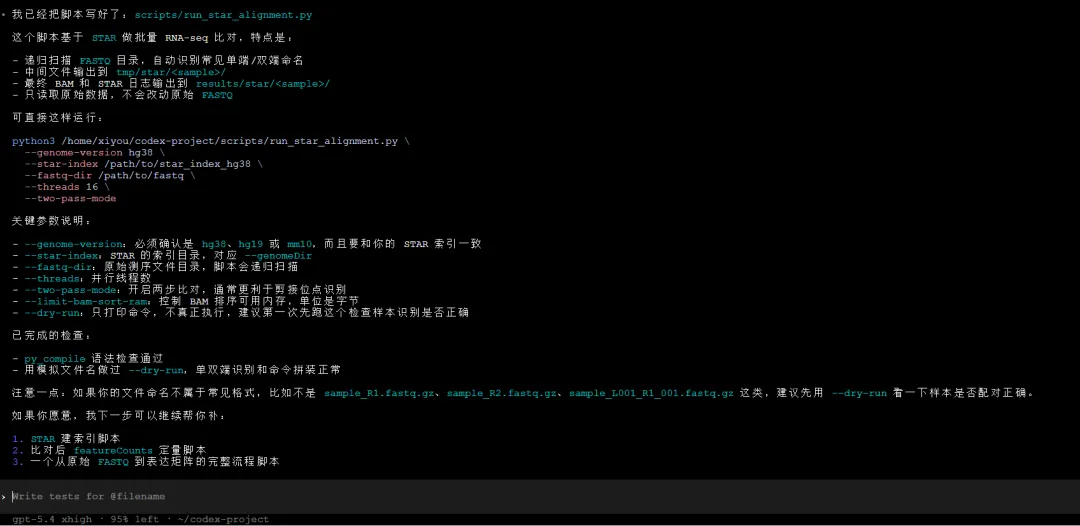
“我要分析一批RNA-seq数据,帮我写个比对脚本”
Codex会根据加载的规范来执行,按照规范询问基因组版本、测序类型等必填参数,而不是直接开始写代码
更新机制
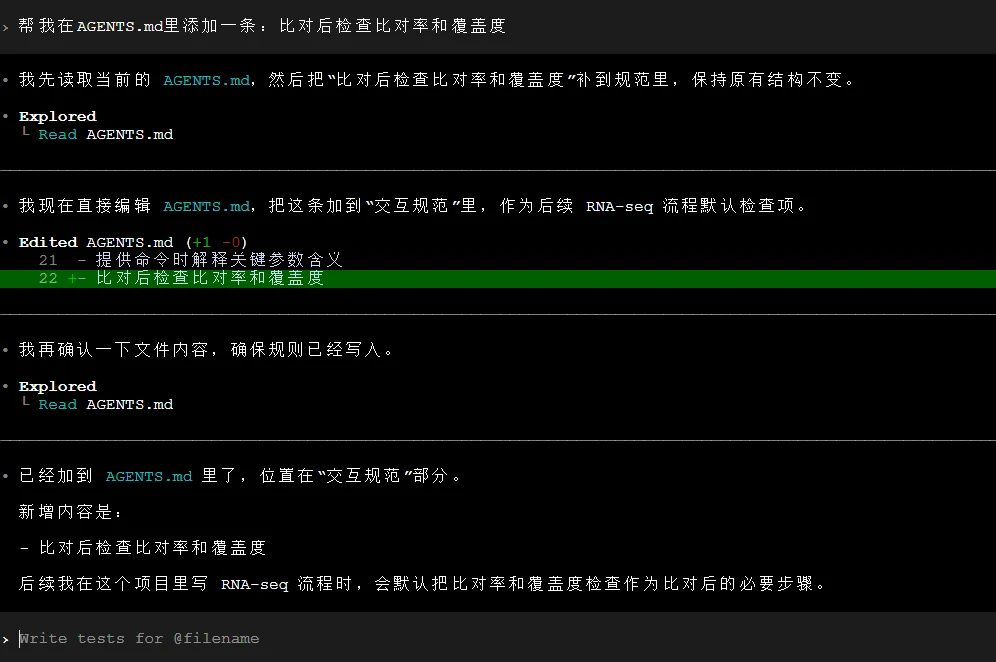
“帮我在AGENTS.md里添加一条:比对后检查比对率和覆盖度”
Codex会读取当前AGENTS.md,在“质控要求”部分追加新规范,经确认后完成更新。
边界说明:
-
只能更新项目级AGENTS.md,不能覆盖系统或开发者层面的更高优先级指令
-
如果新增规则与现有规范冲突,Codex会指出冲突点,按可执行的方式处理
也可以手动编辑 vim AGENTS.md,实时生效。

核心对比

使用建议
Claude用户
Codex用户
-
项目规范:创建项目级AGENTS.md(推荐)
-
全局配置:~/.codex/AGENTS.md(目前不生效,建议放~/AGENTS.md作为父目录继承)
-
快速切换:创建项目级Skill(./.codex/skills/)
-
动态更新:对话中直接让Codex修改AGENTS.md
-
注意:Codex没有Memory系统,临时偏好需要写入AGENTS.md或创建Skill

结语
西柚云在售算力
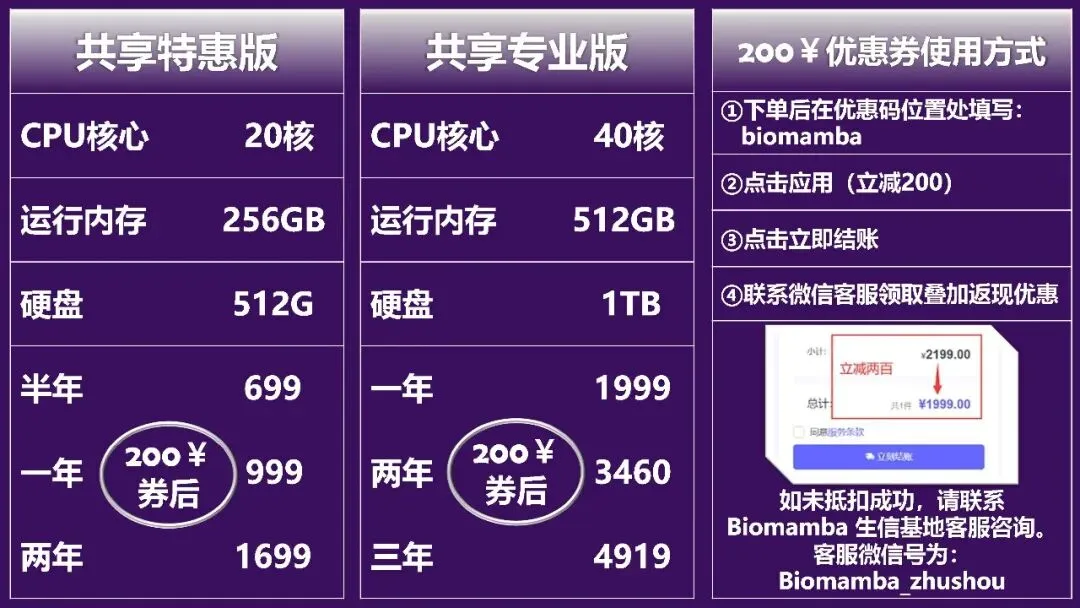
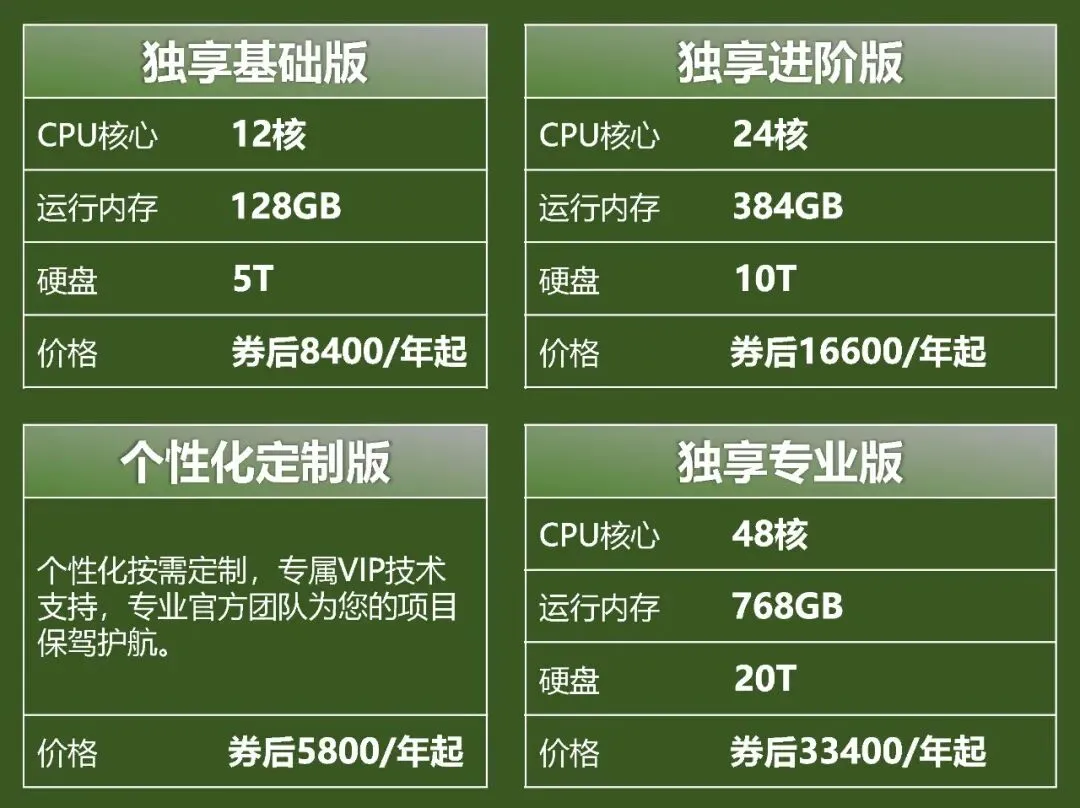
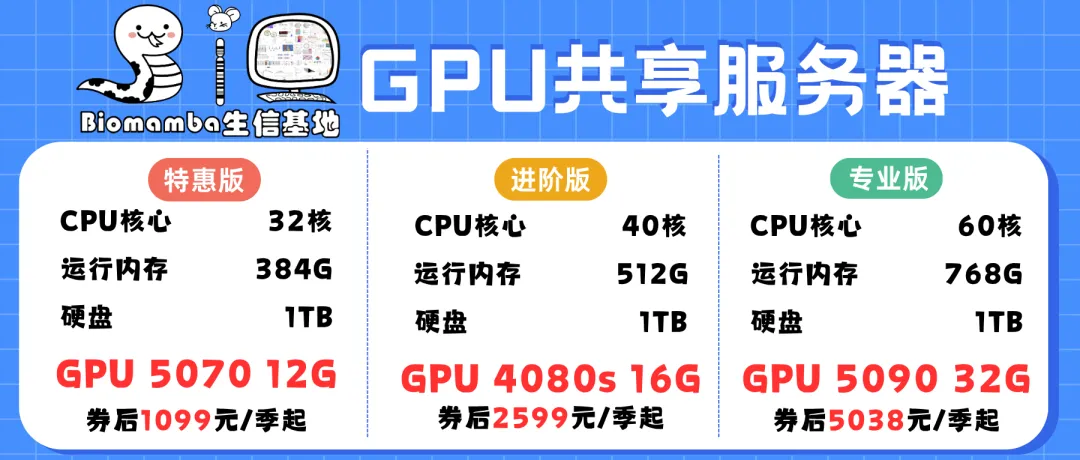

如何联系我们


已有生信基地联系方式的同学无需重复添加


 夜雨聆风
夜雨聆风




