崖州湾实验室田益夫观点文章:构建“编辑器-解析器”系统,实现100%纯度的碱基转换
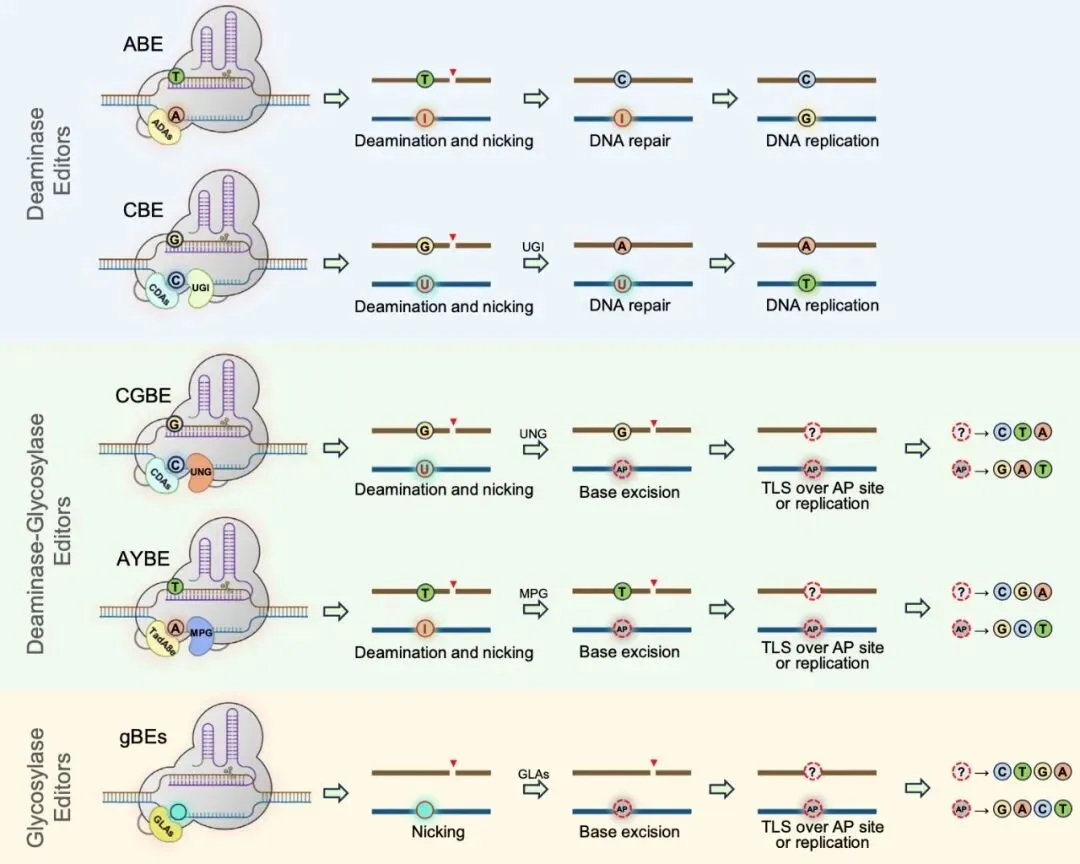
-
碱基切除修复(BER):通过 Pol β 恢复原始序列,抵消编辑效果; -
跨损伤合成(TLS):在缺乏模板的情况下插入核苷酸,可能产生预期的替换; -
双链断裂(DSB):若修复不完全,可能导致非预期的缺失或插入(Indels)。
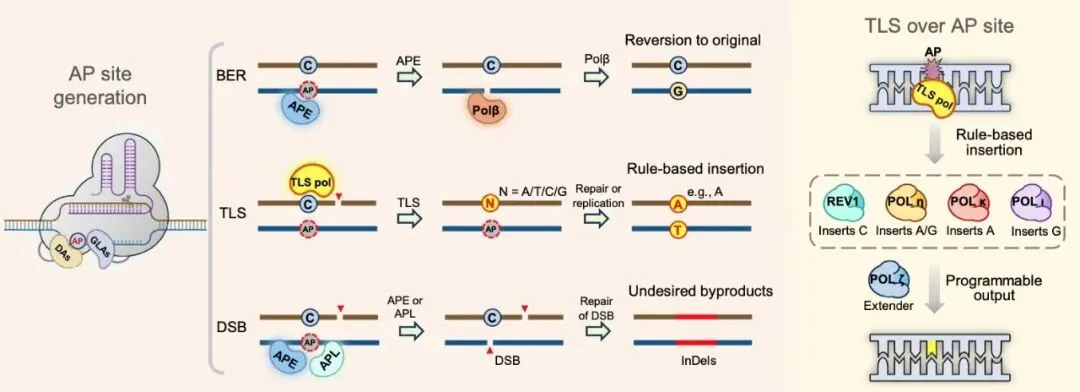
-
Rev1:具有脱氧胞苷单磷酸(dCMP)转移酶活性,倾向于在 AP 位点对面插入 C ; -
Pol η:倾向于插入 A 或 G ; -
Pol κ / Pol ι:分别表现出对 A 或 G 的插入偏好。
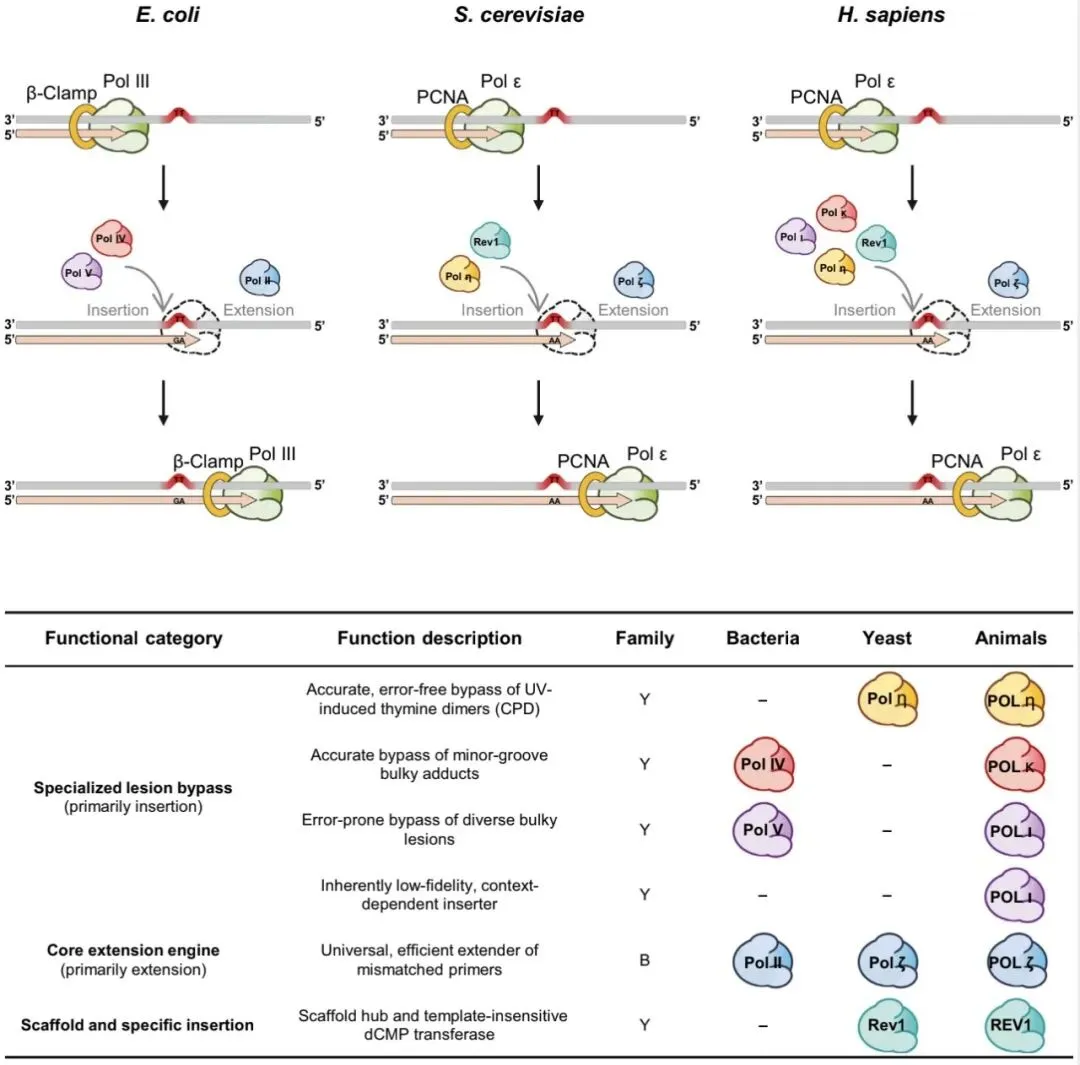
-
微生物验证:将大肠杆菌的 Pol V(偏好插入 T)移植到偏好插入 C 的谷氨酸棒状杆菌中,成功将编辑产物从 C-to-G 重新编程为 C-to-A; -
哺乳动物验证:Pol η 的共表达可将 A-to-Y (Y=T/C) 编辑引导向 A-to-T 产物; -
蛋白质工程:经过结构优化的人源聚合酶变体 Pol η-Q38S,在处理 AP 位点时表现出更高的插入特异性,显著提升了 B-to-A (B=C/G/T) 编辑的产物纯度。
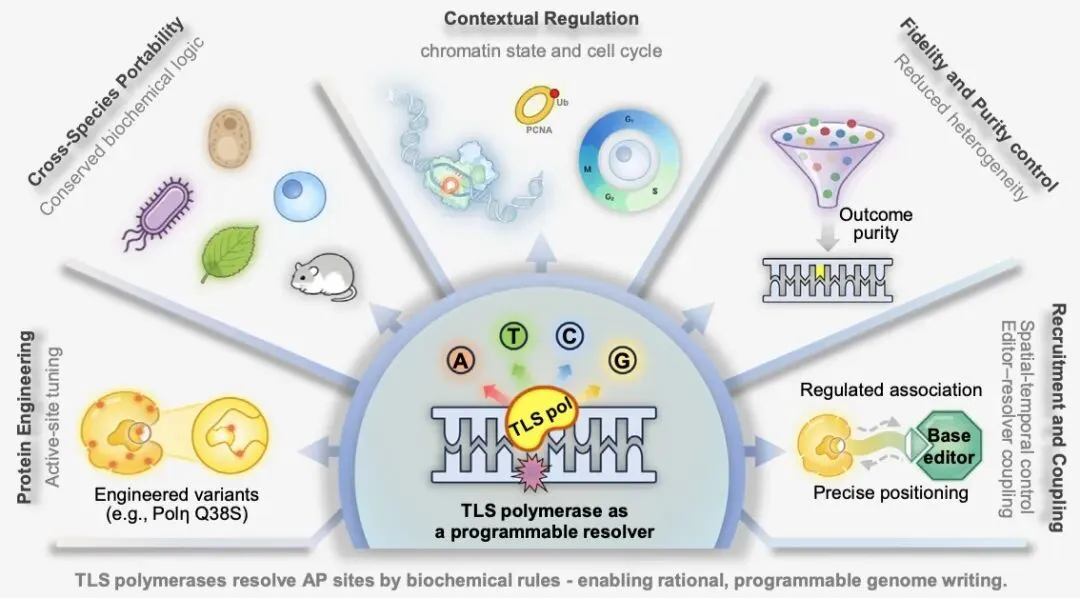
往期推荐
国人团队Nature封面重磅突破!全新可编程编辑器 OpenCRISPR-1 震撼问世,AI 大模型重塑基因编辑,突破自然进化限制
进交流群 | 商务 | 投稿
请添加助手微信
看到了这里,不妨‘一键三连’支持一下,为小编的激情更新助力!
 夜雨聆风
夜雨聆风




