PyMol插件自动可视化氢键、π–π 堆积、阳离子–π、盐桥

插件介绍
今天给大家再分享一个pymol插件!这个插件也是一个用Python编写的PyMOL脚本,专门用于分析两个蛋白链(或多个链)之间的相互作用界面,并自动识别四类关键非共价相互作用:
-
氢键(Hydrogen Bond)
-
π–π 堆积(Pi-Pi Stacking)
-
阳离子–π 作用(Cation–Pi)
-
盐桥(Salt Bridge)
第一步:准备PyMOL、PDB文件、插件文件
(1)安装PyMOL,如果你不知道怎么安装,跳转文章教程:
(2)插入脚本文件,如果你不知道怎么插入脚本,跳转文章教程:
蛋白与配体(小分子药物)相互作用——PyMol插件自动可视化
第二步:PDB 文件必须加氢hydrogen added!因为氢键判断需要氢原子
# 在 PyMOL 中打开 pdb 后执行h_addsave your_file_with_H.pdb
h_add:自动为所有合适的位置添加氢原子(基于当前 pH 和残基类型)save xxx.pdb:把当前状态(包括新加的氢)保存到新文件,your_file_with_H
就是文件名称
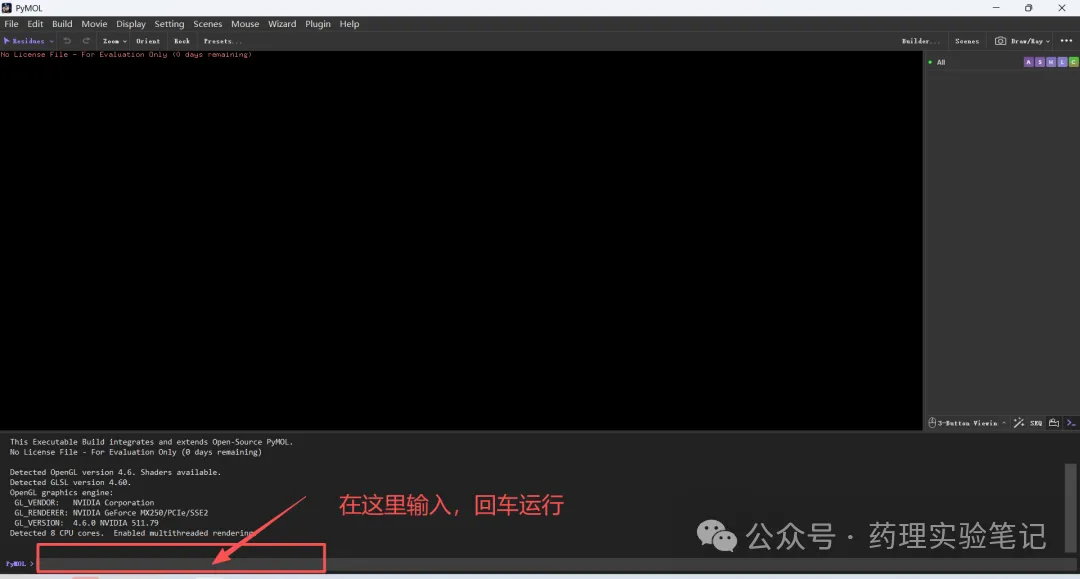
run show_protein_protein_interaction.py这一步是为了运行插件脚本,把脚本中的函数(如 HBond, Pi_Pi_interaction 等)加载到 PyMOL 的 Python 环境中。
第三步:开始分析
- 按下键盘快捷键:
Command (⌘) + 空格键 - 在弹出的搜索框中输入:
Terminal - 按回车,Terminal 就打开了
- 按下:
Win + R(Windows 徽标键 + R 键) - 输入:
powershell - 按回车
cd /your/path/to/files比如都放D盘,分子对接文件夹了,就输入:cd D:\分子对接
(3)运行命令(以分析链 A 和链 B,界面 5Å 为例),PDB 文件名如 myprotein_with_H.pdb:
pymol -qc show_protein_protein_interaction.py -- myprotein_with_H.pdb A B 5运行后会发生什么?
- PyMOL 在后台静默运行
- 识别链 A 和链 B
- 找出距离 ≤5Å 的界面残基(
inter_1,inter_2) - 计算四类相互作用
- 保存结果为
myprotein_with_H_interaction.pse
(4)查看结果,回到终端运行:
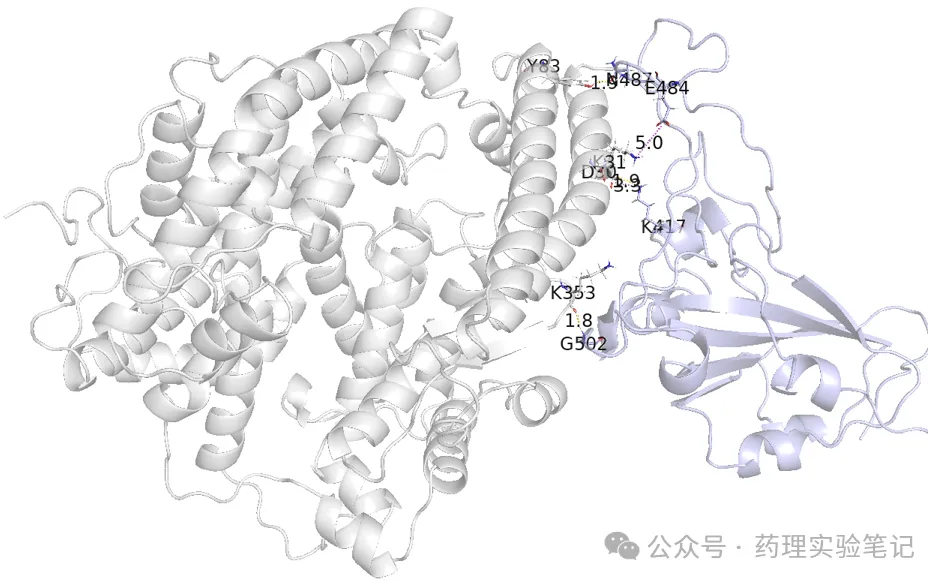
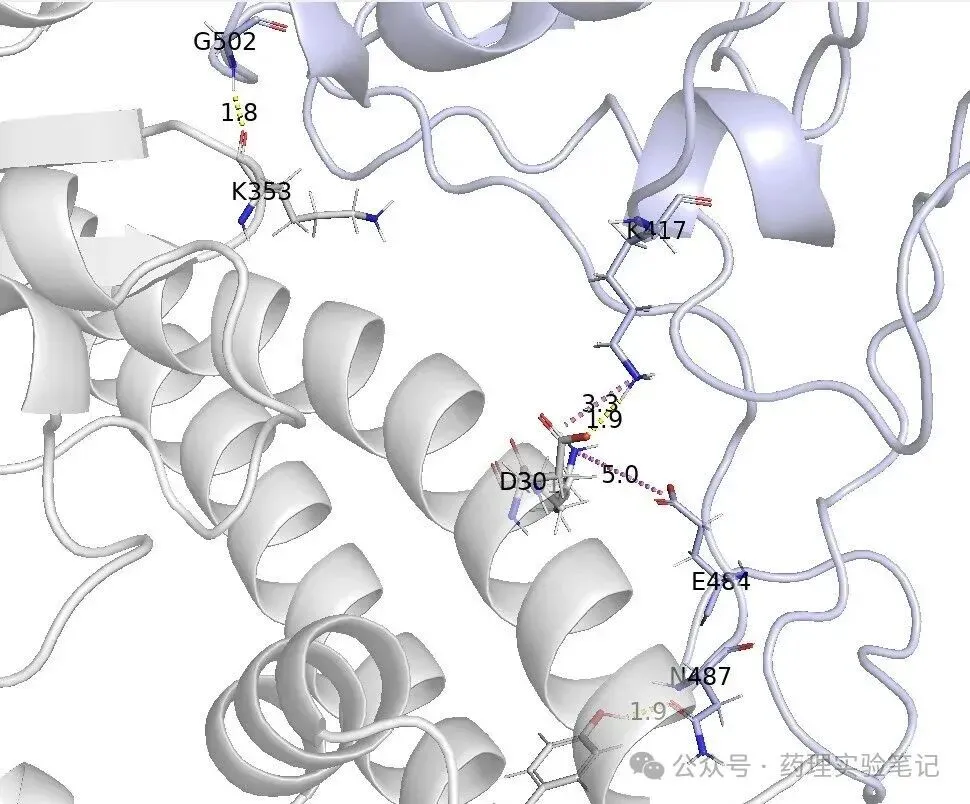
pymol myprotein_with_H_interaction.psePyMOL 图形界面打开,会看到:
- 蛋白结构
- 界面残基高亮
- 各种相互作用用彩色虚线标出
第四步:分析 “多链 VS 多链”
(4)运行命令:
pymol -qc show_protein_protein_interaction.py -- cpx_60_h.pdb H+L A+B 5cpx_60_h是pdb文件名;H、L、A、B 是你的 PDB 文件里自带的 “链标识”
在pymol中,Show as Cartoon,然后在命令行输入:
show chainlabels # 显示每个链的ID标签此时蛋白结构上会直接显示 A、B、H、L 等链 ID,对应到每个链的位置。
(5)查看结果:在终端输入
pymol 6m0j_h_interaction.pse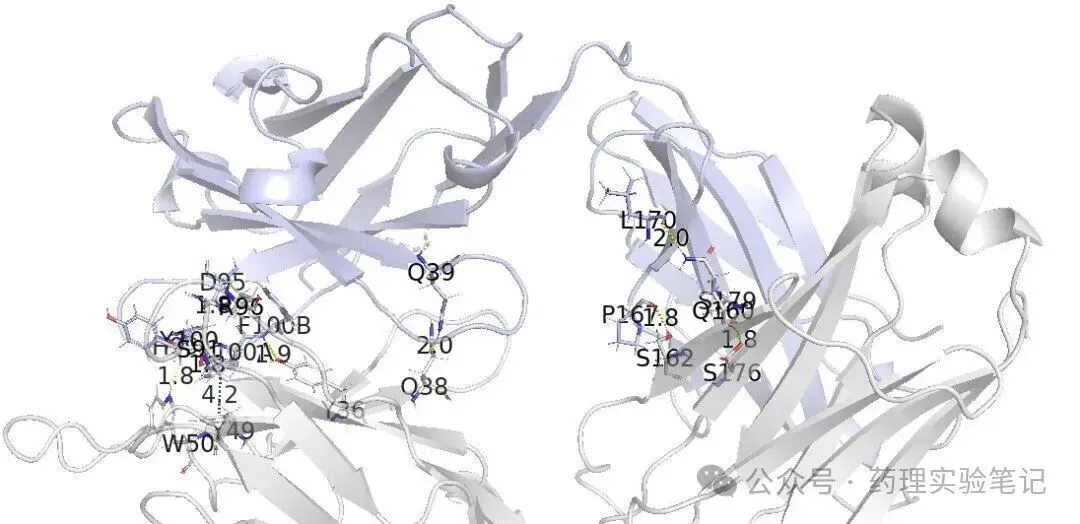
最终输出四条链之间的氢键、π–π 堆积、阳离子–π、盐桥,都是在“界面 ≤5Å 的残基对”范围内
该插件通过网盘分享:show_protein_protein_interaction.py。
点赞👍加爱心❤,评论区留言领取~
科研辅导
科研道路上,每一步都至关重要。从选题立项到实验设计,从论文撰写到成果发表,每一个环节都需要扎实的基础与系统的指导。




课题设计
论文写作
实验指导
考研申博

 夜雨聆风
夜雨聆风




