五款生信神器的超详细教程,手把手教你从零跑通分析,一篇顶十篇!

资源推荐
对于每一位深耕生物信息学的科研人来说,数据是金矿,数据库就是挖掘金矿的地图。
然而,面对界面更新频繁、甚至命令行操作复杂的数据库,你是否也曾感到无从下手?
在这个高通量测序技术日新月异的时代,掌握经典数据库的高效检索与挖掘技巧,早已不是“选修课”,而是决定科研效率与深度的“必修功”。
今天小料君带来了【生信经典数据库教程】,一起来看看吧!

资源详情

资源目录

PART/1
生信经典数据库教程
此套课程内容围绕生信分析中最实用的五个经典工具与数据库展开:从shinyGEO便捷获取GEO公共数据,借助GSEA进行基因集富集分析挖掘核心通路,利用STRING构建蛋白互作网络,再通过Cytoscape实现网络的精美可视化与关键节点筛选,最后用GEPIA2验证目标基因在肿瘤样本中的表达差异与生存意义。

资源亮点

生信经典数据库教程从数据获取到功能富集,再到网络构建与可视化验证,五款经典数据库一次讲透!无论你是刚入门的生信小白,还是想系统梳理分析流程的科研人,这份“组合拳”教程都能帮你少踩坑、提效率,快速跑通从原始数据到论文图表的完整链路!
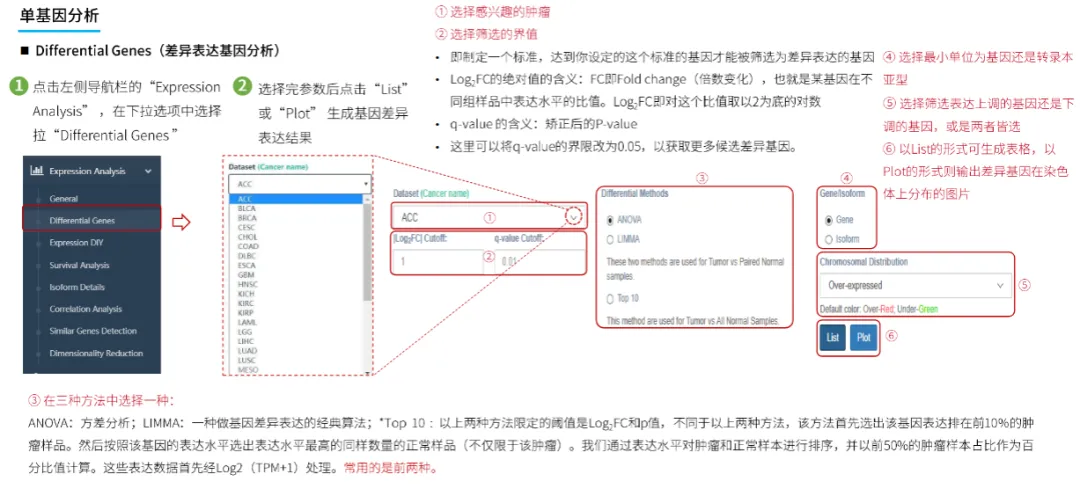
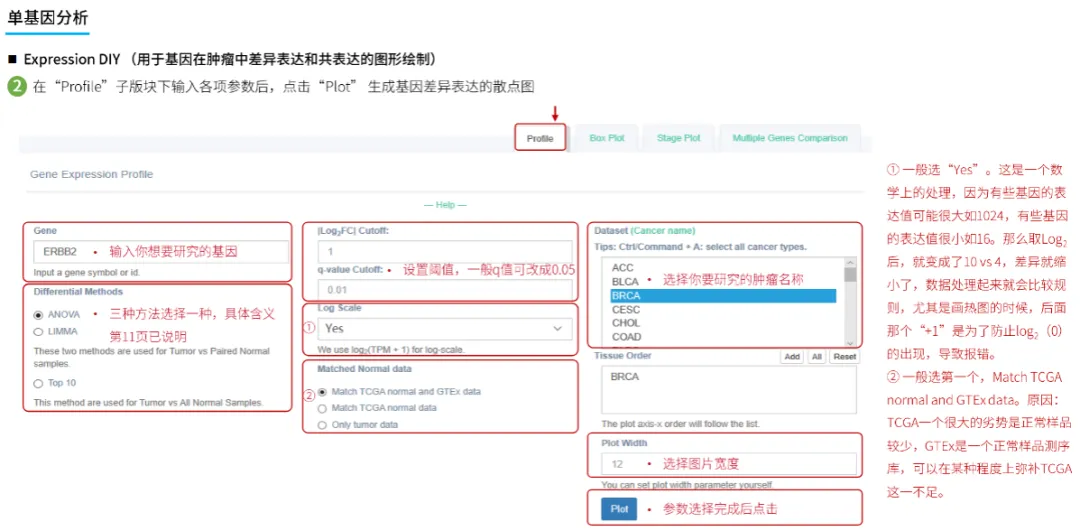
GEPIA2数据库使用教程
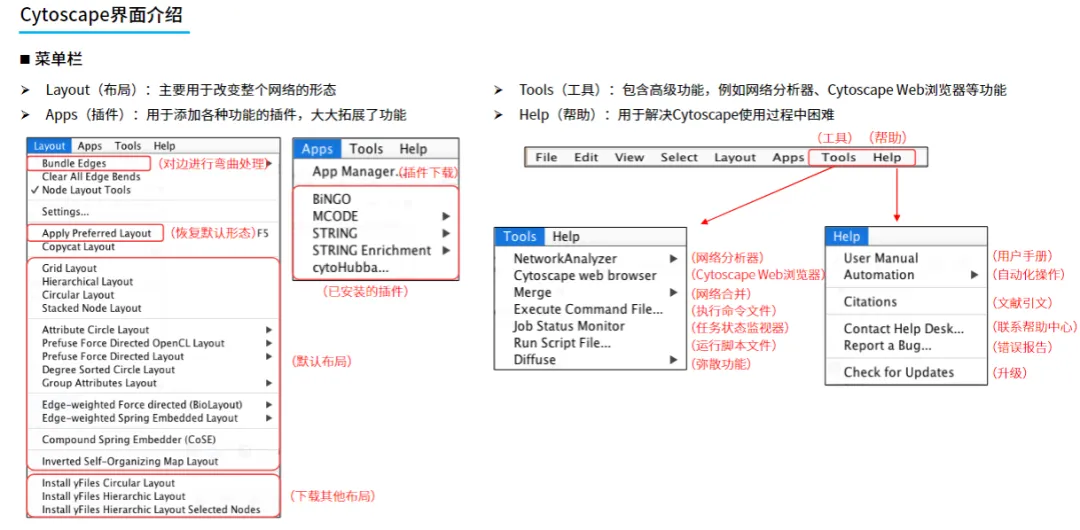
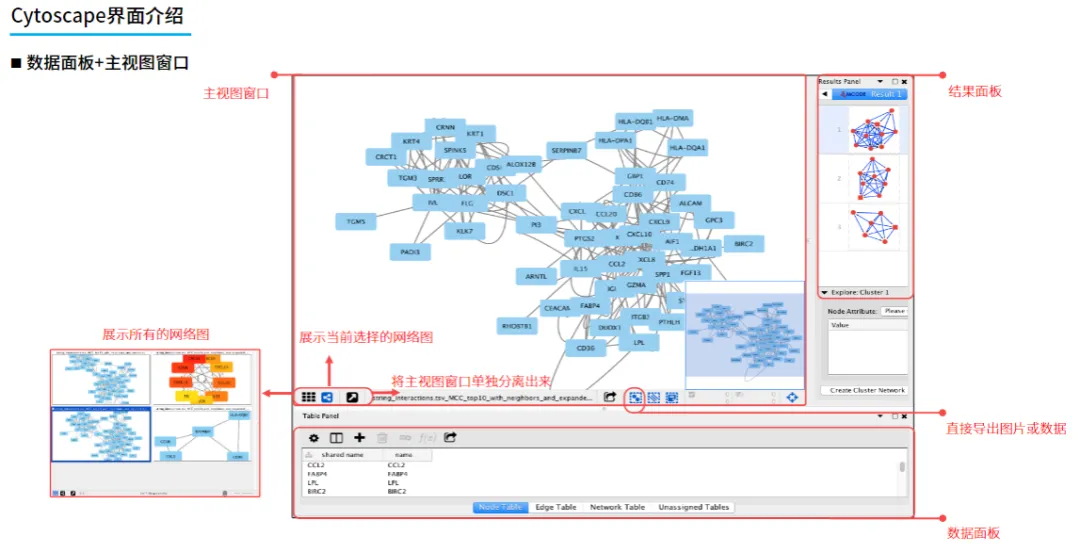
Cytoscape软件使用教程
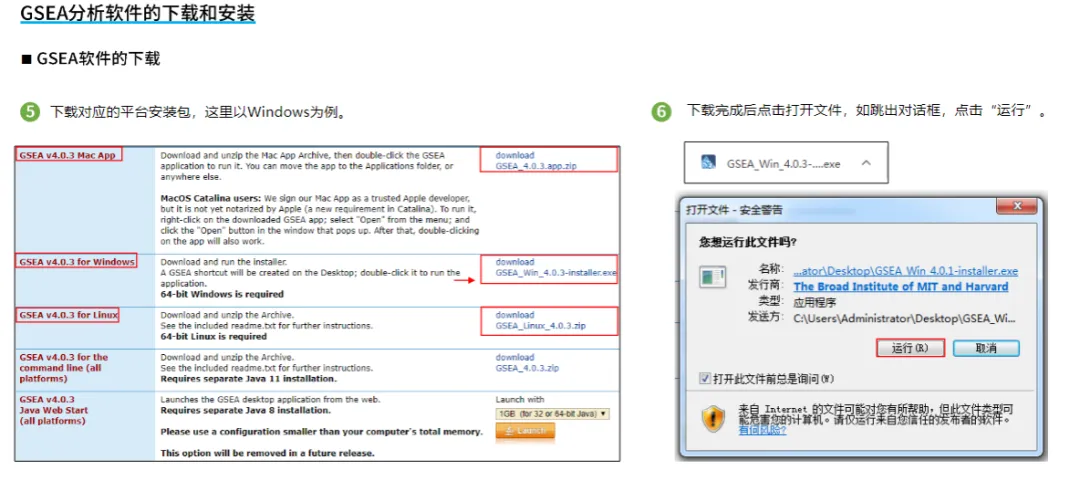

GSEA软件使用教程
篇幅有限,仅部分展示
以上是【生信经典数据库教程】部分内容,获取全部可扫码添加小料君
资料 ·推荐
免费领取方式
扫描下方二维码添加小料君微信回复关键词:“260322”

更多精彩内容
欢迎关注微信公众号【科研小料君】
免责声明:本号所载内容、图片来源互联网,微信公众号等公开渠道,仅交流之目的,不存在任何商业行为。对转载、分享、陈述、观点保持中立,版权归原作者和机构所有,如有侵权,请联系我们,我们将即刻删除妥善处理。
 夜雨聆风
夜雨聆风




