在线工具 | SNP簇、传播簇、最小生成树

GraphSNP –交互式 SNP距离 查看器。使用图形方法,调查疫情 (Outbreaks)和传播网络。
在线用:
https://graphsnp.beatsonlab.com/
本地浏览器或自行布置到Web云平台:
How to use it offline
Clone this repository or download the build directory.
Serve it using your favorite local static server. For example using serve from Node.js Install Node.js
Install ‘serve’ via npm. (e.g. npm install serve -g)
Run serve to the build directory. (e.g. serve -s build)
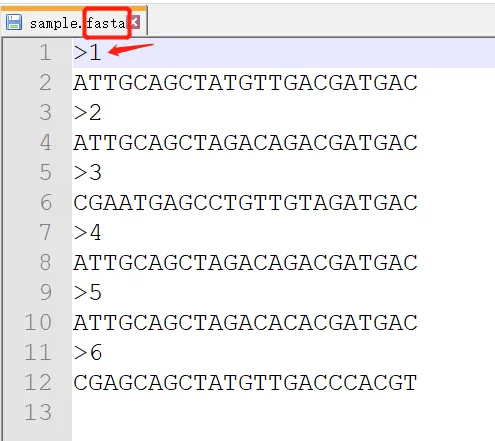
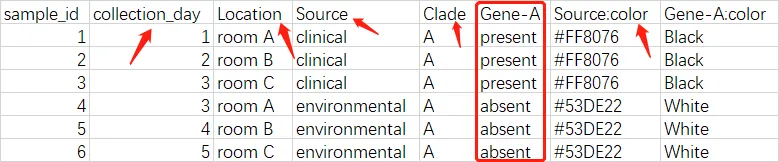
上传:
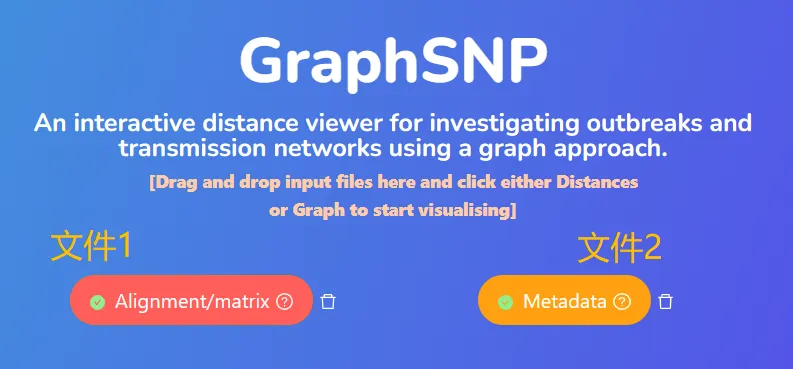
使用真实数据 (已通过其它程序分簇,此处与GraphSNP做个对照,结果见上篇)
点击”Graph”
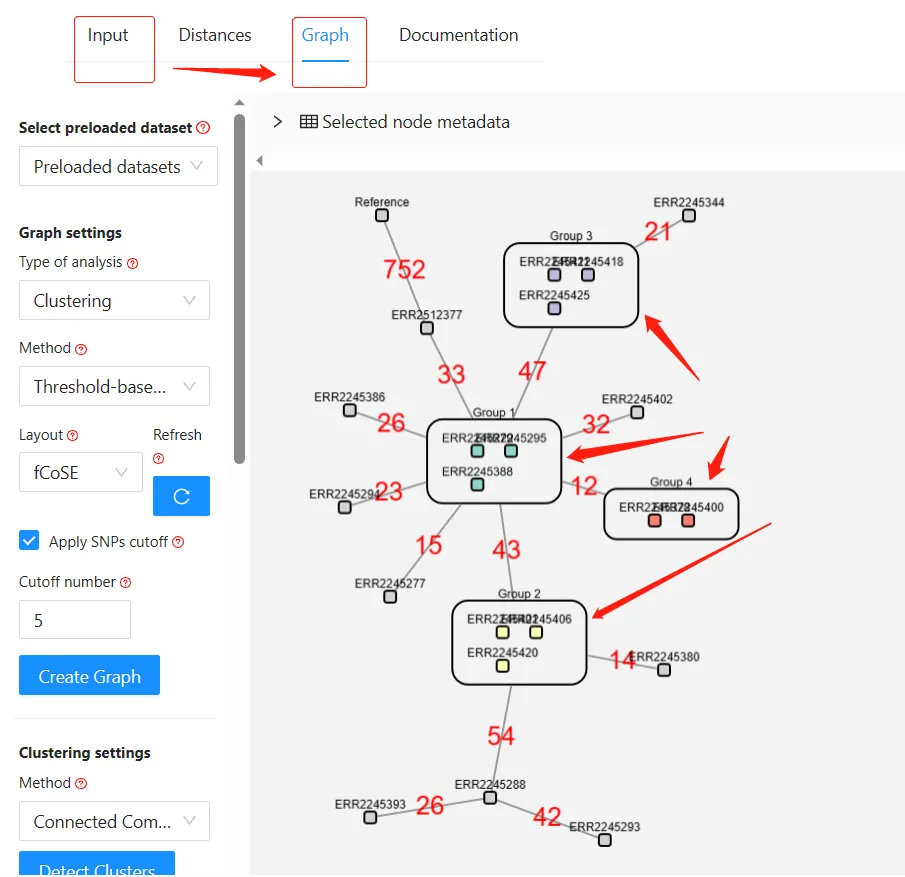
上图的侧边栏可以调:颜色、字体大小、展示风格,等等
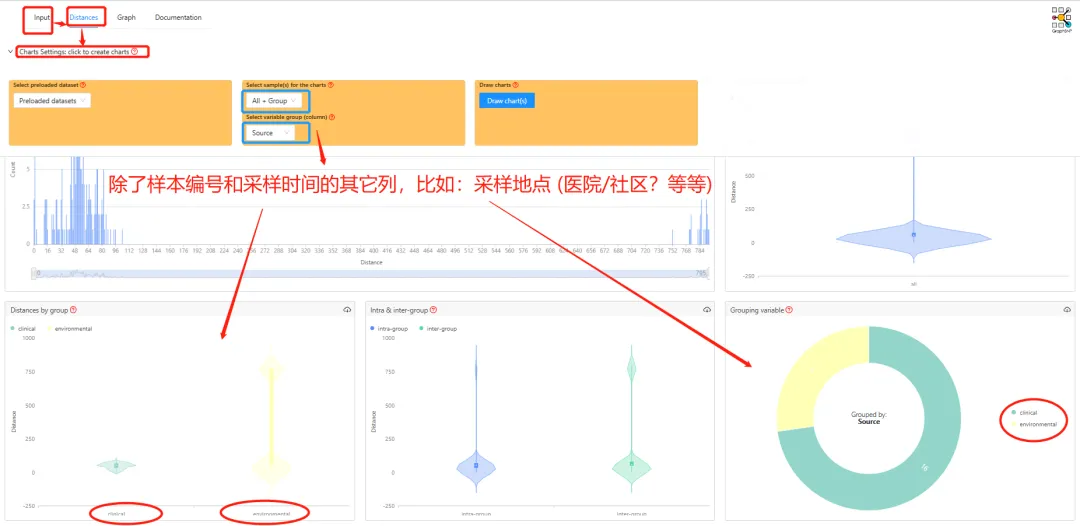
点击”Distance”
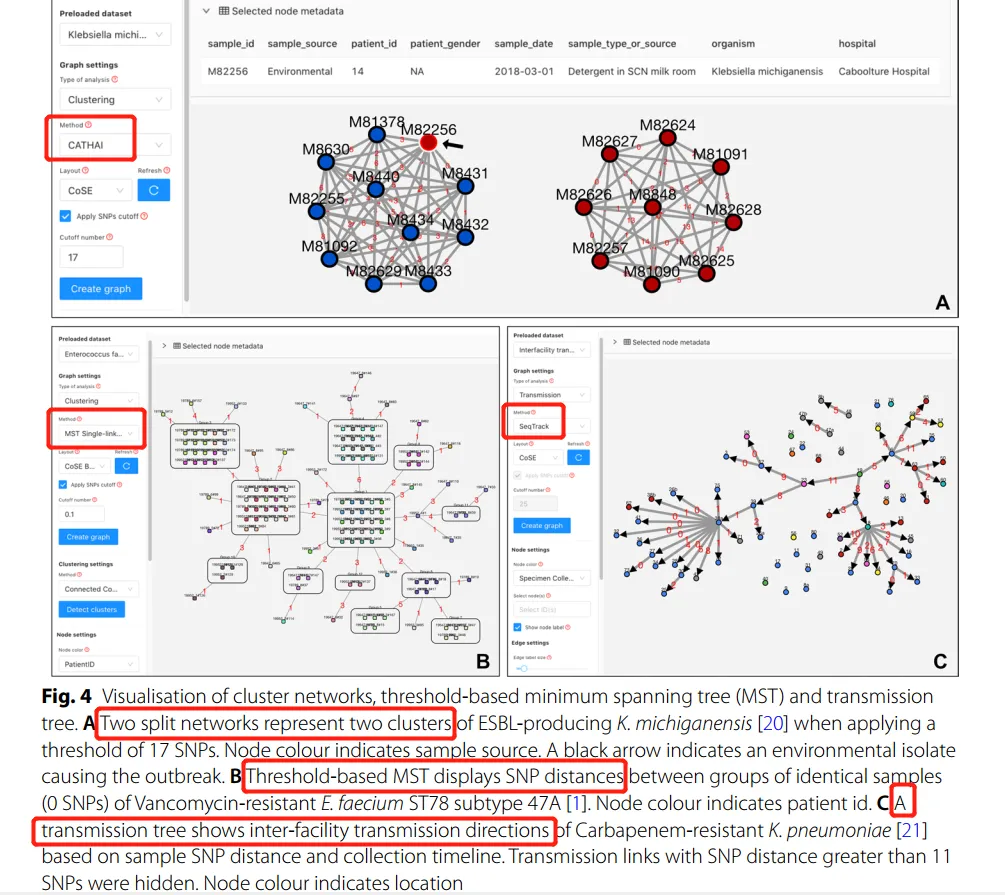
做个传播树
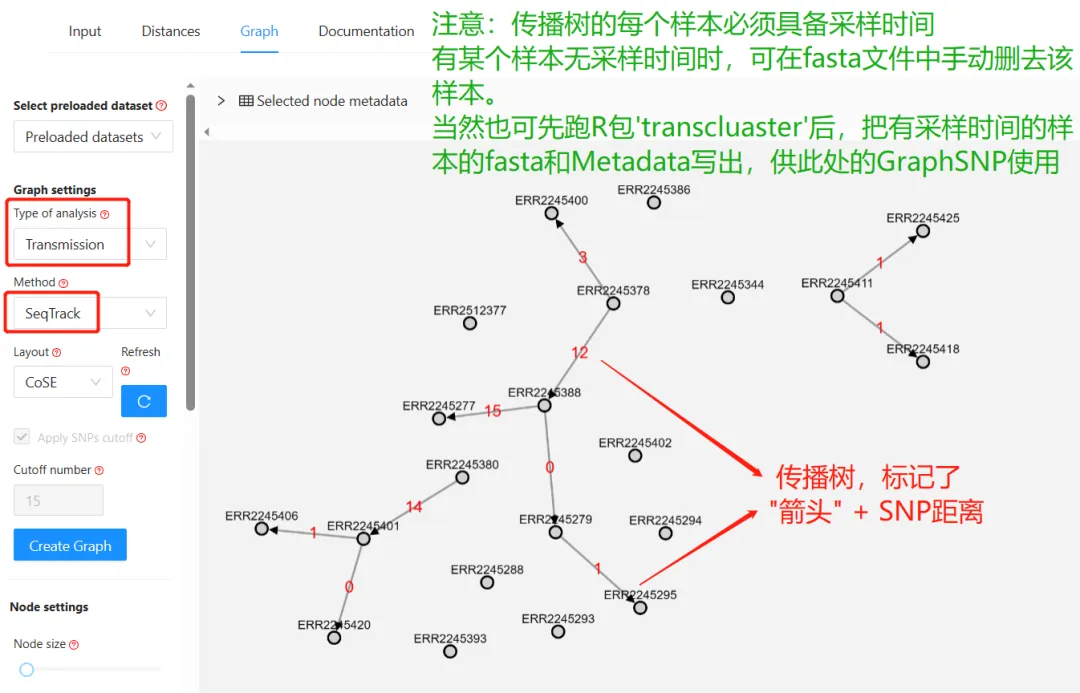
GraphSNP的传播树算法-SeqTrack(可能与上一篇R包transcluster采用的算法不同,且可能生成了有箭头方向的进化树):
SeqTrack算法试图根据遗传距离(不考虑SNP阈值)及分离株的收集日期推断祖先(SeqTrack algorithm attempts to infer ancestry based on genetic distance, regardless of SNP thresholds, and isolate collection dates)。因此,所有可能的传播链都收敛在最早收集的样本上,这可能会模糊不同的传输簇,并错误地推断传播动态。为了屏蔽不太可能的传播,已经应用了一个预定义的范围 (默认:0-15 SNPs)过滤。屏蔽阈值可以使用“显示部分边缘(Show Partial Edge)”函数/功能进行调整。
查看引文结果
Permana et al. BMC Bioinformatics (2023) 24:209

 夜雨聆风
夜雨聆风




